Ensayo de genotipificación para enfermedad de Chagas
|
Por el equipo editorial de LabMedica en español Actualizado el 05 May 2017 |
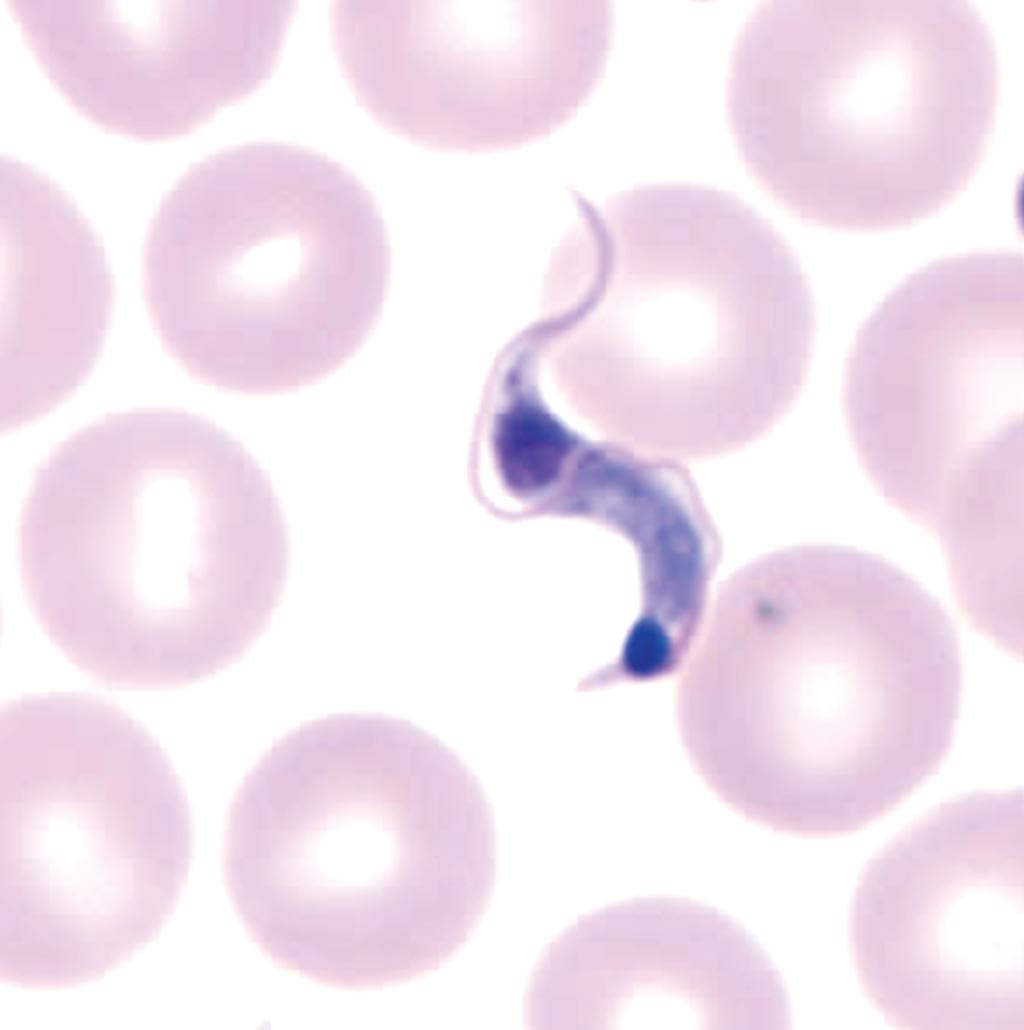
Imagen: Un tripomastigote de Trypanosoma cruzi en un frotis de sangre coloreado con Giemsa de un paciente con enfermedad de Chagas (Fotografía cortesía del CDC).
La enfermedad de Chagas sigue siendo un importante problema de salud pública que infecta entre seis y siete millones de personas en todo el mundo. Los factores que influyen sobre la heterogeneidad clínica de la enfermedad de Chagas no han sido aclarados, aunque se ha sugerido que diferentes resultados clínicos pueden estar asociados con la diversidad genética de los aislados de Trypanosoma cruzi.
También se han reportado diferencias en la respuesta terapéutica de los genotipos y definidos de T. cruzi. Ya se han desarrollado estrategias de tipificación para el diagnóstico genotípico específico de la enfermedad de Chagas, con el fin de identificar las unidades de tipificación discreta de T. cruzi (DTU), incluyendo métodos bioquímicos y moleculares; sin embargo, las técnicas tienen limitaciones.
Científicos de la Universidad Federal de Ouro Preto utilizaron cepas estándar de T. cruzi, representativas de los tres principales genotipos involucrados en el ciclo doméstico de la enfermedad de Chagas en Brasil, para establecer la metodología TcI/TcVI/TcII Chagas-Flujo ATE-IgG2a, para el serodiagnóstico de la infección por T. cruzi. El equipo mantuvo las cepas en ratones y la infección fue confirmada en todos los ratones infectados con T. cruzi, por positividad de un examen de sangre fresca, realizado al día 7, 10 o 15, después de la infección. Las muestras de suero que fueron utilizadas para la serología, con la metodología, TcI/TcVI/TcII Chagas-Flujo ATE-IgG2a, fueron preparadas a partir de muestras de sangre total recogidas por punción del plexo ocular.
Se obtuvieron las formas amastigote/tripomastigote/epimastigote, de los genotipos TcI, TcVI y TcII, de T. cruzi, y se realizó el serodiagnóstico TcI/TcVI/TcII Chagas-Flujo ATE-IgG2a. Los datos de citometría de flujo se obtuvieron con un citómetro de flujo FACSCanto (Becton Dickinson, Franklin Lakes, NJ, EUA). Después de la selección de los antígenos objetivo, se utilizaron histogramas unidimensionales para cuantificar la reactividad del antígeno específico del genotipo anti-T. Cruzi IgG2a, basado en el límite de positividad establecido utilizando como referencia el control interno. Los resultados fueron expresados como porcentaje de parásitos fluorescentes positivos (PPFP), para cada dilución de la muestra ensayada.
Los datos adquiridos demostraron que “α-TcII-TRYPO/1:500, punto de corte/PPFP = 20%”, presentó un excelente desempeño para el diagnóstico universal de la infección por T. cruzi. El conjunto combinado de los atributos “α-TcI-TRYPO/1:4.000, punto de corte/PPFP = 50%”, “α-TcII-AMA/1:1000, punto de corte/PPFP = 40%” y “α-TcVI-EPI/1:1000, punto de corte/PPFP = 45%”, mostraban un buen comportamiento para segregar las infecciones con las cepas, TcI/Colombiana, TcVI/CL o TcII/Y. En general, los huéspedes infectados con las cepas, TcI/Colombiana y TcII/Y mostraron patrones opuestos de reactividad con α-TcI TRYPO y α-TcII AMA.
Los autores concluyeron que el método presentó un buen desempeño para el diagnóstico genotípico específico, con una exactitud global del 69% cuando el escenario población/prototipo incluía infecciones TcI, TcVI y TcII, y de 94% cuando sólo comprenden infecciones TcI y TcII. El método proporciona una herramienta factible para clasificar muestras de suero de huéspedes infectados con genotipos definidos de T. cruzi, apoyando el potencial de este método para el diagnóstico universal y la genotipificación específica de la infección por T. cruzi. El estudio fue publicado el 23 de marzo de 2017, en la revista Public Library of Science Neglected Tropical Diseases.
Últimas Microbiología noticias
- Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
- Análisis de sangre predice sepsis e insuficiencia orgánica en niños
- Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
- Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
- Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
- Nuevo análisis para tuberculosis podría ampliar acceso a pruebas en países de ingresos bajos y medios
- Prueba rápida diagnostica enfermedades tropicales en horas para tratamiento con antibióticos más rápido
- Pruebas moleculares rápidas permiten tratamiento antibiótico más rápido y específico para neumonía
- Plataforma rápida de PSA proporciona resultados terapéuticos específicos días antes que el estándar de atención actual
- Nuevo método de análisis detecta patógenos en sangre de forma más rápida y precisa al fundir ADN
- Prueba rápida de sepsis ofrece resultados dos días más rápidos
- Diagnóstico rápido portátil por PCR podría detectar gonorrea y susceptibilidad a antibióticos
- Prueba CRISPR diagnostica mpox más rápido que método de PCR de laboratorio
- Prueba de PCR multiplexada para detección de patógenos y resistencia a antibióticos ayuda a brindar un tratamiento rápido de ITU
- Nuevo algoritmo detecta e identifica nuevos organismos bacterianos
- Analizador de mesa promete detección de ITU en 1 hora e indicación de sensibilidad a antibióticos
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal.jpeg)
Ensayo de aprendizaje automático basado en sangre detecta de forma no invasiva el cáncer de ovario
El cáncer de ovario es una de las causas más comunes de muerte por cáncer entre las mujeres y tiene una tasa de supervivencia a cinco años de alrededor del 50%.... Más
Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas (CPCP), una neoplasia maligna neuroendocrina que progresa rápidamente, presenta bajas tasas de supervivencia. A pesar de su heterogeneidad molecular y clínica, el... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásPatología
ver canal
Biopsia de piel virtual determina la presencia de células cancerosas
Cuando los dermatólogos detectan una marca inusual en la piel de un paciente, se enfrentan a una elección: controlarla durante algún tiempo o extraerla para realizar una biopsia.... Más
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más











.jpg)


