Identifican bacterias aeróbicas con espectrometría de masas MALDI-TOF
|
Por el equipo editorial de LabMedica en español Actualizado el 15 Mar 2016 |

Imagen A: El espectrómetro de masas MALDI-TOF y el BioTipificador de sobremesa Microflex LT (Fotografía cortesía de Bruker Daltonics).
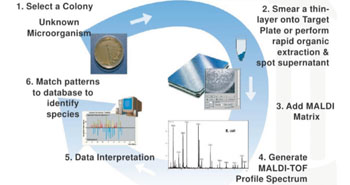
Imagen B: Esquema del Flujo de Trabajo del Bruker MALDI BioTipificador (Fotografía cortesía de la profesora, Melissa B. Miller).
La espectrometría de masas asistida de matriz láser de desorción ionización tiempo de vuelo (MALDI-TOF MS) es una herramienta de diagnóstico para la identificación de organismos que se encuentran rutinariamente en el laboratorio de microbiología.
La MS MALDI-TOF ha demostrado ser un método de diagnóstico rápido y rentable para el uso rutinario en el laboratorio de microbiología clínica y la tecnología MALDI-TOF MS utiliza láser de ionización para los elementos estructurales de la cepa aislada con el fin de generar espectros aislados, derivados, que se comparan con una base de datos de referencia.
Los científicos en el Hospital de Niños de Los Ángeles (California, EUA) y sus colegas en la Facultad de Medicina Keck (Los Ángeles, CA, EUA) utilizaron aislamientos recuperados e identificados, previamente, por cultivos de rutina de muestras clínicas las cuales fueron cultivadas en los medios apropiados, identificados directamente por MALDI-TOF MS y se compararon los resultados con los de varios métodos de identificación bioquímica. Un total de 996 de aislamientos organismos Gram-positivos y Gram-negativos, aeróbicos fueron incluidos en el estudio.
Todas las pruebas de MALDI-TOF MS fueron realizadas por duplicado con el mismo hisopo sembrando en dos puntos en la placa de destino, un punto representando un inóculo “pesado” y el segundo punto representando un inóculo “liviano”. La adquisición y el análisis de los espectros de masas fueron realizado usando el espectrómetro de masas Microflex LT (Bruker Daltonics, Fremont, CA, EUA). Para los estudios de los medios, 84 bacterias Gram-negativas fueron cultivadas en agar sangre, agar chocolate y agar MacConkey; 74 bacterias Gram-positivas fueron cultivadas en agar sangre, agar chocolate, y agar ácido nalidíxico colistina (CNA). Para los estudios de temperatura y estabilidad, cuatro bacterias Gram-negativas y cuatro bacterias Gram-positivas, fueron cultivadas en agar sangre. Los resultados de MALDI-TOF MS fueron comparados con los obtenidos mediante métodos rutinarios realizados en el laboratorio de microbiología. Todas las identificaciones discordantes fueron confirmadas mediante análisis bioquímicos adicionales o por secuenciación de 16S rARN.
En la interpretación de datos de MALDI-TOF MS, una puntuación igual o superior a 2,0 es inequívoca para una identificación confiable a nivel de especie, una puntuación de 1,7 a 1,99 se considera fiable a nivel de género y una puntuación de menos de 1,7 se considera poco fiable para la identificación de bacterias. Utilizando el método de frotis directo, 99,5% y 98,0% de las bacterias aeróbicas Gram-negativas y Gram-positivas, respectivamente, fueron identificadas a nivel de género. En una puntuación igual o superior a 1,9, 97,6% los organismos Gram-negativos y 94,6% los organismos Gram-positivos fueron correctamente identificados a nivel de especie por el método de frotis directo. Sólo el 1.1% de los aislamientos requirió una extracción directa a la placa. El método de frotis directo demostró ser robusto, a diversas temperaturas de crecimiento, medios de cultivo, edad del cultivo y los diferentes operadores no tuvieron un impacto notable en la tasa de identificación bacteriana.
Los autores concluyeron que el método de frotis directo era exacto y eficaz para agilizar el flujo de trabajo de la identificación de bacterias Gram-positivas y Gram-negativas en su laboratorio clínico. Para simplificar, recomiendan usar el método de frotis directo para la mayoría de los especímenes que se encuentran comúnmente en el laboratorio clínico y una puntuación de corte espectral optimizada igual o mayor a 1.9 para las tasas de identificación a nivel de especies mejoradas. El estudio fue publicado el 14 de diciembre de 2015, en la revista Journal of Clinical Laboratory Analysis.
Enlaces relacionados:
Children's Hospital Los Angeles
Keck School of Medicine
Bruker Daltonics
La MS MALDI-TOF ha demostrado ser un método de diagnóstico rápido y rentable para el uso rutinario en el laboratorio de microbiología clínica y la tecnología MALDI-TOF MS utiliza láser de ionización para los elementos estructurales de la cepa aislada con el fin de generar espectros aislados, derivados, que se comparan con una base de datos de referencia.
Los científicos en el Hospital de Niños de Los Ángeles (California, EUA) y sus colegas en la Facultad de Medicina Keck (Los Ángeles, CA, EUA) utilizaron aislamientos recuperados e identificados, previamente, por cultivos de rutina de muestras clínicas las cuales fueron cultivadas en los medios apropiados, identificados directamente por MALDI-TOF MS y se compararon los resultados con los de varios métodos de identificación bioquímica. Un total de 996 de aislamientos organismos Gram-positivos y Gram-negativos, aeróbicos fueron incluidos en el estudio.
Todas las pruebas de MALDI-TOF MS fueron realizadas por duplicado con el mismo hisopo sembrando en dos puntos en la placa de destino, un punto representando un inóculo “pesado” y el segundo punto representando un inóculo “liviano”. La adquisición y el análisis de los espectros de masas fueron realizado usando el espectrómetro de masas Microflex LT (Bruker Daltonics, Fremont, CA, EUA). Para los estudios de los medios, 84 bacterias Gram-negativas fueron cultivadas en agar sangre, agar chocolate y agar MacConkey; 74 bacterias Gram-positivas fueron cultivadas en agar sangre, agar chocolate, y agar ácido nalidíxico colistina (CNA). Para los estudios de temperatura y estabilidad, cuatro bacterias Gram-negativas y cuatro bacterias Gram-positivas, fueron cultivadas en agar sangre. Los resultados de MALDI-TOF MS fueron comparados con los obtenidos mediante métodos rutinarios realizados en el laboratorio de microbiología. Todas las identificaciones discordantes fueron confirmadas mediante análisis bioquímicos adicionales o por secuenciación de 16S rARN.
En la interpretación de datos de MALDI-TOF MS, una puntuación igual o superior a 2,0 es inequívoca para una identificación confiable a nivel de especie, una puntuación de 1,7 a 1,99 se considera fiable a nivel de género y una puntuación de menos de 1,7 se considera poco fiable para la identificación de bacterias. Utilizando el método de frotis directo, 99,5% y 98,0% de las bacterias aeróbicas Gram-negativas y Gram-positivas, respectivamente, fueron identificadas a nivel de género. En una puntuación igual o superior a 1,9, 97,6% los organismos Gram-negativos y 94,6% los organismos Gram-positivos fueron correctamente identificados a nivel de especie por el método de frotis directo. Sólo el 1.1% de los aislamientos requirió una extracción directa a la placa. El método de frotis directo demostró ser robusto, a diversas temperaturas de crecimiento, medios de cultivo, edad del cultivo y los diferentes operadores no tuvieron un impacto notable en la tasa de identificación bacteriana.
Los autores concluyeron que el método de frotis directo era exacto y eficaz para agilizar el flujo de trabajo de la identificación de bacterias Gram-positivas y Gram-negativas en su laboratorio clínico. Para simplificar, recomiendan usar el método de frotis directo para la mayoría de los especímenes que se encuentran comúnmente en el laboratorio clínico y una puntuación de corte espectral optimizada igual o mayor a 1.9 para las tasas de identificación a nivel de especies mejoradas. El estudio fue publicado el 14 de diciembre de 2015, en la revista Journal of Clinical Laboratory Analysis.
Enlaces relacionados:
Children's Hospital Los Angeles
Keck School of Medicine
Bruker Daltonics
Últimas Microbiología noticias
- Firma metabólica unica podría permitir el diagnóstico de sepsis dentro de una hora de la extracción de sangre.
- Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
- Análisis de sangre predice sepsis e insuficiencia orgánica en niños
- Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
- Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
- Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
- Nuevo análisis para tuberculosis podría ampliar acceso a pruebas en países de ingresos bajos y medios
- Prueba rápida diagnostica enfermedades tropicales en horas para tratamiento con antibióticos más rápido
- Pruebas moleculares rápidas permiten tratamiento antibiótico más rápido y específico para neumonía
- Plataforma rápida de PSA proporciona resultados terapéuticos específicos días antes que el estándar de atención actual
- Nuevo método de análisis detecta patógenos en sangre de forma más rápida y precisa al fundir ADN
- Prueba rápida de sepsis ofrece resultados dos días más rápidos
- Diagnóstico rápido portátil por PCR podría detectar gonorrea y susceptibilidad a antibióticos
- Prueba CRISPR diagnostica mpox más rápido que método de PCR de laboratorio
- Prueba de PCR multiplexada para detección de patógenos y resistencia a antibióticos ayuda a brindar un tratamiento rápido de ITU
- Nuevo algoritmo detecta e identifica nuevos organismos bacterianos
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal.jpg)
Prueba de sangre detecta y monitorea cáncer pulmonar de células pequeñas agresivo
El cáncer de pulmón de células pequeñas (CPCP) es un tipo de cáncer muy agresivo conocido por su capacidad de metastatizar. El comportamiento de los tumores se rige en... Más.jpeg)
Ensayo de aprendizaje automático basado en sangre detecta de forma no invasiva el cáncer de ovario
El cáncer de ovario es una de las causas más comunes de muerte por cáncer entre las mujeres y tiene una tasa de supervivencia a cinco años de alrededor del 50%.... Más
Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas (CPCP), una neoplasia maligna neuroendocrina que progresa rápidamente, presenta bajas tasas de supervivencia. A pesar de su heterogeneidad molecular y clínica, el... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Pruebas genéticas combinadas con la detección de fármacos personalizadas en muestras de tumores podrían revolucionar el tratamiento del cáncer
El tratamiento del cáncer generalmente se adhiere a un estándar de atención: regímenes establecidos y validados estadísticamente que son efectivos para la mayoría... Más
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... MásPatología
ver canal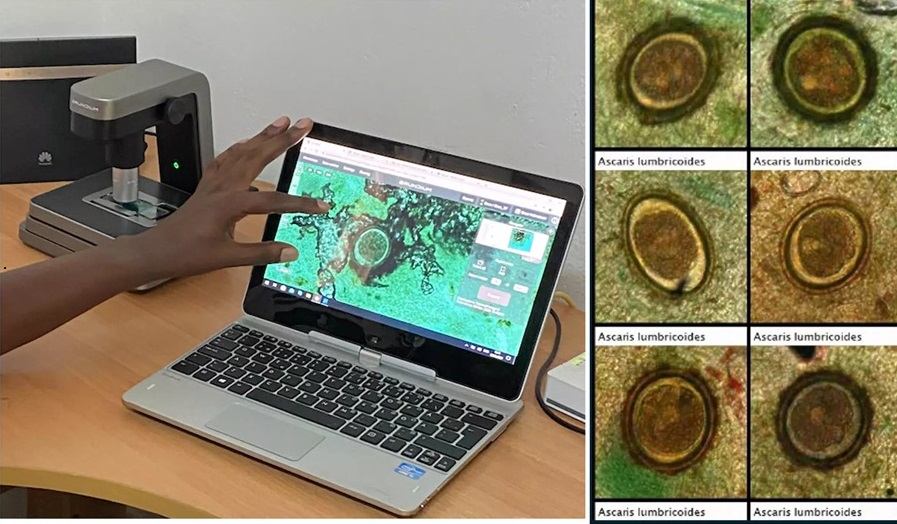
IA basada en imágenes se muestra prometedora para detección de parásitos en muestras de heces digitalizadas
Las infecciones por helmintos transmitidos por el suelo (STH), comúnmente conocidas como gusanos parásitos intestinales, se encuentran entre las enfermedades tropicales desatendidas más... Más
Algoritmos de inteligencia artificial potenciados por aprendizaje profundo mejoran la precisión en el diagnóstico de cáncer de piel.
Algoritmos de inteligencia artificial (IA) se utilizan cada vez más en diversos entornos clínicos, como la dermatología. Estos algoritmos se desarrollan entrenando una computadora... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más