Prueba en heces predice rápidamente la resistencia a los antibióticos de H. pylori
|
Por el equipo editorial de LabMedica en español Actualizado el 09 Nov 2021 |
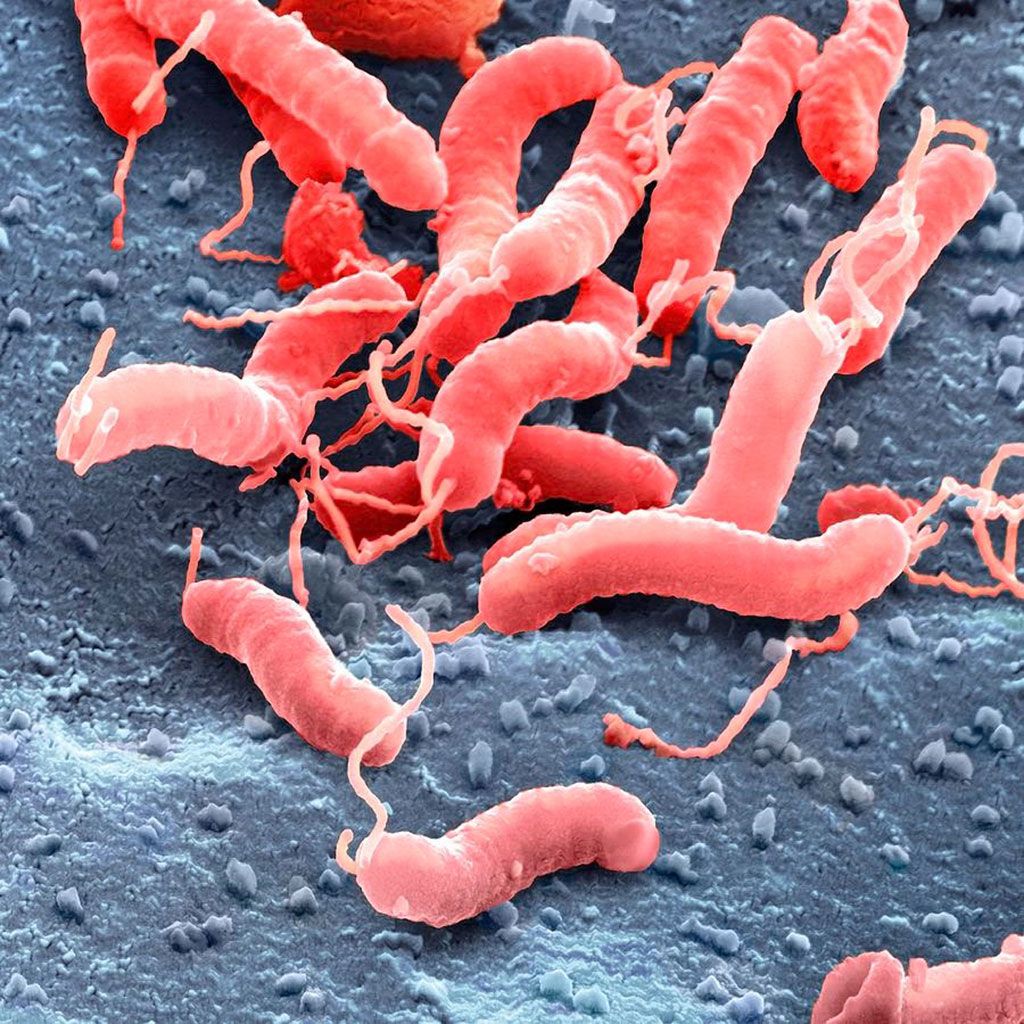
Imagen: Micrografía electrónica de barrido de Helicobacter pylori: la resistencia a los antibióticos se puede perfilar utilizando la secuenciación de próxima generación (Fotografía cortesía de Juergen Berger/Science Photo Library)
Las tasas de erradicación de Helicobacter pylori han disminuido junto con el aumento de la resistencia a los antimicrobianos en todo el mundo. Es necesario realizar pruebas de resistencia a los antibióticos rápidas, exactas y fiables, especialmente en los casos refractarios.
Las pruebas de sensibilidad basadas en cultivos requieren una biopsia gástrica endoscópica, con los consiguientes inconvenientes y costos. Las pruebas moleculares que utilizan la secuenciación de siguiente generación (NGS) de las heces permiten, potencialmente, una rápida predicción de la resistencia a los seis antimicrobianos de uso común.
Los científicos clínicos del Hospital de Rhode Island (Providence, RI, EUA) y sus colegas, compararon la exactitud de la NGS con la biopsia gástrica para identificar la resistencia a los antibióticos de H. pylori en 262 pacientes programados para endoscopia superior en cuatro consultorios clínicos. Se tomaron dos biopsias gástricas para NGS y también se obtuvo una muestra de heces expulsados espontáneamente dentro de las dos semanas posteriores a la endoscopia, pero antes de comenzar el tratamiento para H. pylori. H. pylori se confirmó en biopsias mediante PCR seguida de NGS. H. pylori en heces se confirmó mediante prueba de antígeno fecal y PCR. Las muestras de heces positivas, en al menos dos pruebas de heces, también fueron examinadas por NGS para predecir la resistencia a amoxicilina, claritromicina, metronidazol, tetraciclina, levofloxacina y rifabutina.
Los investigadores informaron que 73 (29%) pacientes fueron H. pylori positivos en las pruebas de heces; dos tenían ADN gástrico insuficiente para el análisis. De los 71 casos evaluables, se obtuvieron resultados idénticos para las muestras de heces y biopsias para los seis antibióticos en 65 (91,5%). En seis casos hubo desajuste entre los resultados gástricos y de las heces; en cuatro casos, esto se debió a una diferencia de mutación asociada al antibiótico. Para el 70,4% de las biopsias gástricas, hubo al menos una mutación asociada a la resistencia. Solo 21 (29,6%) no tenían mutaciones. Los resultados para las heces fueron similares: 50 casos (68,5%) tenían al menos una mutación asociada a resistencia y 23 (31,5%) no tenían mutaciones. La concordancia entre las heces y las biopsias gástricas para los antibióticos individuales osciló entre el 89% (metronidazol) y el 100%.
Steven Moss, MD, gastroenterólogo y autor principal del estudio, dijo: “Las pruebas de susceptibilidad basadas en cultivos requieren una biopsia gástrica endoscópica, con los consiguientes inconvenientes y costos. Ahora es posible obtener rápidamente datos de susceptibilidad sin necesidad de endoscopia”.
Los autores concluyeron que la determinación del perfil de la resistencia a los antibióticos de H. pylori mediante NGS, a partir de muestras de heces, proporciona resultados rápidos muy comparables a los obtenidos a partir de biopsias gástricas. El uso de NGS para determinar la resistencia a los antibióticos de H. pylori utilizando heces evita el costo, las molestias y los riesgos de la endoscopia para los pacientes en los que se necesita un perfil de resistencia. El estudio fue presentado en el Congreso Virtual 2021 del Colegio Americano de Gastroenterología (ACG), que se llevó a cabo del 22 al 27 de octubre de 2021.
Enlace relacionado:
Hospital de Rhode Island
Las pruebas de sensibilidad basadas en cultivos requieren una biopsia gástrica endoscópica, con los consiguientes inconvenientes y costos. Las pruebas moleculares que utilizan la secuenciación de siguiente generación (NGS) de las heces permiten, potencialmente, una rápida predicción de la resistencia a los seis antimicrobianos de uso común.
Los científicos clínicos del Hospital de Rhode Island (Providence, RI, EUA) y sus colegas, compararon la exactitud de la NGS con la biopsia gástrica para identificar la resistencia a los antibióticos de H. pylori en 262 pacientes programados para endoscopia superior en cuatro consultorios clínicos. Se tomaron dos biopsias gástricas para NGS y también se obtuvo una muestra de heces expulsados espontáneamente dentro de las dos semanas posteriores a la endoscopia, pero antes de comenzar el tratamiento para H. pylori. H. pylori se confirmó en biopsias mediante PCR seguida de NGS. H. pylori en heces se confirmó mediante prueba de antígeno fecal y PCR. Las muestras de heces positivas, en al menos dos pruebas de heces, también fueron examinadas por NGS para predecir la resistencia a amoxicilina, claritromicina, metronidazol, tetraciclina, levofloxacina y rifabutina.
Los investigadores informaron que 73 (29%) pacientes fueron H. pylori positivos en las pruebas de heces; dos tenían ADN gástrico insuficiente para el análisis. De los 71 casos evaluables, se obtuvieron resultados idénticos para las muestras de heces y biopsias para los seis antibióticos en 65 (91,5%). En seis casos hubo desajuste entre los resultados gástricos y de las heces; en cuatro casos, esto se debió a una diferencia de mutación asociada al antibiótico. Para el 70,4% de las biopsias gástricas, hubo al menos una mutación asociada a la resistencia. Solo 21 (29,6%) no tenían mutaciones. Los resultados para las heces fueron similares: 50 casos (68,5%) tenían al menos una mutación asociada a resistencia y 23 (31,5%) no tenían mutaciones. La concordancia entre las heces y las biopsias gástricas para los antibióticos individuales osciló entre el 89% (metronidazol) y el 100%.
Steven Moss, MD, gastroenterólogo y autor principal del estudio, dijo: “Las pruebas de susceptibilidad basadas en cultivos requieren una biopsia gástrica endoscópica, con los consiguientes inconvenientes y costos. Ahora es posible obtener rápidamente datos de susceptibilidad sin necesidad de endoscopia”.
Los autores concluyeron que la determinación del perfil de la resistencia a los antibióticos de H. pylori mediante NGS, a partir de muestras de heces, proporciona resultados rápidos muy comparables a los obtenidos a partir de biopsias gástricas. El uso de NGS para determinar la resistencia a los antibióticos de H. pylori utilizando heces evita el costo, las molestias y los riesgos de la endoscopia para los pacientes en los que se necesita un perfil de resistencia. El estudio fue presentado en el Congreso Virtual 2021 del Colegio Americano de Gastroenterología (ACG), que se llevó a cabo del 22 al 27 de octubre de 2021.
Enlace relacionado:
Hospital de Rhode Island
Últimas Diagnóstico Molecular noticias
- Ensayo de aprendizaje automático basado en sangre detecta de forma no invasiva el cáncer de ovario
- Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
- Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
- Prueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
- Sistema de RT-PCR en el punto de atención de 10 minutos detecta hasta 32 objetivos por muestra
- Células extraídas de orina podrían permitir detección más temprana de enfermedad renal
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
Una plataforma de diagnóstico innovadora que ofrece resultados de pruebas de susceptibilidad a los antibióticos (AST) con una velocidad sin precedentes puede convertirse en una herramienta importante para... Más
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... MásPatología
ver canal
Biopsia de piel virtual determina la presencia de células cancerosas
Cuando los dermatólogos detectan una marca inusual en la piel de un paciente, se enfrentan a una elección: controlarla durante algún tiempo o extraerla para realizar una biopsia.... Más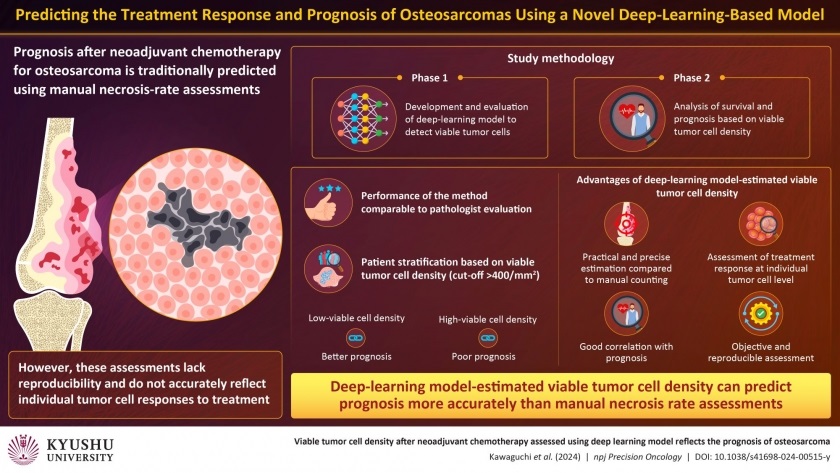
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)


