Características del microbioma humano estratifican a los niños con SII
|
Por el equipo editorial de LabMedica en español Actualizado el 07 May 2019 |

Imagen: El fluorómetro Qubit 4 diseñado para medir con exactitud el ADN, el ARN y la cantidad de proteínas, y ahora también la integridad y calidad del ARN, utilizando los análisis Qubit, altamente sensibles (Fotografía cortesía de Thermo Fisher Scientific).
El síndrome del intestino irritable (SII) es una afección gastrointestinal disruptiva caracterizada por hinchazón, cambios en los hábitos intestinales y dolor que afecta hasta al 20% de la población mundial (niños y adultos). La evidencia creciente indica que el inicio y los síntomas del SII están relacionados con el microbioma intestinal.
Para mejorar el tratamiento de los niños con SII, los investigadores han desarrollado una forma sofisticada de analizar los contenidos microbianos y metabólicos del intestino. Un informe describe cómo una nueva batería de pruebas permite a los científicos diferenciar a los pacientes con SII de los niños sanos e identifica las correlaciones entre ciertos microbios y metabolitos con el dolor abdominal.
Los científicos de la facultad de medicina Baylor (Houston, TX, EUA) y sus colegas, obtuvieron muestras de 23 niños preadolescentes con SII (de 7 a 12 años) y 22 controles sanos. Se pidió a los participantes que hicieran anotaciones diarias en sus diarios sobre el dolor y las heces durante dos semanas y que proporcionaran muestras de heces (fecales).
El ADN de las heces se extrajo utilizando el kit de aislamiento de ADN PowerSoil (MO BIO Laboratories, Carlsbad, CA, EUA). La calidad y el rendimiento del ADN se evaluaron mediante geles de agarosa NanoDrop 1000 (NanoDrop, Wilmington, DE, EUA) y el fluorómetro Qubit (Life Technologies, Carlsbad, CA, EUA). Se generaron bibliotecas de WGS utilizando bibliotecas pareadas de 100 pb y la plataforma HiSeq 2000 (Illumina, San Diego, CA, EUA).
Los investigadores descubrieron que había diferencias en la composición bacteriana, los genes bacterianos y los metabolitos fecales en niños con SII en comparación con los controles sanos. Además de identificar las correlaciones de estos factores con el dolor abdominal, generaron un clasificador de gran exactitud utilizando marcadores metagenómicos y metabólicos que permiten diferenciar a los niños con SII de los controles sanos con una exactitud del 80% o más. Este clasificador evalúa metabolitos específicos, tipos de bacterias, vías funcionales y otros factores.
Este clasificador basado en microbiomas puede ayudar potencialmente a identificar subpoblaciones de niños con SII que tienen más probabilidades de beneficiarse de terapias relacionadas con microbiomas, incluida la modificación de la dieta, mientras que guían a otros a planes de tratamiento alternativos apropiados. Los investigadores también proporcionan información sobre cómo los hallazgos específicos relacionados con los microbiomas pueden estar relacionados con el dolor abdominal, lo que abre nuevos enfoques potenciales para el tratamiento.
James Versalovic, MD, PhD, patólogo y coautor del estudio, dijo: “Este estudio destaca la importancia del eje microbioma-intestino-cerebro y nuestra comprensión del dolor abdominal crónico. El desarrollo de nuevos clasificadores de enfermedades basados en datos de microbiomas permite que se desarrollen diagnósticos de precisión para el SII y trastornos similares. Aunque otros estudios han encontrado diferencias en los microbiomas intestinales de los pacientes con SII, este estudio es el primero en combinar el análisis profundo de microbiomas con el desarrollo de nuevas estrategias de diagnóstico”. El estudio se publicó el 17 de abril de 2019 en la revista Journal of Molecular Diagnostics.
Enlace relacionado:
Facultad de Medicina Baylor
MO BIO Laboratories
NanoDrop
Life Technologies
Illumina
Para mejorar el tratamiento de los niños con SII, los investigadores han desarrollado una forma sofisticada de analizar los contenidos microbianos y metabólicos del intestino. Un informe describe cómo una nueva batería de pruebas permite a los científicos diferenciar a los pacientes con SII de los niños sanos e identifica las correlaciones entre ciertos microbios y metabolitos con el dolor abdominal.
Los científicos de la facultad de medicina Baylor (Houston, TX, EUA) y sus colegas, obtuvieron muestras de 23 niños preadolescentes con SII (de 7 a 12 años) y 22 controles sanos. Se pidió a los participantes que hicieran anotaciones diarias en sus diarios sobre el dolor y las heces durante dos semanas y que proporcionaran muestras de heces (fecales).
El ADN de las heces se extrajo utilizando el kit de aislamiento de ADN PowerSoil (MO BIO Laboratories, Carlsbad, CA, EUA). La calidad y el rendimiento del ADN se evaluaron mediante geles de agarosa NanoDrop 1000 (NanoDrop, Wilmington, DE, EUA) y el fluorómetro Qubit (Life Technologies, Carlsbad, CA, EUA). Se generaron bibliotecas de WGS utilizando bibliotecas pareadas de 100 pb y la plataforma HiSeq 2000 (Illumina, San Diego, CA, EUA).
Los investigadores descubrieron que había diferencias en la composición bacteriana, los genes bacterianos y los metabolitos fecales en niños con SII en comparación con los controles sanos. Además de identificar las correlaciones de estos factores con el dolor abdominal, generaron un clasificador de gran exactitud utilizando marcadores metagenómicos y metabólicos que permiten diferenciar a los niños con SII de los controles sanos con una exactitud del 80% o más. Este clasificador evalúa metabolitos específicos, tipos de bacterias, vías funcionales y otros factores.
Este clasificador basado en microbiomas puede ayudar potencialmente a identificar subpoblaciones de niños con SII que tienen más probabilidades de beneficiarse de terapias relacionadas con microbiomas, incluida la modificación de la dieta, mientras que guían a otros a planes de tratamiento alternativos apropiados. Los investigadores también proporcionan información sobre cómo los hallazgos específicos relacionados con los microbiomas pueden estar relacionados con el dolor abdominal, lo que abre nuevos enfoques potenciales para el tratamiento.
James Versalovic, MD, PhD, patólogo y coautor del estudio, dijo: “Este estudio destaca la importancia del eje microbioma-intestino-cerebro y nuestra comprensión del dolor abdominal crónico. El desarrollo de nuevos clasificadores de enfermedades basados en datos de microbiomas permite que se desarrollen diagnósticos de precisión para el SII y trastornos similares. Aunque otros estudios han encontrado diferencias en los microbiomas intestinales de los pacientes con SII, este estudio es el primero en combinar el análisis profundo de microbiomas con el desarrollo de nuevas estrategias de diagnóstico”. El estudio se publicó el 17 de abril de 2019 en la revista Journal of Molecular Diagnostics.
Enlace relacionado:
Facultad de Medicina Baylor
MO BIO Laboratories
NanoDrop
Life Technologies
Illumina
Últimas Microbiología noticias
- Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
- Análisis de sangre predice sepsis e insuficiencia orgánica en niños
- Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
- Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
- Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
- Nuevo análisis para tuberculosis podría ampliar acceso a pruebas en países de ingresos bajos y medios
- Prueba rápida diagnostica enfermedades tropicales en horas para tratamiento con antibióticos más rápido
- Pruebas moleculares rápidas permiten tratamiento antibiótico más rápido y específico para neumonía
- Plataforma rápida de PSA proporciona resultados terapéuticos específicos días antes que el estándar de atención actual
- Nuevo método de análisis detecta patógenos en sangre de forma más rápida y precisa al fundir ADN
- Prueba rápida de sepsis ofrece resultados dos días más rápidos
- Diagnóstico rápido portátil por PCR podría detectar gonorrea y susceptibilidad a antibióticos
- Prueba CRISPR diagnostica mpox más rápido que método de PCR de laboratorio
- Prueba de PCR multiplexada para detección de patógenos y resistencia a antibióticos ayuda a brindar un tratamiento rápido de ITU
- Nuevo algoritmo detecta e identifica nuevos organismos bacterianos
- Analizador de mesa promete detección de ITU en 1 hora e indicación de sensibilidad a antibióticos
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
Una plataforma de diagnóstico innovadora que ofrece resultados de pruebas de susceptibilidad a los antibióticos (AST) con una velocidad sin precedentes puede convertirse en una herramienta importante para... Más
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... MásPatología
ver canal
Biopsia de piel virtual determina la presencia de células cancerosas
Cuando los dermatólogos detectan una marca inusual en la piel de un paciente, se enfrentan a una elección: controlarla durante algún tiempo o extraerla para realizar una biopsia.... Más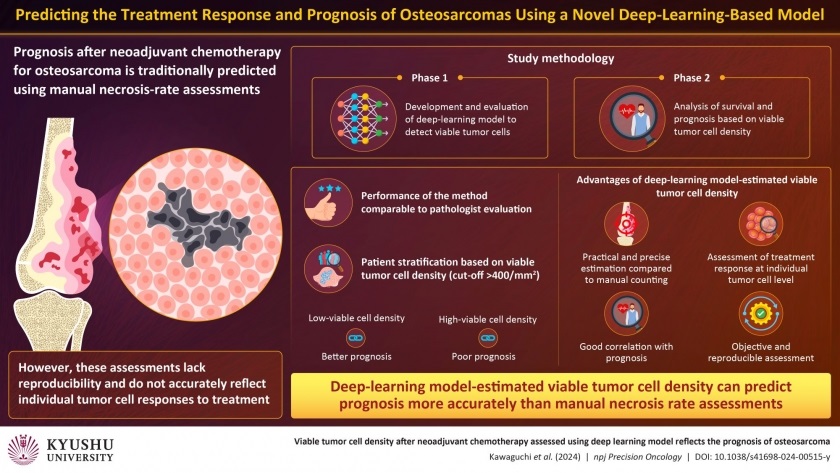
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más











.jpg)


