Análisis rápido de flujo lateral detecta las variantes de la COVID-19 y diferencia la COVID-19 de otras enfermedades virales respiratorias
|
Por el equipo editorial de LabMedica en español Actualizado el 04 Mar 2021 |
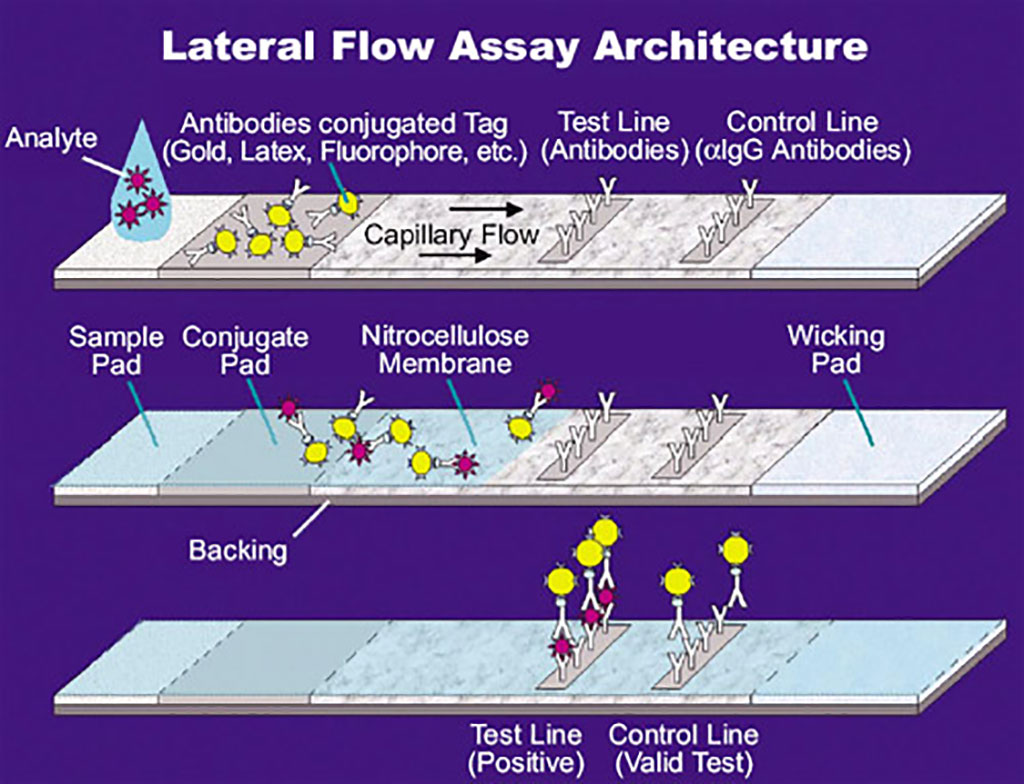
Imagen: Ilustración de un ensayo de flujo lateral (LFA) (Fotografía cortesía de la Administración Nacional de Aeronáutica y del Espacio de EUA a través de Wikimedia Commons)
Una publicación reciente informó el desarrollo de dos pruebas de diagnóstico rápido: una que detecta variantes de COVID-19 y otra que diferencia la COVID-19 de otras enfermedades virales respiratorias.
Los investigadores de la Facultad de Medicina de la Universidad de Minnesota (Minneapolis/St. Paul, EUA) utilizaron la herramienta de edición de genes CRISPR/Cas9 para desarrollar dos pruebas rápidas de diagnóstico de flujo lateral. Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013 se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) en una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada. El sistema CRISPR/Cas9 convencional de Streptococcus pyogenes se compone de dos partes: la enzima Cas9, que escinde la molécula de ADN y guías específicas de ARN que llevan la proteína Cas9 al gen diana en una hebra de ADN.
Los investigadores integraron reactivos disponibles comercialmente en un ensayo de flujo lateral (LFA) basado en CRISPR/Cas9, que podría detectar secuencias del coronavirus 2 del síndrome respiratorio agudo severo (SARS-CoV-2) con especificidad de una sola base. Este enfoque requería un equipo mínimo y representaba una plataforma simplificada para la implementación en el campo. También desarrollaron un ensayo rápido múltiplex de escisión de nucleasa CRISPR/Cas9 de fluorescencia, capaz de detectar y diferenciar el SARS-CoV-2, la influenza A y B y el virus sincitial respiratorio (VSR) en una sola reacción.
Las tiras reactivas del LFA emplearon isotiocianato de fluoresceína (FITC)/6-carboxifluoresceína (FAM) y biotina unidas para generar un resultado positivo. Por lo tanto, los investigadores utilizaron un cebador de PCR marcado con FITC/FAM y un Cas9 biotinilado inactivo con nucleasa (“muerto”) y un solo ARNsg específico para el gen ORF8a del SARS-Co-V-2 para marcar los amplicones para su detección mediante el LFA. Este enfoque fue capaz de resolución de un solo nucleótido y evitó falsos positivos de dímero de cebador o artefactos de amplificación no específicos que podrían ocurrir con el uso de cebadores en tándem marcados con FITC y biotina para los LFA.
“La aprobación de la vacuna contra el SARS-CoV-2 es muy prometedora, pero el tiempo entre las primeras dosis y la inmunidad de la población puede ser de meses”, dijo el primer autor, el Dr. Mark J. Osborn, profesor asistente de pediatría en la Facultad de Medicina de la Universidad de Minnesota. “Esta plataforma de pruebas puede ayudar a cerrar la brecha entre la inmunización y la inmunidad”.
Las pruebas rápidas de LFA se describieron en la edición en línea del 12 de febrero de 2021 de la revista Bioengineering.
Enlace relacionado:
Facultad de Medicina de la Universidad de Minnesota
Los investigadores de la Facultad de Medicina de la Universidad de Minnesota (Minneapolis/St. Paul, EUA) utilizaron la herramienta de edición de genes CRISPR/Cas9 para desarrollar dos pruebas rápidas de diagnóstico de flujo lateral. Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013 se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) en una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada. El sistema CRISPR/Cas9 convencional de Streptococcus pyogenes se compone de dos partes: la enzima Cas9, que escinde la molécula de ADN y guías específicas de ARN que llevan la proteína Cas9 al gen diana en una hebra de ADN.
Los investigadores integraron reactivos disponibles comercialmente en un ensayo de flujo lateral (LFA) basado en CRISPR/Cas9, que podría detectar secuencias del coronavirus 2 del síndrome respiratorio agudo severo (SARS-CoV-2) con especificidad de una sola base. Este enfoque requería un equipo mínimo y representaba una plataforma simplificada para la implementación en el campo. También desarrollaron un ensayo rápido múltiplex de escisión de nucleasa CRISPR/Cas9 de fluorescencia, capaz de detectar y diferenciar el SARS-CoV-2, la influenza A y B y el virus sincitial respiratorio (VSR) en una sola reacción.
Las tiras reactivas del LFA emplearon isotiocianato de fluoresceína (FITC)/6-carboxifluoresceína (FAM) y biotina unidas para generar un resultado positivo. Por lo tanto, los investigadores utilizaron un cebador de PCR marcado con FITC/FAM y un Cas9 biotinilado inactivo con nucleasa (“muerto”) y un solo ARNsg específico para el gen ORF8a del SARS-Co-V-2 para marcar los amplicones para su detección mediante el LFA. Este enfoque fue capaz de resolución de un solo nucleótido y evitó falsos positivos de dímero de cebador o artefactos de amplificación no específicos que podrían ocurrir con el uso de cebadores en tándem marcados con FITC y biotina para los LFA.
“La aprobación de la vacuna contra el SARS-CoV-2 es muy prometedora, pero el tiempo entre las primeras dosis y la inmunidad de la población puede ser de meses”, dijo el primer autor, el Dr. Mark J. Osborn, profesor asistente de pediatría en la Facultad de Medicina de la Universidad de Minnesota. “Esta plataforma de pruebas puede ayudar a cerrar la brecha entre la inmunización y la inmunidad”.
Las pruebas rápidas de LFA se describieron en la edición en línea del 12 de febrero de 2021 de la revista Bioengineering.
Enlace relacionado:
Facultad de Medicina de la Universidad de Minnesota
Últimas COVID-19 noticias
- Inmunosensor nuevo allana el camino para pruebas rápidas POC para COVID-19 y enfermedades infecciosas emergentes
- Encuentran etiologías de COVID prolongada en muestras de sangre con infección aguda
- Dispositivo novedoso detecta anticuerpos contra la COVID-19 en cinco minutos
- Prueba para COVID-19 mediante CRISPR detecta SARS-CoV-2 en 30 minutos usando tijeras genéticas
- Asocian disbiosis del microbioma intestinal con la COVID-19
- Validan prueba rápida novedosa de antígeno para el SARS-CoV-2 con respecto a su exactitud diagnóstica
- Prueba nueva COVID + Influenza + VSR ayudará a estar preparados para la ‘tripledemia’
- IA elimina las conjeturas de las pruebas de flujo lateral
- Prueba de antígeno del SARS-CoV-2 más rápida, jamás diseñada, permite realizar pruebas de COVID-19 no invasivas en cualquier entorno
- Pruebas rápidas de antígeno detectan las variantes ómicron, delta del SARS-CoV-2
- Prueba en sangre realizada durante la infección inicial predice el riesgo de COVID prolongada
- Investigadores afirman que hay que crear “reservistas” de laboratorio para responder más rápidamente a la próxima pandemia
- Estudio encuentra que los profesionales sanitarios mostraron mayor interés en tecnologías POC durante la pandemia
- Plataforma de análisis de bajo costo para la COVID-19 combina sensibilidad de la PCR y velocidad de pruebas de antígeno
- Prueba de sangre por punción digital identifica inmunidad a la COVID-19
- Kit de prueba rápida determina inmunidad contra la COVID-19 y sus variantes
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas (CPCP), una neoplasia maligna neuroendocrina que progresa rápidamente, presenta bajas tasas de supervivencia. A pesar de su heterogeneidad molecular y clínica, el... Más
Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
La biopsia líquida, un método para diagnosticar el cáncer mediante análisis de sangre de rutina, es una herramienta potencial importante para la detección temprana del... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Innovadora plataforma de diagnóstico proporciona resultados de AST con velocidad sin precedentes
Una plataforma de diagnóstico innovadora que ofrece resultados de pruebas de susceptibilidad a los antibióticos (AST) con una velocidad sin precedentes puede convertirse en una herramienta importante para... Más
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... MásPatología
ver canal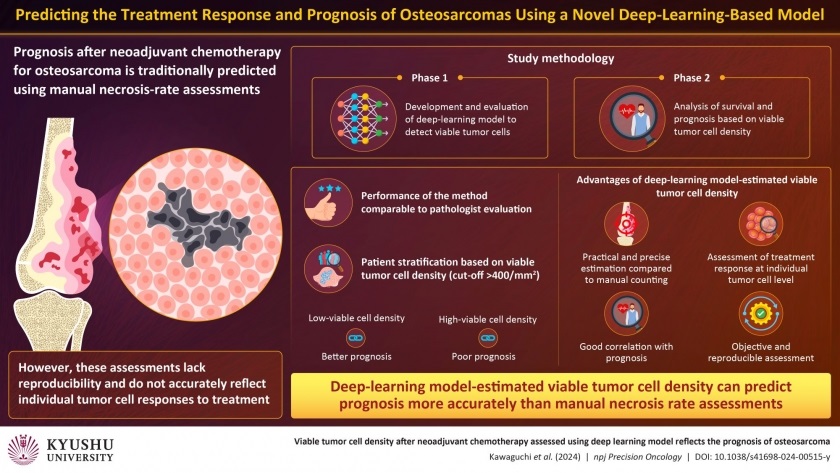
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)

.jpg)



