Pruebas genéticas tienden a no poder detectar la hipercolesterolemia familiar
|
Por el equipo editorial de LabMedica en español Actualizado el 17 Aug 2021 |

Imagen: El NovaSeq 6000 realiza la secuenciación del genoma completo (Fotografía cortesía de Illumina)
La hipercolesterolemia familiar es un trastorno genético caracterizado por niveles altos de colesterol, específicamente niveles muy altos de lipoproteínas de baja densidad (LDL), en la sangre y enfermedad cardiovascular temprana. Las mutaciones más comunes disminuyen el número de receptores de LDL funcionales en el hígado.
La hipercolesterolemia familiar (HF) es la enfermedad cardiovascular hereditaria más común y conlleva importantes riesgos de morbilidad y mortalidad. Las pruebas genéticas pueden identificar a los individuos afectados, pero algunos ensayos basados en arrays analizan solo un pequeño subconjunto de variantes patógenas conocidas. La HF es un trastorno autosómico dominante que se asocia con mayor frecuencia con variantes en el gen del receptor de LDL (LDLR).
Los bioquímicos moleculares del Instituto de Medicina Genómica Geisinger (Danville, PA, EUA) y sus colegas llevaron a cabo un estudio transversal y compararon los resultados de las pruebas genéticas integrales para las variantes clínicamente significativas asociadas con la HF con los resultados de un subconjunto de 24 variantes examinadas por un array de variantes limitadas. Los datos fueron desidentificados al analizar los resultados de secuenciación de próxima generación de los paneles genéticos basados en indicación o genéticos proactivos. Se incluyeron las personas que recibieron pruebas genéticas basadas en secuenciación de próxima generación, ya sea para una indicación de HF entre noviembre de 2015 y junio de 2020 o como un examen de salud proactivo entre febrero de 2016 y junio de 2020.
Los genes fueron ubicados con cebos de oligonucleótidos para capturar los exones ± 10 pares de bases de la secuencia intrónica adyacente y ciertas regiones no codificantes de interés clínico. Las regiones seleccionadas se secuenciaron a una profundidad media de 350 × cobertura de lectura (mínimo 50 ×). Toda la secuenciación primaria se realizó en instrumentos Illumina HiSeq o NovaSeq (Illumina, San Diego, CA, EUA). Se identificó el número de variantes patógenas o probablemente patógenas (P/LP). El estudio incluyó a 4.563 personas que fueron remitidas para pruebas de diagnóstico de HF y 6.482 personas que recibieron la secuenciación de próxima generación de genes asociados a HF como parte de una prueba genética proactiva. Entre los individuos de la cohorte de indicación, la edad media (rango intercuartílico) en el momento de la prueba fue de 49 (32-61) años, el 55,4% (2.528 de 4.563) eran mujeres y el 63,6% (2.902 de 4.563) eran blancos/caucásicos autoreportados.
Las cohortes se analizaron para detectar más de 2.000 posibles variantes en cuatro genes asociados a la HF: LDLR, APOB, PCSK9 y LDLRAP1. El equipo informó que, en la cohorte de indicación, la tasa de detección positiva habría sido del 8,4% (382 de 4.563) para una detección de variante limitada en comparación con el 27,0% (1.230 de 4.563) observado con la prueba completa basada en secuenciación de próxima generación. Como resultado, el 68,9% (848 de 1.230) de los individuos con un hallazgo de P/LP en un gen asociado a la HF se habrían pasado por alto en el cribado limitado.
El potencial de resultados pasados por alto en la cohorte de indicación varió según la ascendencia. Entre las personas con un hallazgo de P/LP, el 93,7% (59 de 63) de las personas negras/afroamericanas autoreportadas y el 84,7% (122 de 144) de las personas hispanas no habrían sido detectadas en el cribado de variante limitada, en comparación con el 33,3 % (4 de 12) de judíos asquenazíes. En la cohorte proactiva, la prevalencia de variantes de HF clínicamente significativas fue de aproximadamente 1: 191 según la prueba integral, y el 61,8% (21 de 34) de los individuos con un hallazgo de P/LP asociado con HF se habrían pasado por alto por un cribado limitado a la variante.
Los autores concluyen que las pruebas de detección de variantes limitadas pueden tranquilizar falsamente a la mayoría de las personas con riesgo de HF de que no portan una variante que cause la enfermedad, especialmente las personas de ascendencia negra/afroamericana e hispana autoreportadas. El estudio fue publicado el 26 de mayo de 2021 en la revista JAMA Cardiology.
Enlace relacionado:
Instituto de Medicina Genómica Geisinger
La hipercolesterolemia familiar (HF) es la enfermedad cardiovascular hereditaria más común y conlleva importantes riesgos de morbilidad y mortalidad. Las pruebas genéticas pueden identificar a los individuos afectados, pero algunos ensayos basados en arrays analizan solo un pequeño subconjunto de variantes patógenas conocidas. La HF es un trastorno autosómico dominante que se asocia con mayor frecuencia con variantes en el gen del receptor de LDL (LDLR).
Los bioquímicos moleculares del Instituto de Medicina Genómica Geisinger (Danville, PA, EUA) y sus colegas llevaron a cabo un estudio transversal y compararon los resultados de las pruebas genéticas integrales para las variantes clínicamente significativas asociadas con la HF con los resultados de un subconjunto de 24 variantes examinadas por un array de variantes limitadas. Los datos fueron desidentificados al analizar los resultados de secuenciación de próxima generación de los paneles genéticos basados en indicación o genéticos proactivos. Se incluyeron las personas que recibieron pruebas genéticas basadas en secuenciación de próxima generación, ya sea para una indicación de HF entre noviembre de 2015 y junio de 2020 o como un examen de salud proactivo entre febrero de 2016 y junio de 2020.
Los genes fueron ubicados con cebos de oligonucleótidos para capturar los exones ± 10 pares de bases de la secuencia intrónica adyacente y ciertas regiones no codificantes de interés clínico. Las regiones seleccionadas se secuenciaron a una profundidad media de 350 × cobertura de lectura (mínimo 50 ×). Toda la secuenciación primaria se realizó en instrumentos Illumina HiSeq o NovaSeq (Illumina, San Diego, CA, EUA). Se identificó el número de variantes patógenas o probablemente patógenas (P/LP). El estudio incluyó a 4.563 personas que fueron remitidas para pruebas de diagnóstico de HF y 6.482 personas que recibieron la secuenciación de próxima generación de genes asociados a HF como parte de una prueba genética proactiva. Entre los individuos de la cohorte de indicación, la edad media (rango intercuartílico) en el momento de la prueba fue de 49 (32-61) años, el 55,4% (2.528 de 4.563) eran mujeres y el 63,6% (2.902 de 4.563) eran blancos/caucásicos autoreportados.
Las cohortes se analizaron para detectar más de 2.000 posibles variantes en cuatro genes asociados a la HF: LDLR, APOB, PCSK9 y LDLRAP1. El equipo informó que, en la cohorte de indicación, la tasa de detección positiva habría sido del 8,4% (382 de 4.563) para una detección de variante limitada en comparación con el 27,0% (1.230 de 4.563) observado con la prueba completa basada en secuenciación de próxima generación. Como resultado, el 68,9% (848 de 1.230) de los individuos con un hallazgo de P/LP en un gen asociado a la HF se habrían pasado por alto en el cribado limitado.
El potencial de resultados pasados por alto en la cohorte de indicación varió según la ascendencia. Entre las personas con un hallazgo de P/LP, el 93,7% (59 de 63) de las personas negras/afroamericanas autoreportadas y el 84,7% (122 de 144) de las personas hispanas no habrían sido detectadas en el cribado de variante limitada, en comparación con el 33,3 % (4 de 12) de judíos asquenazíes. En la cohorte proactiva, la prevalencia de variantes de HF clínicamente significativas fue de aproximadamente 1: 191 según la prueba integral, y el 61,8% (21 de 34) de los individuos con un hallazgo de P/LP asociado con HF se habrían pasado por alto por un cribado limitado a la variante.
Los autores concluyen que las pruebas de detección de variantes limitadas pueden tranquilizar falsamente a la mayoría de las personas con riesgo de HF de que no portan una variante que cause la enfermedad, especialmente las personas de ascendencia negra/afroamericana e hispana autoreportadas. El estudio fue publicado el 26 de mayo de 2021 en la revista JAMA Cardiology.
Enlace relacionado:
Instituto de Medicina Genómica Geisinger
Últimas Diagnóstico Molecular noticias
- Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
- Prueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
- Sistema de RT-PCR en el punto de atención de 10 minutos detecta hasta 32 objetivos por muestra
- Células extraídas de orina podrían permitir detección más temprana de enfermedad renal
- Análisis de sangre identifica a personas con mayor riesgo de morir por insuficiencia cardíaca
- Análisis de sangre muestra precisión del 83 % para detectar cáncer colorrectal
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal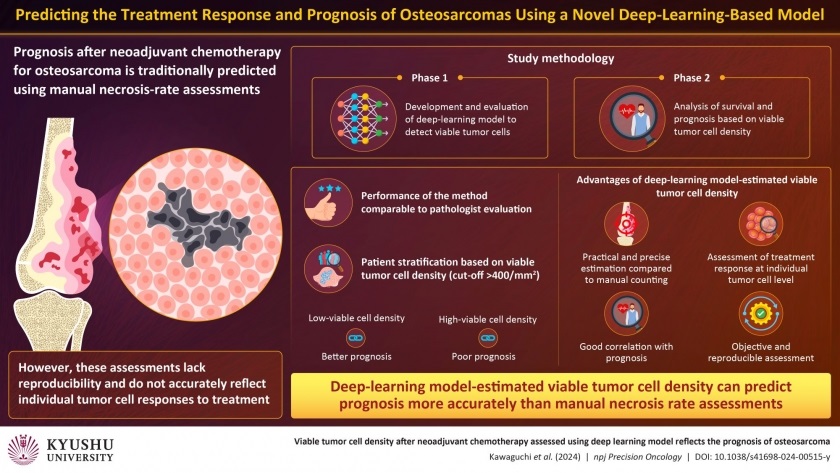
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)