Identifican mutaciones genéticas para el raro síndrome de VEXAS
|
Por el equipo editorial de LabMedica en español Actualizado el 24 Mar 2021 |
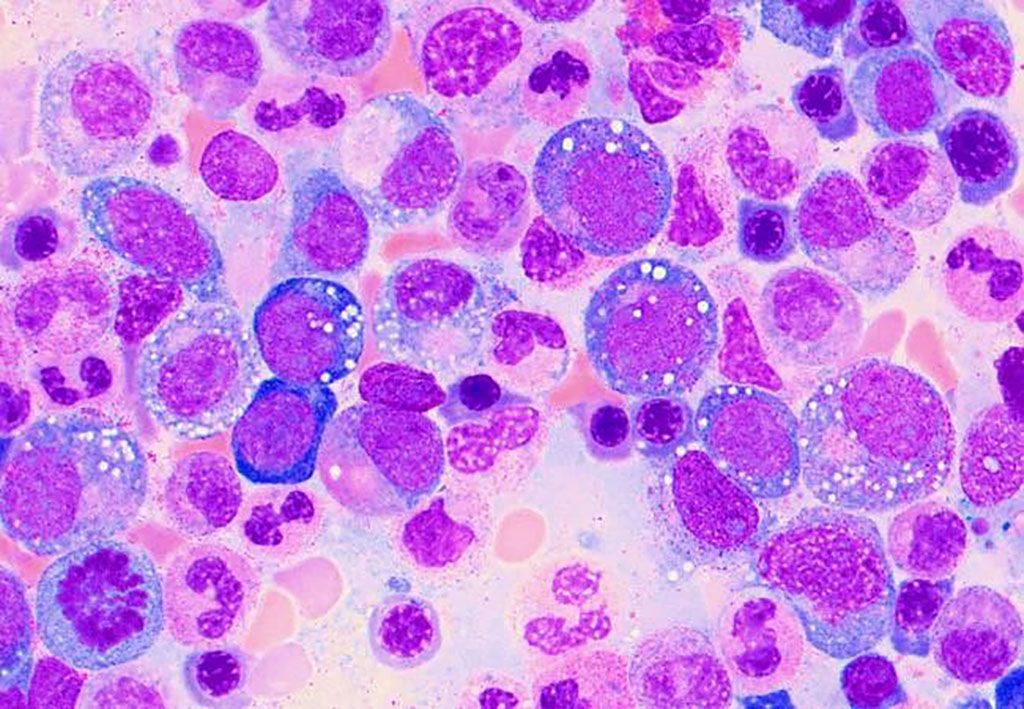
Imagen: Frotis de médula ósea que muestra vacuolas en las células mieloides en un paciente con VEXAS (Fotografía cortesía de Katherine Calvo, MD, PhD y Marcela Ferrada, MD)
El síndrome de VEXAS es una afección inflamatoria grave que se desarrolla en hombres mayores de 50 años, lo que hace que se sientan muy enfermos y fatigados, y puede ser fatal. Originalmente se pensó que era raro, pero un nuevo estudio ha identificado mutaciones genéticas que indican que la enfermedad es, en realidad, mucho más común.
El síndrome de VEXAS causa fiebres inexplicables, erupciones cutáneas dolorosas y afecta la médula ósea, lo que resulta en una reducción del número de glóbulos rojos y blancos. La enfermedad afecta solo a los hombres porque es causada por mutaciones genéticas en el cromosoma X y los hombres son portadores de un solo cromosoma X. Las mutaciones no están presentes al nacer; por el contrario, se desarrollan durante la vida del paciente.
Un equipo multicéntrico dirigido por la Universidad de Leeds (Leeds, Reino Unido), examinó muestras de ADN para establecer la prevalencia de las mutaciones genéticas identificadas cuando se descubrió la enfermedad por primera vez en 2020. Examinaron una cohorte de 18 pacientes locales que coincidieron con los síntomas y encontraron mutaciones en 10 de ellos. Ocho tenían la variante conocida previamente asociada con la enfermedad, pero dos pacientes tenían variantes completamente diferentes. Esto identificó una nueva forma en que las mutaciones pueden causar VEXAS, lo que significa que es probable que sea mucho más común de lo que se pensaba actualmente. VEXAS significa Vacuolas, enzima E1, ligado al cromosoma X, autoinflamatorio, síndrome somático.
El equipo identificó 10 pacientes nuevos con mutaciones somáticas en UBA1, pero solo ocho tenían una alteración en p.Met41. Se identificó la presencia de una nueva variante, c.167C>T; p.Ser56Phe, en los linajes mieloides y no linfoides que condujo a una pérdida preferencial de la actividad catalítica del UBA1 citoplásmico. Se identificó una nueva variante adicional, c.118-1G> C en el sitio aceptor de empalme del exón 3, que conduce a un empalme alterado in vitro. Las biopsias de médula ósea de dos pacientes con una sustitución de Met41 y la nueva variante del sitio de empalme coincidieron con las características de VEXAS informadas anteriormente. La médula ósea del paciente con la variante p.Ser56Phe fue menos similar, probablemente promovida por un mecanismo de enfermedad distinto pero superpuesto.
Sinisa Savic, MRCP, FRCPath, PhD, inmunóloga clínica y autora principal del estudio, dijo: “He cuidado a varios pacientes con lo que ahora sabemos que es el síndrome VEXAS durante varios años. Su atención se ha visto complicada por el hecho de que no contábamos con un diagnóstico, lo que dificultaba mucho la elección de su tratamiento y aconsejarles sobre el pronóstico. Habiendo establecido la causa de VEXAS, ahora tenemos una oportunidad real de transformar la atención de estos pacientes. Sabemos que todavía hay muchos pacientes que tienen una afección similar a VEXAS, pero en los que desconocemos la causa”.
Los autores concluyeron que su estudio confirma las sustituciones somáticas de p.Met41 en UBA1 como una de las principales causas del síndrome VEXAS e identifica dos mutaciones nuevas que causan enfermedades. El estudio fue publicado el 9 de marzo de 2021 en la revista Blood Advances.
Enlace relacionado:
Universidad de Leeds
El síndrome de VEXAS causa fiebres inexplicables, erupciones cutáneas dolorosas y afecta la médula ósea, lo que resulta en una reducción del número de glóbulos rojos y blancos. La enfermedad afecta solo a los hombres porque es causada por mutaciones genéticas en el cromosoma X y los hombres son portadores de un solo cromosoma X. Las mutaciones no están presentes al nacer; por el contrario, se desarrollan durante la vida del paciente.
Un equipo multicéntrico dirigido por la Universidad de Leeds (Leeds, Reino Unido), examinó muestras de ADN para establecer la prevalencia de las mutaciones genéticas identificadas cuando se descubrió la enfermedad por primera vez en 2020. Examinaron una cohorte de 18 pacientes locales que coincidieron con los síntomas y encontraron mutaciones en 10 de ellos. Ocho tenían la variante conocida previamente asociada con la enfermedad, pero dos pacientes tenían variantes completamente diferentes. Esto identificó una nueva forma en que las mutaciones pueden causar VEXAS, lo que significa que es probable que sea mucho más común de lo que se pensaba actualmente. VEXAS significa Vacuolas, enzima E1, ligado al cromosoma X, autoinflamatorio, síndrome somático.
El equipo identificó 10 pacientes nuevos con mutaciones somáticas en UBA1, pero solo ocho tenían una alteración en p.Met41. Se identificó la presencia de una nueva variante, c.167C>T; p.Ser56Phe, en los linajes mieloides y no linfoides que condujo a una pérdida preferencial de la actividad catalítica del UBA1 citoplásmico. Se identificó una nueva variante adicional, c.118-1G> C en el sitio aceptor de empalme del exón 3, que conduce a un empalme alterado in vitro. Las biopsias de médula ósea de dos pacientes con una sustitución de Met41 y la nueva variante del sitio de empalme coincidieron con las características de VEXAS informadas anteriormente. La médula ósea del paciente con la variante p.Ser56Phe fue menos similar, probablemente promovida por un mecanismo de enfermedad distinto pero superpuesto.
Sinisa Savic, MRCP, FRCPath, PhD, inmunóloga clínica y autora principal del estudio, dijo: “He cuidado a varios pacientes con lo que ahora sabemos que es el síndrome VEXAS durante varios años. Su atención se ha visto complicada por el hecho de que no contábamos con un diagnóstico, lo que dificultaba mucho la elección de su tratamiento y aconsejarles sobre el pronóstico. Habiendo establecido la causa de VEXAS, ahora tenemos una oportunidad real de transformar la atención de estos pacientes. Sabemos que todavía hay muchos pacientes que tienen una afección similar a VEXAS, pero en los que desconocemos la causa”.
Los autores concluyeron que su estudio confirma las sustituciones somáticas de p.Met41 en UBA1 como una de las principales causas del síndrome VEXAS e identifica dos mutaciones nuevas que causan enfermedades. El estudio fue publicado el 9 de marzo de 2021 en la revista Blood Advances.
Enlace relacionado:
Universidad de Leeds
Últimas Diagnóstico Molecular noticias
- Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
- Prueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
- Sistema de RT-PCR en el punto de atención de 10 minutos detecta hasta 32 objetivos por muestra
- Células extraídas de orina podrían permitir detección más temprana de enfermedad renal
- Análisis de sangre identifica a personas con mayor riesgo de morir por insuficiencia cardíaca
- Análisis de sangre muestra precisión del 83 % para detectar cáncer colorrectal
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal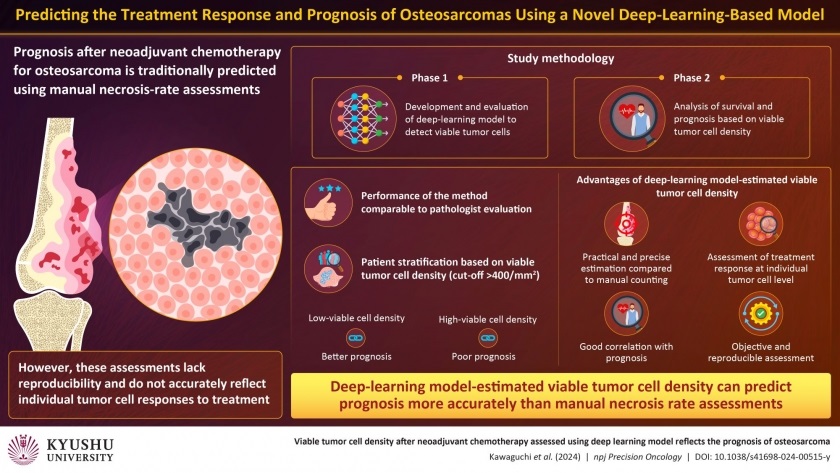
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)