Asocian infección de C. difficile con el bacterioma vinculado a los hongos
|
Por el equipo editorial de LabMedica en español Actualizado el 17 Sep 2019 |
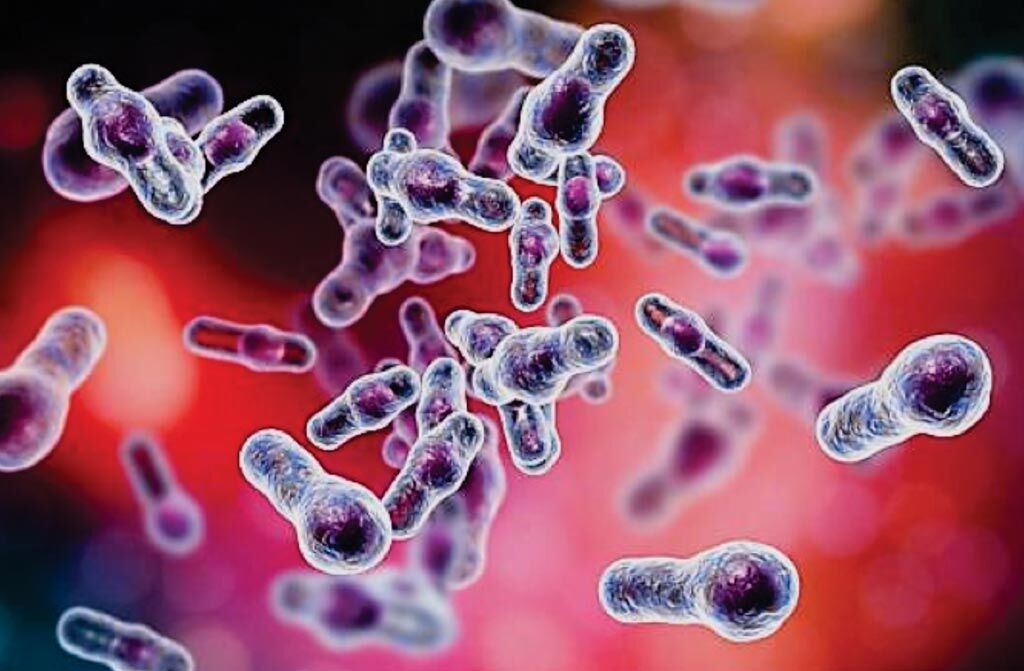
Imagen: Bacilos de Clostridioides difficile en forma de palillos de tambor tal como aparecen en la microscopía electrónica de barrido (Fotografía cortesía de Kateryna Kon, PhD).
La infección por Clostridioides difficile (ICD), la etiología más común de la diarrea infecciosa nosocomial, es causada por una disbiosis intestinal que casi siempre se atribuye a los antibióticos. Esto causa una de las infecciones adquiridas en el hospital más comunes en los Estados Unidos.
Cada vez hay más datos que muestran que distintas estructuras comunitarias bacterianas y fúngicas permiten diferenciar el estado disbiótico de la ICD de la diarrea asociada a antibióticos debido a otras causas. Los datos sugieren que las interacciones entre especies fúngicas y bacterianas juegan un papel importante en las infecciones nosocomiales.
Un equipo de científicos que colabora con la Universidad de Arizona (Tucson, AZ, EUA) recolectó heces diarreicas de 49 pacientes hospitalizados (18 de los cuales dieron positivo para ICD) bajo estrictos criterios de inclusión. La prueba de C. difficile se realizó usando una prueba de amplificación de ácido nucleico, disponible comercialmente, diseñada para detectar una secuencia altamente conservada dentro del gen tcdA. Se conservaron las muestras de heces positivas y negativas para C. difficile.
Los extractos de ADN fecal fueron analizadas con la reacción en cadena de la polimerasa (PCR) (Illumina, San Diego, CA, EUA) para los genes 16S rARN e ITS2, agrupados en proporciones equimolares, purificados en gel y secuenciados en el Illumina MiSeq (Bibliotecas 16S rARN) y plataformas NextSeq (bibliotecas ITS). Las secuencias bacterianas (gen 16S rARN) y fúngicas (ITS) se filtraron de calidad, se agruparon en unidades taxonómicas operativas (OTU) y se normalizaron utilizando las líneas de producción USEARCH y QIIME. El equipo utilizó un enfoque de secuenciación escalonada para identificar taxones de bacterias y hongos enriquecidos, utilizando la secuenciación de amplicon del gen 16S rARN y el espaciador transcrito interno (ITS), con metagenómica y metatranscriptómica coincidentes realizadas en un subconjunto de la población.
Los científicos informaron que distintas composiciones bacterianas y fúngicas permitían diferenciar a los pacientes positivos y negativos para la ICD, con la mayor diferenciación entre las cohortes observadas en función de la metatranscriptómica bacteriana. Los análisis de redes bipartitas demostraron que los taxones Aspergillus y Penicillium compartían una fuerte relación positiva en pacientes con ICD y juntos formaban relaciones negativas coexistentes con varios taxones bacterianos, incluidos Oscillospira, Comamonadaceae, Microbacteriaceae y Cytophagaceae. Los investigadores identificaron nuevas vías asociadas con infecciones por C. difficile. Esas vías apuntaban a otras especies bacterianas, incluida Escherichia coli, que pueden contribuir a la disbiosis o al desequilibrio entre las especies bacterianas en el intestino, asociadas con C. difficile.
David B. Stewart, MD, cirujano y primer autor del estudio, dijo: “El desarrollo de la infección por C. difficile aparentemente es influenciado tanto por patógenos bacterianos como por hongos particulares a esta enfermedad. Hasta ahora, los hongos han sido poco estudiados y subestimados en el microbioma intestinal”. El estudio fue publicado el 28 de agosto de 2019 en la revista mSphere.
Enlace relacionado:
Universidad de Arizona
Illumina
Cada vez hay más datos que muestran que distintas estructuras comunitarias bacterianas y fúngicas permiten diferenciar el estado disbiótico de la ICD de la diarrea asociada a antibióticos debido a otras causas. Los datos sugieren que las interacciones entre especies fúngicas y bacterianas juegan un papel importante en las infecciones nosocomiales.
Un equipo de científicos que colabora con la Universidad de Arizona (Tucson, AZ, EUA) recolectó heces diarreicas de 49 pacientes hospitalizados (18 de los cuales dieron positivo para ICD) bajo estrictos criterios de inclusión. La prueba de C. difficile se realizó usando una prueba de amplificación de ácido nucleico, disponible comercialmente, diseñada para detectar una secuencia altamente conservada dentro del gen tcdA. Se conservaron las muestras de heces positivas y negativas para C. difficile.
Los extractos de ADN fecal fueron analizadas con la reacción en cadena de la polimerasa (PCR) (Illumina, San Diego, CA, EUA) para los genes 16S rARN e ITS2, agrupados en proporciones equimolares, purificados en gel y secuenciados en el Illumina MiSeq (Bibliotecas 16S rARN) y plataformas NextSeq (bibliotecas ITS). Las secuencias bacterianas (gen 16S rARN) y fúngicas (ITS) se filtraron de calidad, se agruparon en unidades taxonómicas operativas (OTU) y se normalizaron utilizando las líneas de producción USEARCH y QIIME. El equipo utilizó un enfoque de secuenciación escalonada para identificar taxones de bacterias y hongos enriquecidos, utilizando la secuenciación de amplicon del gen 16S rARN y el espaciador transcrito interno (ITS), con metagenómica y metatranscriptómica coincidentes realizadas en un subconjunto de la población.
Los científicos informaron que distintas composiciones bacterianas y fúngicas permitían diferenciar a los pacientes positivos y negativos para la ICD, con la mayor diferenciación entre las cohortes observadas en función de la metatranscriptómica bacteriana. Los análisis de redes bipartitas demostraron que los taxones Aspergillus y Penicillium compartían una fuerte relación positiva en pacientes con ICD y juntos formaban relaciones negativas coexistentes con varios taxones bacterianos, incluidos Oscillospira, Comamonadaceae, Microbacteriaceae y Cytophagaceae. Los investigadores identificaron nuevas vías asociadas con infecciones por C. difficile. Esas vías apuntaban a otras especies bacterianas, incluida Escherichia coli, que pueden contribuir a la disbiosis o al desequilibrio entre las especies bacterianas en el intestino, asociadas con C. difficile.
David B. Stewart, MD, cirujano y primer autor del estudio, dijo: “El desarrollo de la infección por C. difficile aparentemente es influenciado tanto por patógenos bacterianos como por hongos particulares a esta enfermedad. Hasta ahora, los hongos han sido poco estudiados y subestimados en el microbioma intestinal”. El estudio fue publicado el 28 de agosto de 2019 en la revista mSphere.
Enlace relacionado:
Universidad de Arizona
Illumina
Últimas Diagnóstico Molecular noticias
- Prueba en orina detecta cáncer de cabeza y cuello
- Prueba de sangre detecta y monitorea cáncer pulmonar de células pequeñas agresivo
- Ensayo de aprendizaje automático basado en sangre detecta de forma no invasiva el cáncer de ovario
- Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
- Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
- Prueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Prueba en orina detecta cáncer de cabeza y cuello
El virus del papiloma humano (VPH) es bien conocido por su papel en la causa del cáncer de cuello uterino y también se identifica cada vez más como responsable de los cánceres... Más.jpg)
Prueba de sangre detecta y monitorea cáncer pulmonar de células pequeñas agresivo
El cáncer de pulmón de células pequeñas (CPCP) es un tipo de cáncer muy agresivo conocido por su capacidad de metastatizar. El comportamiento de los tumores se rige en... Más.jpeg)
Ensayo de aprendizaje automático basado en sangre detecta de forma no invasiva el cáncer de ovario
El cáncer de ovario es una de las causas más comunes de muerte por cáncer entre las mujeres y tiene una tasa de supervivencia a cinco años de alrededor del 50%.... Más
Ensayo de PCR simple diferencia con precisión entre los subtipos de cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas (CPCP), una neoplasia maligna neuroendocrina que progresa rápidamente, presenta bajas tasas de supervivencia. A pesar de su heterogeneidad molecular y clínica, el... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Herramienta de IA ajusta con precisión los medicamentos contra el cáncer con los pacientes utilizando información de cada célula tumoral
Las estrategias actuales para emparejar a los pacientes con cáncer con tratamientos específicos a menudo dependen de la secuenciación masiva de ADN y ARN tumoral, que proporciona un perfil promedio de... Más
Pruebas genéticas combinadas con la detección de fármacos personalizadas en muestras de tumores podrían revolucionar el tratamiento del cáncer
El tratamiento del cáncer generalmente se adhiere a un estándar de atención: regímenes establecidos y validados estadísticamente que son efectivos para la mayoría... Más
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... MásPatología
ver canal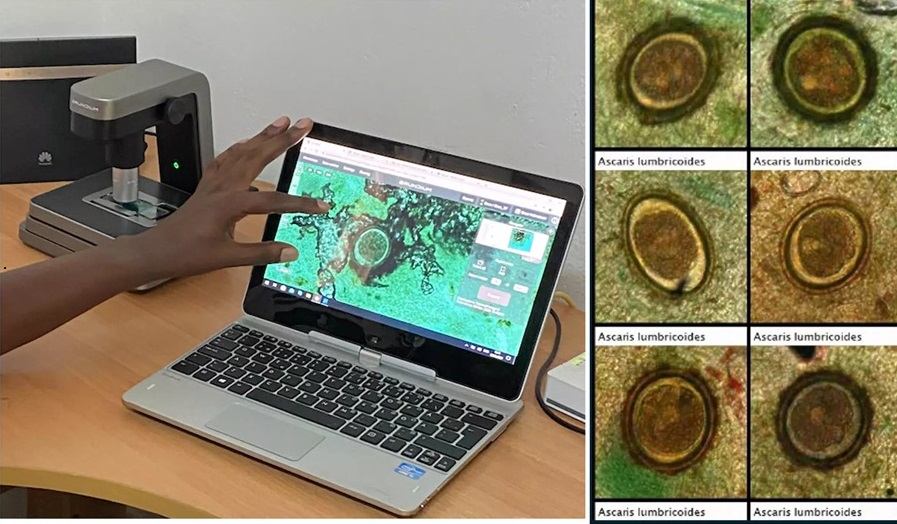
IA basada en imágenes se muestra prometedora para detección de parásitos en muestras de heces digitalizadas
Las infecciones por helmintos transmitidos por el suelo (STH), comúnmente conocidas como gusanos parásitos intestinales, se encuentran entre las enfermedades tropicales desatendidas más... Más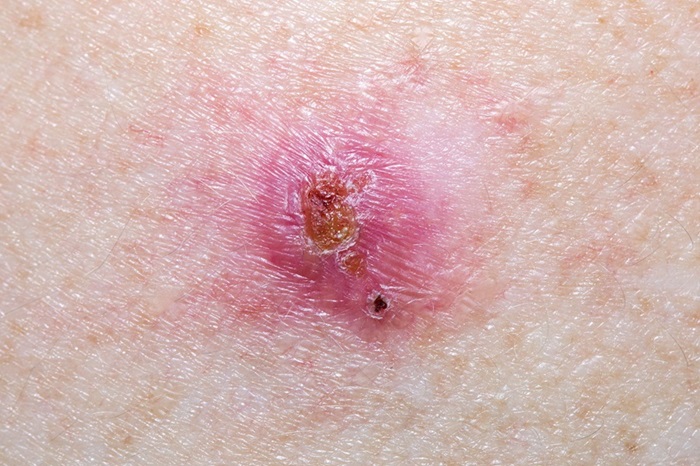
Algoritmos de inteligencia artificial potenciados por aprendizaje profundo mejoran la precisión en el diagnóstico de cáncer de piel.
Algoritmos de inteligencia artificial (IA) se utilizan cada vez más en diversos entornos clínicos, como la dermatología. Estos algoritmos se desarrollan entrenando una computadora... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más