El ADN circulante en el plasma puede identificar potencialmente los tumores incipientes
|
Por el equipo editorial de LabMedica en español Actualizado el 13 Mar 2019 |
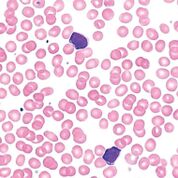
Imagen: Frotis de sangre de un paciente con linfocitosis monoclonal de células B. Los dos linfocitos atípicos están maduros con un borde pequeño de citoplasma basófilo y cromatina aglomerada o agrietada (Fotografía cortesía de Elizabeth Courville, MD).
El diagnóstico precoz del cáncer podría mejorar las tasas de supervivencia. Como el ADN tumoral circulante (ctADN) conlleva modificaciones específicas del cáncer, tiene un gran potencial como biomarcador no invasivo para la detección de tumores incipientes.
Un estudio reciente describe otro avance potencial mediante el análisis del ADN libre de células (cfADN) para identificar desequilibrios en las alteraciones del número de copias de todo el genoma (CNA) como un medio de detección de cáncer en individuos sanos. La identificación de tumores en las primeras etapas ofrecería la posibilidad de mejorar las tasas de supervivencia.
Un equipo de investigadores belgas y holandeses liderados por los Hospitales Universitarios de Lovaina (Lovaina, Bélgica), desarrolló un método único de creación de análisis genómicos para cfADN denominado The Genomic Desbalance Profiling from cfADN SEQuencing (GIPseq). El equipo recolectó muestras de cfADN de 1.002 pacientes ancianos belgas sin antecedentes de cáncer, y utilizaron el GIPseq para buscar aberraciones cromosómicas que sugirieran la presencia de una enfermedad maligna. Se llevaron a cabo análisis clínicos a los seis meses en los casos en que se encontraron aberraciones, y los investigadores catalogaron cualquier CNA presente en el cfADN para crear un “mapa” de las aberraciones encontradas en esta población en envejecimiento.
Los científicos informaron que en el 3% de los participantes se detectaron desequilibrios cromosómicos. Los análisis de seguimiento, incluidos los exámenes de resonancia magnética de todo el cuerpo, confirmaron la presencia de cinco tumores malignos hematológicos: un linfoma de Hodgkin (LH), estadío II; tres linfomas no Hodgkin (leucemia linfocítica crónica tipo, Rai I – Binet A); linfoma linfocítico pequeño tipo (SLL), estadío III; tejido linfoide asociado a la mucosa tipo, estadío I y un síndrome mielodisplásico con exceso de blastos, estadío II. Los CNA detectados en el cfADN fueron específicos de cada tumor. Además, se identificó un caso con linfocitosis monoclonal de células B, un precursor potencial de la malignidad de las células B. En 24 individuos adicionales, se identificaron CNA pero no se hizo un diagnóstico de cáncer. Para nueve de ellos, el análisis de cfADN aberrante se originó a partir de células de sangre periférica. Para otros 15, el origen de las aberraciones en el cfADN permanece indeterminado.
Los autores concluyeron que sus resultados ilustraban la efectividad de la prueba GIPseq en la detección de neoplasias malignas hematológicas incipientes y del mosaicismo clonal con importancia clínica desconocida en pacientes sanos. Demostraron que el cribado con cfADN detecta las CNA, que no solo se derivan de la sangre periférica, sino, incluso más, de otros tejidos. Dado que la relevancia clínica de los mosaicos clonales en otros tejidos sigue siendo desconocida, el seguimiento a largo plazo está justificado. El estudio fue publicado el 1 de enero de 2019 en la revista Annals of Oncology.
Enlace relacionado:
Hospitales Universitarios de Lovaina
Un estudio reciente describe otro avance potencial mediante el análisis del ADN libre de células (cfADN) para identificar desequilibrios en las alteraciones del número de copias de todo el genoma (CNA) como un medio de detección de cáncer en individuos sanos. La identificación de tumores en las primeras etapas ofrecería la posibilidad de mejorar las tasas de supervivencia.
Un equipo de investigadores belgas y holandeses liderados por los Hospitales Universitarios de Lovaina (Lovaina, Bélgica), desarrolló un método único de creación de análisis genómicos para cfADN denominado The Genomic Desbalance Profiling from cfADN SEQuencing (GIPseq). El equipo recolectó muestras de cfADN de 1.002 pacientes ancianos belgas sin antecedentes de cáncer, y utilizaron el GIPseq para buscar aberraciones cromosómicas que sugirieran la presencia de una enfermedad maligna. Se llevaron a cabo análisis clínicos a los seis meses en los casos en que se encontraron aberraciones, y los investigadores catalogaron cualquier CNA presente en el cfADN para crear un “mapa” de las aberraciones encontradas en esta población en envejecimiento.
Los científicos informaron que en el 3% de los participantes se detectaron desequilibrios cromosómicos. Los análisis de seguimiento, incluidos los exámenes de resonancia magnética de todo el cuerpo, confirmaron la presencia de cinco tumores malignos hematológicos: un linfoma de Hodgkin (LH), estadío II; tres linfomas no Hodgkin (leucemia linfocítica crónica tipo, Rai I – Binet A); linfoma linfocítico pequeño tipo (SLL), estadío III; tejido linfoide asociado a la mucosa tipo, estadío I y un síndrome mielodisplásico con exceso de blastos, estadío II. Los CNA detectados en el cfADN fueron específicos de cada tumor. Además, se identificó un caso con linfocitosis monoclonal de células B, un precursor potencial de la malignidad de las células B. En 24 individuos adicionales, se identificaron CNA pero no se hizo un diagnóstico de cáncer. Para nueve de ellos, el análisis de cfADN aberrante se originó a partir de células de sangre periférica. Para otros 15, el origen de las aberraciones en el cfADN permanece indeterminado.
Los autores concluyeron que sus resultados ilustraban la efectividad de la prueba GIPseq en la detección de neoplasias malignas hematológicas incipientes y del mosaicismo clonal con importancia clínica desconocida en pacientes sanos. Demostraron que el cribado con cfADN detecta las CNA, que no solo se derivan de la sangre periférica, sino, incluso más, de otros tejidos. Dado que la relevancia clínica de los mosaicos clonales en otros tejidos sigue siendo desconocida, el seguimiento a largo plazo está justificado. El estudio fue publicado el 1 de enero de 2019 en la revista Annals of Oncology.
Enlace relacionado:
Hospitales Universitarios de Lovaina
Últimas Diagnóstico Molecular noticias
- Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
- Prueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
- Sistema de RT-PCR en el punto de atención de 10 minutos detecta hasta 32 objetivos por muestra
- Células extraídas de orina podrían permitir detección más temprana de enfermedad renal
- Análisis de sangre identifica a personas con mayor riesgo de morir por insuficiencia cardíaca
- Análisis de sangre muestra precisión del 83 % para detectar cáncer colorrectal
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Enfoque revolucionario de análisis de células T permite detección temprana del cáncer
La biopsia líquida, un método para diagnosticar el cáncer mediante análisis de sangre de rutina, es una herramienta potencial importante para la detección temprana del... MásPrueba genética única podría acelerar el diagnóstico de trastornos raros del desarrollo
Las alteraciones en el ADN humano varían desde variaciones menores de un solo nucleótido hasta alteraciones sustanciales que implican la eliminación o duplicación de segmentos... Más
Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
QIAGEN (Venlo, Países Bajos) ha lanzado el analizador QIAstat-Dx 2.0, incluida la actualización del software 1.6. Esto representa un avance significativo con respecto al analizador QIAstat-Dx 1.... Más
Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
La pandemia de COVID-19 ha demostrado la necesidad de que los profesionales de la salud tengan pruebas de diagnóstico disponibles lo más cerca posible del paciente, proporcionando resultados... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal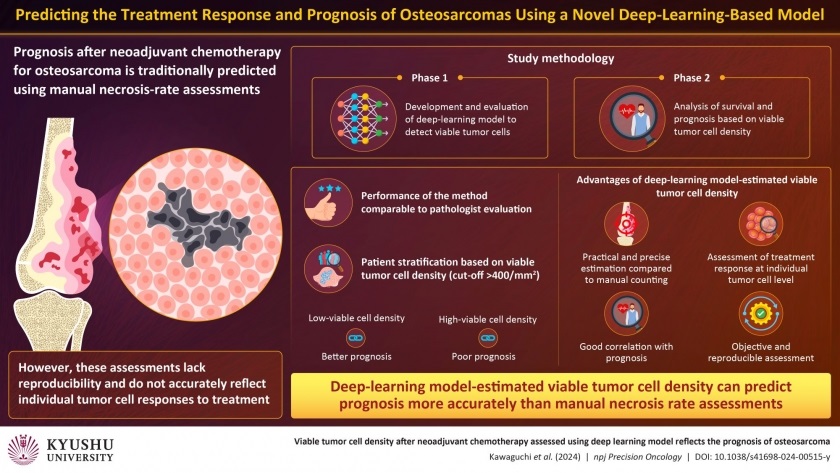
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)