Desarrollan dispositivo de mano para amplificación y detección de ADN
|
Por el equipo editorial de LabMedica en español Actualizado el 19 Feb 2018 |
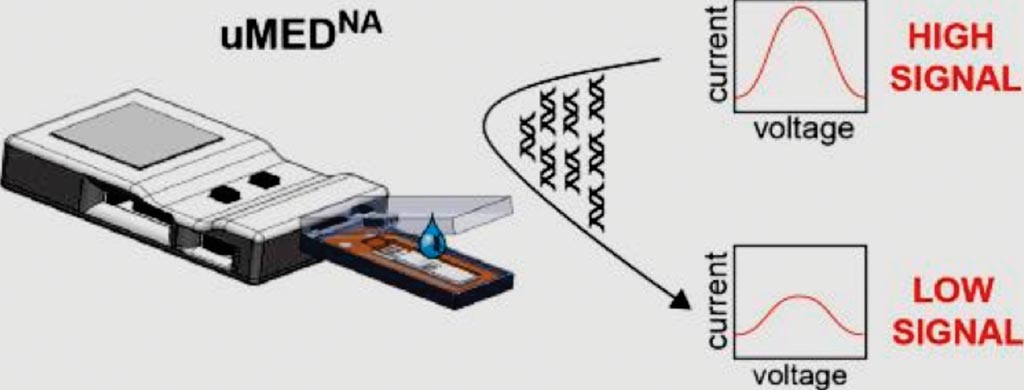
Imagen: Una representación del dispositivo portátil uMEDNA para la amplificación y detección del ADN (Fotografía cortesía de la Universidad de Harvard).
Se ha desarrollado un método que combina la detección electroquímica con la amplificación de la recombinasa polimerasa (RPA) en un dispositivo portátil para mejorar la detección de material genético de múltiples cepas de tuberculosis.
La reacción RPA usa enzimas llamadas recombinasas que forman complejos con cebadores de oligonucleótidos y emparejan los cebadores con secuencias homólogas en el ADN. Una proteína de unión al ADN monocatenario se une a la cadena de ADN desplazada y estabiliza el bucle resultante. El cebador luego inicia la amplificación del ADN mediante una polimerasa, pero solo si la secuencia de ADN diana está presente.
Científicos de la Universidad de Harvard (Boston, MA, EUA) y de Diagnósticos para Todos (Diagnostics for All) (Salem, MA, EUA) usaron tiras de papel descartables que integran tres electrodos de carbono serigrafiados y logran la termorregulación con una exactitud de temperatura de +/- 0,1ºC. Para detectar el ADN, el equipo primero prepara la tira de papel para el análisis que incluye la muestra de sangre y los cebadores, además de los electrodos integrados que contienen los reactivos para la RPA. Las tiras reactivas le permiten al equipo reducir el volumen de la reacción, reduciendo el costo de los reactivos y el tamaño de la muestra de sangre. Después de identificar una región de 213 pb común a tanto Mycobacterium tuberculosis como Mycobacterium smegmatis, el equipo diseñó cebadores apropiados para el ensayo de RPA con el fin de amplificar la secuencia específica. Realizado a 65ºC, el ensayo combinó la amplificación isotérmica con la lectura electroquímica de la reacción redox-activa del hexa-amina rutenio (III) (Ru (NH3)6]3+) como un mediador electroactivo para la detección electroquímica del ADN.
El equipo también realizó la reacción con niveles variables de concentraciones iniciales del ADN objetivo de M. smegmatis para demostrar la sensibilidad del análisis. Según el estudio, el límite de detección del ensayo es de 0,04 ng/μL, equivalente a 11 unidades formadoras de colonias (UFC)/mL de M. tuberculosis. Debido a que los ensayos RPA no necesitan tiempo adicional para la preparación de la muestra, el ensayo en el estudio requirió apenas de 20 minutos para identificar la bioseñal.
Los científicos enfatizaron que el ensayo RPA podría identificar potencialmente la señal más rápido dependiendo del tipo de cebador y la secuencia diana. Si bien el equipo utilizó M. smegmatis como una cepa sustituta para M. tuberculosis, el ensayo RPA de sobremesa que desarrollaron puede detectar hasta 19 especies de Mycobacterium. Además, el equipo también llevó a cabo experimentos utilizando muestras cargadas con ADN de M. tuberculosis que destaca que el método electroquímico también funciona con la cepa bacteriana específica.
Los datos recopilados por el dispositivo, llamado uMEDNA, se pueden transmitir conectándolo a la toma de auriculares de un teléfono celular. El dispositivo uMEDNA también se comunica con cualquier dispositivo con Bluetooth habilitado y se puede conectar a cualquier computadora, tableta o teléfono inteligente. Por el momento, los científicos han desarrollado un software para dispositivos Apple y actualmente trabajan en la adaptación del programa para dispositivos Android. Maria-Nefeli Tsaloglou, PhD, autora principal del estudio, dijo: “El dispositivo uMEDNA solo le costará al usuario final unos 30 dólares. La introducción de las tiras de papel para la detección de ADN también mantendrá el precio del ensayo relativamente bajo. Los analizadores electroquímicos en el laboratorio son voluminosos y caros, casi en el rango de 300.000 a un millón de dólares. En este estudio, demostramos que tanto el tamaño como la electrónica dentro del analizador pueden ser más baratos”. El estudio fue publicado en la edición de febrero de 2018 de la revista Analytical Biochemistry.
La reacción RPA usa enzimas llamadas recombinasas que forman complejos con cebadores de oligonucleótidos y emparejan los cebadores con secuencias homólogas en el ADN. Una proteína de unión al ADN monocatenario se une a la cadena de ADN desplazada y estabiliza el bucle resultante. El cebador luego inicia la amplificación del ADN mediante una polimerasa, pero solo si la secuencia de ADN diana está presente.
Científicos de la Universidad de Harvard (Boston, MA, EUA) y de Diagnósticos para Todos (Diagnostics for All) (Salem, MA, EUA) usaron tiras de papel descartables que integran tres electrodos de carbono serigrafiados y logran la termorregulación con una exactitud de temperatura de +/- 0,1ºC. Para detectar el ADN, el equipo primero prepara la tira de papel para el análisis que incluye la muestra de sangre y los cebadores, además de los electrodos integrados que contienen los reactivos para la RPA. Las tiras reactivas le permiten al equipo reducir el volumen de la reacción, reduciendo el costo de los reactivos y el tamaño de la muestra de sangre. Después de identificar una región de 213 pb común a tanto Mycobacterium tuberculosis como Mycobacterium smegmatis, el equipo diseñó cebadores apropiados para el ensayo de RPA con el fin de amplificar la secuencia específica. Realizado a 65ºC, el ensayo combinó la amplificación isotérmica con la lectura electroquímica de la reacción redox-activa del hexa-amina rutenio (III) (Ru (NH3)6]3+) como un mediador electroactivo para la detección electroquímica del ADN.
El equipo también realizó la reacción con niveles variables de concentraciones iniciales del ADN objetivo de M. smegmatis para demostrar la sensibilidad del análisis. Según el estudio, el límite de detección del ensayo es de 0,04 ng/μL, equivalente a 11 unidades formadoras de colonias (UFC)/mL de M. tuberculosis. Debido a que los ensayos RPA no necesitan tiempo adicional para la preparación de la muestra, el ensayo en el estudio requirió apenas de 20 minutos para identificar la bioseñal.
Los científicos enfatizaron que el ensayo RPA podría identificar potencialmente la señal más rápido dependiendo del tipo de cebador y la secuencia diana. Si bien el equipo utilizó M. smegmatis como una cepa sustituta para M. tuberculosis, el ensayo RPA de sobremesa que desarrollaron puede detectar hasta 19 especies de Mycobacterium. Además, el equipo también llevó a cabo experimentos utilizando muestras cargadas con ADN de M. tuberculosis que destaca que el método electroquímico también funciona con la cepa bacteriana específica.
Los datos recopilados por el dispositivo, llamado uMEDNA, se pueden transmitir conectándolo a la toma de auriculares de un teléfono celular. El dispositivo uMEDNA también se comunica con cualquier dispositivo con Bluetooth habilitado y se puede conectar a cualquier computadora, tableta o teléfono inteligente. Por el momento, los científicos han desarrollado un software para dispositivos Apple y actualmente trabajan en la adaptación del programa para dispositivos Android. Maria-Nefeli Tsaloglou, PhD, autora principal del estudio, dijo: “El dispositivo uMEDNA solo le costará al usuario final unos 30 dólares. La introducción de las tiras de papel para la detección de ADN también mantendrá el precio del ensayo relativamente bajo. Los analizadores electroquímicos en el laboratorio son voluminosos y caros, casi en el rango de 300.000 a un millón de dólares. En este estudio, demostramos que tanto el tamaño como la electrónica dentro del analizador pueden ser más baratos”. El estudio fue publicado en la edición de febrero de 2018 de la revista Analytical Biochemistry.
Últimas Microbiología noticias
- Análisis de sangre predice sepsis e insuficiencia orgánica en niños
- Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
- Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
- Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
- Nuevo análisis para tuberculosis podría ampliar acceso a pruebas en países de ingresos bajos y medios
- Prueba rápida diagnostica enfermedades tropicales en horas para tratamiento con antibióticos más rápido
- Pruebas moleculares rápidas permiten tratamiento antibiótico más rápido y específico para neumonía
- Plataforma rápida de PSA proporciona resultados terapéuticos específicos días antes que el estándar de atención actual
- Nuevo método de análisis detecta patógenos en sangre de forma más rápida y precisa al fundir ADN
- Prueba rápida de sepsis ofrece resultados dos días más rápidos
- Diagnóstico rápido portátil por PCR podría detectar gonorrea y susceptibilidad a antibióticos
- Prueba CRISPR diagnostica mpox más rápido que método de PCR de laboratorio
- Prueba de PCR multiplexada para detección de patógenos y resistencia a antibióticos ayuda a brindar un tratamiento rápido de ITU
- Nuevo algoritmo detecta e identifica nuevos organismos bacterianos
- Analizador de mesa promete detección de ITU en 1 hora e indicación de sensibilidad a antibióticos
- Prueba rápida junto a la cama podría proteger a recién nacidos de enfermedades potencialmente mortales
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
La capacidad de diagnosticar enfermedades de forma temprana puede optimizar significativamente la eficacia de los tratamientos clínicos y mejorar las tasas de supervivencia. Un enfoque prometedor... Más
Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
La malaria, una enfermedad grave que a menudo provoca la muerte, se transmite por una especie específica de mosquito que infecta a los humanos con un parásito. Otros modos de transmisión... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásPatología
ver canal
Prueba simple de biopsia de piel detecta el Parkinson y enfermedades neurodegenerativas relacionadas
La enfermedad de Parkinson y un grupo de trastornos neurodegenerativos relacionados conocidos como sinucleinopatías afectan a millones de personas en todo el mundo. Estas afecciones, incluida la... Más.jpg)
Herramienta bioinformática para identificar alteraciones cromosómicas en células tumorales puede mejorar diagnóstico del cáncer
La inestabilidad cromosómica es una característica común en los tumores sólidos y desempeña un papel crucial en el inicio, la progresión y la propagación... Más
Dispositivo del tamaño de una moneda aísla rápidamente plasma sanguíneo para diagnósticos clínicos más rápidos y precisos
La identificación de biomarcadores para diversos cánceres y enfermedades a menudo se basa en ADN, ARN y vesículas extracelulares libres de células. Tradicionalmente, separar... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)
.jpg)
.jpg)