Desarrollan prueba novedosa para detectar e identificar patógenos
|
Por el equipo editorial de LabMedica en español Actualizado el 05 Oct 2021 |
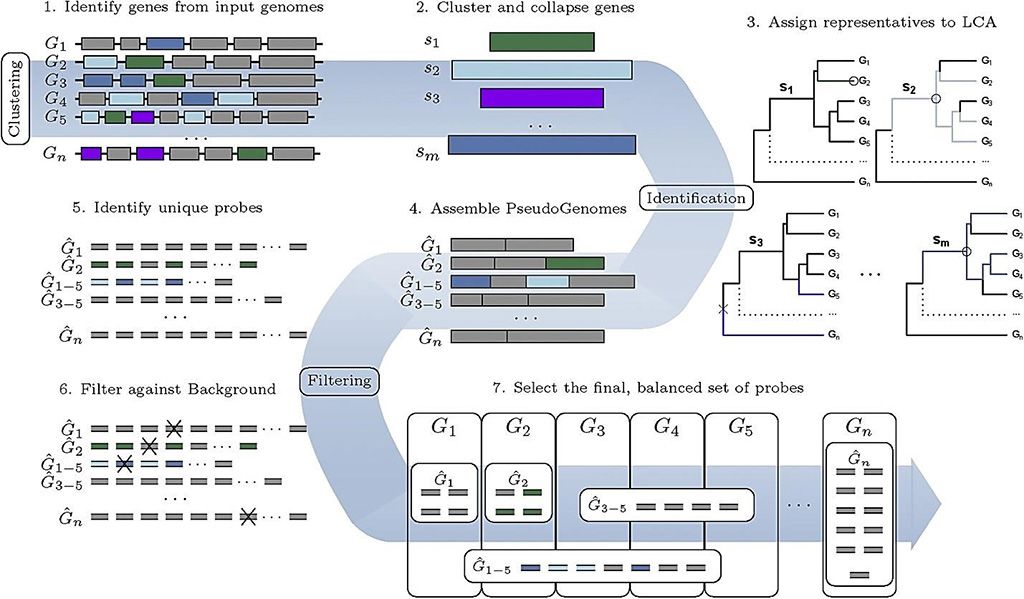
Imagen: El flujo de trabajo de la línea de productos en proyecto, HUBDesign: diseño de sonda para la captura simultánea y dirigida de diversos objetivos metagenómicos (Fotografía cortesía de la Universidad McMaster)
Los patógenos en entornos clínicos o de vida silvestre, como las muestras de sangre o saliva, por ejemplo, son particularmente difíciles de aislar, ya que pueden constituir fácilmente menos de una millonésima parte de una muestra, especialmente en las primeras etapas de una infección, cuando las concentraciones todavía son bajas y la detección es más crítica para los pacientes.
Una amplia gama de esfuerzos de estudios metagenómicos se ven obstaculizados por el mismo desafío: bajas concentraciones de objetivos de interés combinadas con cantidades abrumadoras de señal de fondo. Aunque se puede utilizar PCR o captura de ADN sin tratamiento previo cuando hay una pequeña cantidad de organismos de interés, los desafíos de diseño se vuelven insostenibles para una gran cantidad de objetivos.
Un equipo de científicos de la Universidad McMaster (Hamilton, ON, Canadá) y sus colegas desarrollaron una herramienta sofisticada nueva que podría ayudar a proporcionar una alerta temprana de virus raros y desconocidos en el medio ambiente e identificar patógenos bacterianos potencialmente mortales que causan sepsis. El nuevo algoritmo es una herramienta avanzada que puede ayudar a desarrollar sondas para capturar trazas de patógenos, tanto conocidos como desconocidos provenientes de una amplia variedad de situaciones, como la transmisión de infecciones de animal a humano como el SARS-CoV-2 o los reservorios de monitoreo en el medio ambiente por posibles patógenos emergentes.
El equipo probó con éxito las sondas en toda la familia de coronavirus, incluido el SARS-CoV-2. Las sondas proporcionan un atajo al apuntar, aislar e identificar, las secuencias de ADN, de manera específica y simultánea, que se comparten entre organismos relacionados, con mayor frecuencia debido a la historia evolutiva o la ascendencia. Para demostrar las capacidades y la eficacia de la herramienta, el Diseño de Cebos Jerárquicos Únicos (The Hierarchical Unique Bait Design, HUBDesign), diseñaron y probaron dos conjuntos de sondas: un conjunto de sondas de coronavirus capaz de detectar simultáneamente todos los coronavirus secuenciados y un conjunto de sondas dirigidas a patógenos bacterianos asociados con la sepsis.
La mayoría (62,5%) de las sondas tienen objetivos específicos para un virus. De las sondas que se dirigen a varios virus, la mayoría (78,1%) se dirigen a dos o tres. Los tres conjuntos restantes de sondas se dirigen a loci específicos de merbecovirus y embecovirus (ambos son subgéneros de Betacoronavirus) y loci comunes al género Deltacoronavirus. Tanto el SARS-CoV-2 como el HCoV-NL63 tienen sondas en dos niveles en la jerarquía.
El conjunto de sondas HUBDesign para patógenos de la sepsis contenía 26.870 sondas dirigidas a patógenos bacterianos, que cubren el 2,09% de todos los nucleótidos en el conjunto de datos de entrada a una profundidad media de cobertura de 3,64x. Los investigadores demostraron la efectividad de las sondas para capturar la increíble variedad de patógenos asociados con la sepsis, una condición potencialmente mortal y de rápido desarrollo que ocurre cuando el cuerpo reacciona de forma exagerada a una infección que generalmente comienza en los pulmones, el tracto urinario, la piel o el tracto gastrointestinal.
Hendrik Poinar, PhD, profesor de Genética Evolutiva Molecular y autor principal del estudio, dijo: “Actualmente necesitamos formas más rápidas, económicas y concisas de detectar patógenos en muestras humanas y ambientales que democraticen la caza y esta línea de productos en proyecto hace exactamente eso”. El estudio fue publicado el 15 de septiembre de 2021 en la revista Cell Reports Methods.
Enlace relacionado:
Universidad McMaster
Una amplia gama de esfuerzos de estudios metagenómicos se ven obstaculizados por el mismo desafío: bajas concentraciones de objetivos de interés combinadas con cantidades abrumadoras de señal de fondo. Aunque se puede utilizar PCR o captura de ADN sin tratamiento previo cuando hay una pequeña cantidad de organismos de interés, los desafíos de diseño se vuelven insostenibles para una gran cantidad de objetivos.
Un equipo de científicos de la Universidad McMaster (Hamilton, ON, Canadá) y sus colegas desarrollaron una herramienta sofisticada nueva que podría ayudar a proporcionar una alerta temprana de virus raros y desconocidos en el medio ambiente e identificar patógenos bacterianos potencialmente mortales que causan sepsis. El nuevo algoritmo es una herramienta avanzada que puede ayudar a desarrollar sondas para capturar trazas de patógenos, tanto conocidos como desconocidos provenientes de una amplia variedad de situaciones, como la transmisión de infecciones de animal a humano como el SARS-CoV-2 o los reservorios de monitoreo en el medio ambiente por posibles patógenos emergentes.
El equipo probó con éxito las sondas en toda la familia de coronavirus, incluido el SARS-CoV-2. Las sondas proporcionan un atajo al apuntar, aislar e identificar, las secuencias de ADN, de manera específica y simultánea, que se comparten entre organismos relacionados, con mayor frecuencia debido a la historia evolutiva o la ascendencia. Para demostrar las capacidades y la eficacia de la herramienta, el Diseño de Cebos Jerárquicos Únicos (The Hierarchical Unique Bait Design, HUBDesign), diseñaron y probaron dos conjuntos de sondas: un conjunto de sondas de coronavirus capaz de detectar simultáneamente todos los coronavirus secuenciados y un conjunto de sondas dirigidas a patógenos bacterianos asociados con la sepsis.
La mayoría (62,5%) de las sondas tienen objetivos específicos para un virus. De las sondas que se dirigen a varios virus, la mayoría (78,1%) se dirigen a dos o tres. Los tres conjuntos restantes de sondas se dirigen a loci específicos de merbecovirus y embecovirus (ambos son subgéneros de Betacoronavirus) y loci comunes al género Deltacoronavirus. Tanto el SARS-CoV-2 como el HCoV-NL63 tienen sondas en dos niveles en la jerarquía.
El conjunto de sondas HUBDesign para patógenos de la sepsis contenía 26.870 sondas dirigidas a patógenos bacterianos, que cubren el 2,09% de todos los nucleótidos en el conjunto de datos de entrada a una profundidad media de cobertura de 3,64x. Los investigadores demostraron la efectividad de las sondas para capturar la increíble variedad de patógenos asociados con la sepsis, una condición potencialmente mortal y de rápido desarrollo que ocurre cuando el cuerpo reacciona de forma exagerada a una infección que generalmente comienza en los pulmones, el tracto urinario, la piel o el tracto gastrointestinal.
Hendrik Poinar, PhD, profesor de Genética Evolutiva Molecular y autor principal del estudio, dijo: “Actualmente necesitamos formas más rápidas, económicas y concisas de detectar patógenos en muestras humanas y ambientales que democraticen la caza y esta línea de productos en proyecto hace exactamente eso”. El estudio fue publicado el 15 de septiembre de 2021 en la revista Cell Reports Methods.
Enlace relacionado:
Universidad McMaster
Últimas Tecnología noticias
- Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
- Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
- Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
- Primera tecnología de su tipo para detectar glucosa en saliva humana
- Dispositivo electroquímico identifica personas con mayor riesgo de osteoporosis mediante una sola gota de sangre
- Nueva prueba no invasiva detecta infección por malaria sin muestra de sangre
- Dispositivos de detección optofluídicos portátiles podrían realizar simultáneamente una variedad de pruebas médicas
- Solución de software para punto de atención ayuda a manejar escenarios de pruebas POC dispares en ubicaciones de prueba de pacientes
- Biosensor electrónico detecta biomarcadores en muestras de sangre completa sin agregar reactivos
- Prueba innovadora detecta marcadores biológicos relacionados con una variedad mayor de cánceres
- Kit de detección rápida POC determina la salud intestinal a partir de muestras de suero sanguíneo y heces
- Dispositivo convierte teléfono inteligente en microscopio de fluorescencia por solo 50 dólares
- Lector de tubos portátil habilitado para Wi-Fi diseñado para una fácil portabilidad
- Novedosa plataforma de pruebas de diagnóstico asegura el tiempo de respuesta a situaciones de pandemia emergentes
- Transistor revolucionario podría permitir dispositivos portátiles para medir el sodio y el potasio en la sangre
- Sensor portátil de bajo costo detecta metales pesados en el sudor
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal
Innovador dispositivo de extracción de sangre supera obstáculos comunes relacionados con la flebotomía
La incomodidad asociada con las extracciones de sangre tradicionales genera un problema importante: aproximadamente el 30 % de las pruebas de diagnóstico prescritas por los médicos nunca... Más
Dispositivo POC intraoperatorio distingue entre quistes ováricos benignos y malignos en 15 minutos
Los quistes ováricos representan un problema de salud importante para las mujeres en todo el mundo, y hasta el 10 % experimenta esta afección en algún momento de sus vidas.... Más
Prueba simple de biopsia de piel detecta el Parkinson y enfermedades neurodegenerativas relacionadas
La enfermedad de Parkinson y un grupo de trastornos neurodegenerativos relacionados conocidos como sinucleinopatías afectan a millones de personas en todo el mundo. Estas afecciones, incluida la... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)
.jpg)