Diseñan sensor olfativo portátil para diagnóstico de bacterias
|
Por el equipo editorial de LabMedica en español Actualizado el 06 Feb 2018 |
Image
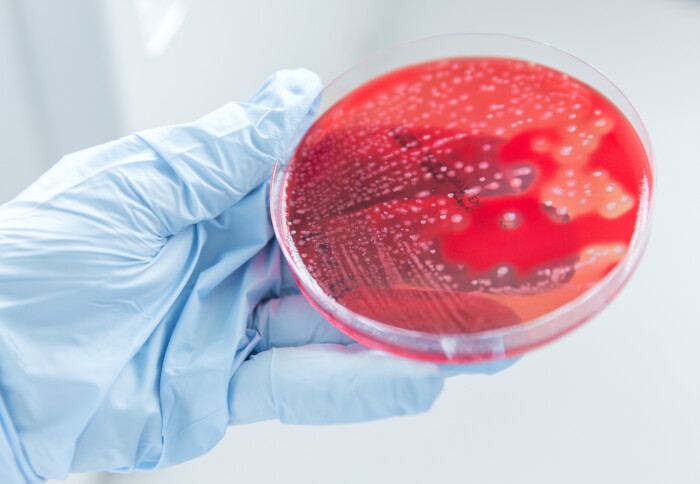
Se diseñó una nariz electrónica portátil (eNose) para detectar e identificar rápidamente las bacterias más comunes que causan infecciones en los tejidos blandos.
El diagnóstico rápido de las infecciones de heridas se basa en coloraciones de las bacterias, cultivos y ensayos de reacción en cadena de la polimerasa, y los resultados están disponibles después de varias horas como mínimo, pero con mayor frecuencia hasta que pasan varios días de espera. Por lo tanto, el tratamiento con antibióticos a menudo se administra empíricamente sin un diagnóstico específico.
Para rectificar esta situación, un equipo de bioingenieros finlandeses desarrolló la eNose, un dispositivo capaz de producir un perfil olfativo para cada compuesto molecular en la superficie gaseosa creada por una infección bacteriana. El perfil fue analizado por una computadora programada para diferenciar entre los diferentes compuestos.
Los investigadores utilizaron el sistema eNose para un estudio de prueba de concepto destinado a diferenciar las bacterias más relevantes que causan infecciones de las heridas. El estudio utilizó un conjunto de cultivos bacterianos clínicos en placas de cultivo de sangre idénticas y estableció las líneas bacterianas desde la superficie gaseosa.
Los resultados revelaron que el sistema eNose era capaz de diferenciar tanto el Staphylococcus aureus sensible a meticilina (SASM) como el Staphylococcus aureus resistente a meticilina (SARM), el Streptococcus pyogenes, la Escherichia coli, la Pseudomonas aeruginosa y el Clostridium perfringens con una exactitud del 78%, en cuestión de minutos, sin necesidad de preparación previa de la muestra. Lo que es más importante, el sistema fue capaz de diferenciar el SARM del SASM con una sensibilidad del 83%, una especificidad del 100% y una exactitud global del 91%.
“Nuestro objetivo era crear un método para el diagnóstico rápido de las infecciones en los tejidos blandos. Si tuviéramos un método de este tipo, el tratamiento podría iniciarse de manera oportuna y orientarse directamente al patógeno relevante. Esto reduciría la necesidad de tratamientos empíricos y acortaría los retrasos diagnósticos”, dijo el primer autor, el Dr. Taavi Saviauk, investigador de la facultad de medicina y ciencias de la vida de la Universidad de Tampere (Finlandia; www.uta.fi). “El dispositivo portátil eNose que utilizamos no requiere condiciones de laboratorio o capacitación especial, por lo que es adecuado para uso en los pacientes ambulatorios. Los resultados de este estudio son un paso significativo hacia nuestro objetivo”.
El estudio eNose se publicó en la edición de enero de 2018 de la revista European Surgical Research.
El diagnóstico rápido de las infecciones de heridas se basa en coloraciones de las bacterias, cultivos y ensayos de reacción en cadena de la polimerasa, y los resultados están disponibles después de varias horas como mínimo, pero con mayor frecuencia hasta que pasan varios días de espera. Por lo tanto, el tratamiento con antibióticos a menudo se administra empíricamente sin un diagnóstico específico.
Para rectificar esta situación, un equipo de bioingenieros finlandeses desarrolló la eNose, un dispositivo capaz de producir un perfil olfativo para cada compuesto molecular en la superficie gaseosa creada por una infección bacteriana. El perfil fue analizado por una computadora programada para diferenciar entre los diferentes compuestos.
Los investigadores utilizaron el sistema eNose para un estudio de prueba de concepto destinado a diferenciar las bacterias más relevantes que causan infecciones de las heridas. El estudio utilizó un conjunto de cultivos bacterianos clínicos en placas de cultivo de sangre idénticas y estableció las líneas bacterianas desde la superficie gaseosa.
Los resultados revelaron que el sistema eNose era capaz de diferenciar tanto el Staphylococcus aureus sensible a meticilina (SASM) como el Staphylococcus aureus resistente a meticilina (SARM), el Streptococcus pyogenes, la Escherichia coli, la Pseudomonas aeruginosa y el Clostridium perfringens con una exactitud del 78%, en cuestión de minutos, sin necesidad de preparación previa de la muestra. Lo que es más importante, el sistema fue capaz de diferenciar el SARM del SASM con una sensibilidad del 83%, una especificidad del 100% y una exactitud global del 91%.
“Nuestro objetivo era crear un método para el diagnóstico rápido de las infecciones en los tejidos blandos. Si tuviéramos un método de este tipo, el tratamiento podría iniciarse de manera oportuna y orientarse directamente al patógeno relevante. Esto reduciría la necesidad de tratamientos empíricos y acortaría los retrasos diagnósticos”, dijo el primer autor, el Dr. Taavi Saviauk, investigador de la facultad de medicina y ciencias de la vida de la Universidad de Tampere (Finlandia; www.uta.fi). “El dispositivo portátil eNose que utilizamos no requiere condiciones de laboratorio o capacitación especial, por lo que es adecuado para uso en los pacientes ambulatorios. Los resultados de este estudio son un paso significativo hacia nuestro objetivo”.
El estudio eNose se publicó en la edición de enero de 2018 de la revista European Surgical Research.
Últimas Diagnóstico Molecular noticias
- Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
- Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
- Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
- Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
- Prueba de biomarcadores líquidos detecta enfermedades neurodegenerativas antes de que aparezcan síntomas
- Nuevo método genómico ayuda a diagnosticar pacientes con enfermedad renal inexplicable
- Nuevo hidrogel inteligente allana el camino para nueva "piruleta" para diagnóstico de cáncer de boca
- Prueba de biomarcadores podría mejorar diagnóstico del cáncer de endometrio
- Prueba de ADN en heces de próxima generación supera a PIF en detección del cáncer colorrectal
- Innovador análisis de sangre de pTau217 es tan preciso como imágenes cerebrales o pruebas del LCR para diagnosticar Alzheimer
- Sistema de RT-PCR en el punto de atención de 10 minutos detecta hasta 32 objetivos por muestra
- Células extraídas de orina podrían permitir detección más temprana de enfermedad renal
- Análisis de sangre identifica a personas con mayor riesgo de morir por insuficiencia cardíaca
- Análisis de sangre muestra precisión del 83 % para detectar cáncer colorrectal
- Análisis de sangre podría predecir adultos jóvenes que podrían desarrollar enfermedades del envejecimiento
- Prueba de diagnóstico molecular predice con precisión resultados de terapia en pacientes con cáncer de mama
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal
Innovador dispositivo de extracción de sangre supera obstáculos comunes relacionados con la flebotomía
La incomodidad asociada con las extracciones de sangre tradicionales genera un problema importante: aproximadamente el 30 % de las pruebas de diagnóstico prescritas por los médicos nunca... Más
Dispositivo POC intraoperatorio distingue entre quistes ováricos benignos y malignos en 15 minutos
Los quistes ováricos representan un problema de salud importante para las mujeres en todo el mundo, y hasta el 10 % experimenta esta afección en algún momento de sus vidas.... Más
Prueba simple de biopsia de piel detecta el Parkinson y enfermedades neurodegenerativas relacionadas
La enfermedad de Parkinson y un grupo de trastornos neurodegenerativos relacionados conocidos como sinucleinopatías afectan a millones de personas en todo el mundo. Estas afecciones, incluida la... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)
.jpg)