Análisis rápido CRISPR/Cas para el diagnóstico de fiebres virales en ambientes de baja tecnología
|
Por el equipo editorial de LabMedica en español Actualizado el 07 Sep 2020 |
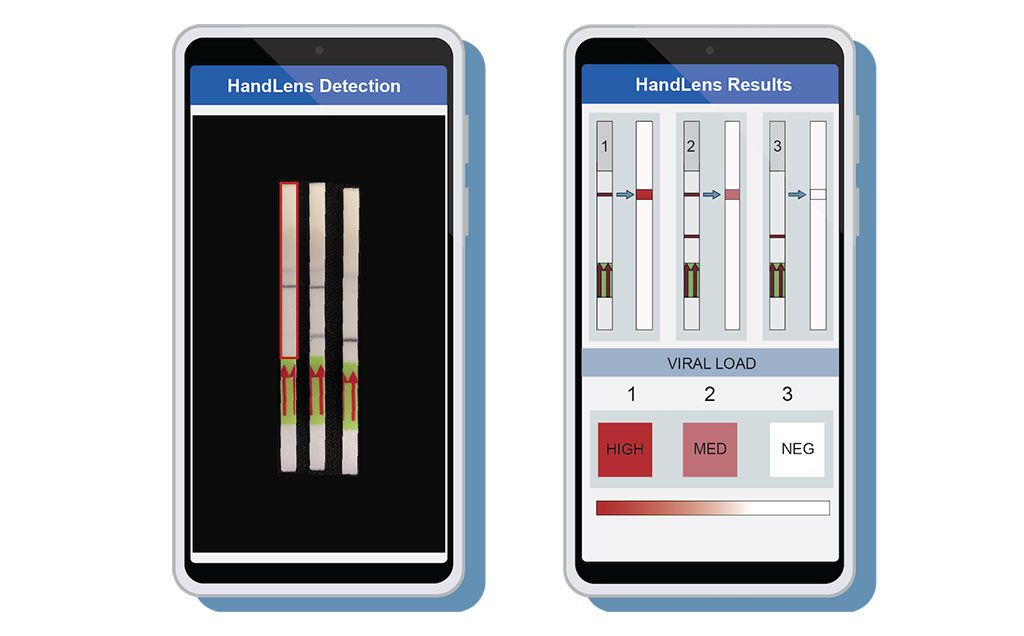
Imagen: Se diseñó una aplicación para teléfonos móviles llamada HandLens para leer e informar los resultados en las tiras de papel SHERLOCK (Fotografía cortesía de Anna Lachenauer, Facultad de Medicina de la Universidad de Stanford)
Las pruebas de diagnóstico rápido para los virus de la fiebre del Ébola y Lassa, basadas en el complejo CRISPR/Cas13a, dirigidas a la detección del ARN, se han probado con éxito en condiciones de campo en varios países africanos.
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
Últimas Tecnología noticias
- Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
- Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
- Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
- Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
- Primera tecnología de su tipo para detectar glucosa en saliva humana
- Dispositivo electroquímico identifica personas con mayor riesgo de osteoporosis mediante una sola gota de sangre
- Nueva prueba no invasiva detecta infección por malaria sin muestra de sangre
- Dispositivos de detección optofluídicos portátiles podrían realizar simultáneamente una variedad de pruebas médicas
- Solución de software para punto de atención ayuda a manejar escenarios de pruebas POC dispares en ubicaciones de prueba de pacientes
- Biosensor electrónico detecta biomarcadores en muestras de sangre completa sin agregar reactivos
- Prueba innovadora detecta marcadores biológicos relacionados con una variedad mayor de cánceres
- Kit de detección rápida POC determina la salud intestinal a partir de muestras de suero sanguíneo y heces
- Dispositivo convierte teléfono inteligente en microscopio de fluorescencia por solo 50 dólares
- Lector de tubos portátil habilitado para Wi-Fi diseñado para una fácil portabilidad
- Novedosa plataforma de pruebas de diagnóstico asegura el tiempo de respuesta a situaciones de pandemia emergentes
- Transistor revolucionario podría permitir dispositivos portátiles para medir el sodio y el potasio en la sangre
Canales
Química Clínica
ver canal
Espectrómetro de masas impreso en 3D para el punto de atención supera a los modelos de última generación
La espectrometría de masas es una técnica precisa para identificar los componentes químicos de una muestra y tiene un potencial significativo para monitorear estados de salud de enfermedades... Más.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Un diagnóstico de bajo costo en el punto de atención ampliará el acceso a pruebas de enfermedades de transmisión sexual
La gonorrea es la segunda infección bacteriana de transmisión sexual (ITS) más comúnmente reportada, con alrededor de 82 millones de casos en todo el mundo en 2020. La infección puede tener graves consecuencias... MásPrueba de orina de 18 genes para el cáncer de próstata ayuda a evitar biopsias innecesarias.
Uno de los principales desafíos en el tratamiento del cáncer de próstata es distinguir entre tumores de crecimiento lento, que tienen menos probabilidades de causar daño, y... MásHematología
ver canal
Primera prueba NAT 4 en 1 para el cribado de arbovirus podría reducir el riesgo de infecciones transmitidas por transfusiones
Los arbovirus representan una amenaza emergente para la salud mundial, exacerbada por el cambio climático y el aumento de la conectividad mundial que está facilitando su propagación a nuevas regiones.... Más
Instrumento de próxima generación detecta trastornos de la hemoglobina en recién nacidos
Las hemoglobinopatías, las enfermedades hereditarias más extendidas a nivel mundial, afectan a alrededor del 7 % de la población como portadores, y el 2,7 % de los recién nacidos nacen con estas enfermedades.... Más
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásInmunología
ver canal
Análisis de sangre para diagnóstico de rechazo celular después de trasplante de órganos podría reemplazar las biopsias quirúrgicas
Los órganos trasplantados enfrentan constantemente el riesgo de ser rechazados por el sistema inmunológico del receptor, que los diferencia de los órganos no propios mediante... Más
Herramienta de IA ajusta con precisión los medicamentos contra el cáncer con los pacientes utilizando información de cada célula tumoral
Las estrategias actuales para emparejar a los pacientes con cáncer con tratamientos específicos a menudo dependen de la secuenciación masiva de ADN y ARN tumoral, que proporciona un perfil promedio de... Más
Pruebas genéticas combinadas con la detección de fármacos personalizadas en muestras de tumores podrían revolucionar el tratamiento del cáncer
El tratamiento del cáncer generalmente se adhiere a un estándar de atención: regímenes establecidos y validados estadísticamente que son efectivos para la mayoría de los pacientes. Sin embargo, la variabilidad... Más
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... MásPatología
ver canal
IA basada en imágenes se muestra prometedora para detección de parásitos en muestras de heces digitalizadas
Las infecciones por helmintos transmitidos por el suelo (STH), comúnmente conocidas como gusanos parásitos intestinales, se encuentran entre las enfermedades tropicales desatendidas más... Más
Algoritmos de inteligencia artificial potenciados por aprendizaje profundo mejoran la precisión en el diagnóstico de cáncer de piel.
Algoritmos de inteligencia artificial (IA) se utilizan cada vez más en diversos entornos clínicos, como la dermatología. Estos algoritmos se desarrollan entrenando una computadora... MásTecnología
ver canal
Nuevo sistema de diagnóstico de laboratorio en un chip iguala la precisión de las pruebas de PCR
Si bien las pruebas de PCR son el estándar de oro en cuanto a precisión para las pruebas de virología, tienen limitaciones como la complejidad, la necesidad de operadores de laboratorio capacitados y tiempos... Más
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)