Secuenciación en células individuales revela diversidad clonal entre los pacientes con LMA
|
Por el equipo editorial de LabMedica en español Actualizado el 03 Nov 2020 |

Imagen: El sistema de secuenciación NovaSeq 6000 (Fotografía cortesía de Illumina).
Un cuerpo creciente de evidencia respalda el papel de la diversidad clonal en la resistencia terapéutica, la recurrencia y los malos resultados en el cáncer. La diversidad clonal también refleja la historia de la acumulación de mutaciones somáticas dentro de un tumor.
La capacidad de inferir heterogeneidad clonal y filogenia tumoral a partir de datos de secuenciación masiva es inherentemente limitada, porque las técnicas de secuenciación masiva no pueden inferir de manera confiable ocurrencias simultáneas de mutaciones y, por lo tanto, a menudo fallan en la reconstrucción exacta de la subestructura clonal. La secuenciación de ADN de una sola célula (scADN-seq) puede abordar algunos de estos desafíos.
Un gran equipo de científicos del Centro de Cáncer MD Anderson de la Universidad de Texas (Houston, TX, EUA), analizó 154 muestras (140 células mononucleares de médula ósea (BMMC) y 14 células mononucleares de sangre periférica) de 123 pacientes con leucemia mieloide aguda (LMA) que tenían al menos una mutación somática cubierta por el panel dirigido para scADN-seq. De los 123 pacientes, 108 pacientes fueron analizados antes del tratamiento (N = 98) o en el punto de tiempo de recaída/refractaria (N = 10). Entre 123 pacientes, 97 fueron analizados por scADN-seq, 23 fueron analizados por secuenciación simultánea de ADN de una sola célula y de las proteínas de superficie celular (scADN+protein-seq), y tres fueron analizados por scADN-seq y scADN+protein-seq.
La biblioteca agrupada se secuenció mediante una de las siguientes plataformas de secuenciación, MiSeq, HiSeq 4000 o NovaSeq 6000 (Illumina, San Diego, CA, EUA), con el procesamiento de pares de bases (pb) de 150 o 250 pares multiplexadas en el extremo. El equipo realizó una PCR digital por gotitas (ddPCR) utilizando el sistema digital QX200 Droplet (Bio-Rad Laboratories, Hércules, CA, EUA), para confirmar las variantes que fueron detectadas por scADN-seq, pero que no fueron detectadas por la secuenciación masiva. Se realizó un perfil simultáneo de la mutación del ADN y el inmunofenotipo de la superficie celular (scADN+protein-seq) utilizando el kit de panel de diseño personalizado y 10-15 anticuerpos oligoconjugados (Mission Bio, South San Francisco, CA, EUA). Los inmunofenotipos de las células de la médula ósea de pacientes con LMA se evaluaron mediante citometría de flujo de ocho colores en un instrumento FACSCanto II (BD Biosciences, San José, CA, EUA).
En total, los científicos secuenciaron más de 730.000 células para encontrar 543 mutaciones somáticas en 31 genes relacionados con el cáncer, el 98% de los cuales fueron validados ortogonalmente. Las mutaciones más comunes que detectaron fueron en NPM1, seguidas de las de DNMT3A y NRAS. Además, consiguieron que si bien se encontraron varias mutaciones que eran funcionalmente redundantes en los mismos pacientes, las alteraciones se encontraron a menudo en clones mutuamente excluyentes. Esto se extendió a las alteraciones que afectan a los genes de la vía de señalización del receptor tirosina quinasa (RTK)/Gas GTPasa (RAS)/MAP quinasa (MAPK), así como a las mutaciones IDH1 e IDH2 y a las mutaciones TET2 e IDH. Esto sugirió a los científicos que las células no necesitan dos mutaciones o que, cuando aparecen juntas, las mutaciones son tóxicas, lo que podría sugerir una posible vía de tratamiento para investigar.
Los investigadores también analizaron las correlaciones genotipo-fenotipo entre las células para encontrar, por ejemplo, que las células con mutaciones en NPM1 o IDH expresaban niveles más bajos de CD34 y HLA-DR, mientras que las células con una sola mutación en TP53 tenían un fenotipo CD34+ CD117+, pero que las mutaciones dobles en TP53 tenían un inmunofenotipo monocítico.
Koichi Takahashi, MD, PhD, autor principal del estudio, dijo: “Esta información también está disponible, de alguna manera, a partir de datos de secuenciación masiva longitudinal, pero creo que los datos de una sola célula proporcionan de manera única esta visión meticulosa de la dinámica clon por clon, lo que simplemente no es posible mediante la secuenciación masiva”. El estudio fue publicado el 21 de octubre de 2020 en la revista Nature Communications.
Enlace relacionado:
Centro de Cáncer MD Anderson de la Universidad de Texas
Bio-Rad Laboratories
Mission Bio
BD Biosciences
La capacidad de inferir heterogeneidad clonal y filogenia tumoral a partir de datos de secuenciación masiva es inherentemente limitada, porque las técnicas de secuenciación masiva no pueden inferir de manera confiable ocurrencias simultáneas de mutaciones y, por lo tanto, a menudo fallan en la reconstrucción exacta de la subestructura clonal. La secuenciación de ADN de una sola célula (scADN-seq) puede abordar algunos de estos desafíos.
Un gran equipo de científicos del Centro de Cáncer MD Anderson de la Universidad de Texas (Houston, TX, EUA), analizó 154 muestras (140 células mononucleares de médula ósea (BMMC) y 14 células mononucleares de sangre periférica) de 123 pacientes con leucemia mieloide aguda (LMA) que tenían al menos una mutación somática cubierta por el panel dirigido para scADN-seq. De los 123 pacientes, 108 pacientes fueron analizados antes del tratamiento (N = 98) o en el punto de tiempo de recaída/refractaria (N = 10). Entre 123 pacientes, 97 fueron analizados por scADN-seq, 23 fueron analizados por secuenciación simultánea de ADN de una sola célula y de las proteínas de superficie celular (scADN+protein-seq), y tres fueron analizados por scADN-seq y scADN+protein-seq.
La biblioteca agrupada se secuenció mediante una de las siguientes plataformas de secuenciación, MiSeq, HiSeq 4000 o NovaSeq 6000 (Illumina, San Diego, CA, EUA), con el procesamiento de pares de bases (pb) de 150 o 250 pares multiplexadas en el extremo. El equipo realizó una PCR digital por gotitas (ddPCR) utilizando el sistema digital QX200 Droplet (Bio-Rad Laboratories, Hércules, CA, EUA), para confirmar las variantes que fueron detectadas por scADN-seq, pero que no fueron detectadas por la secuenciación masiva. Se realizó un perfil simultáneo de la mutación del ADN y el inmunofenotipo de la superficie celular (scADN+protein-seq) utilizando el kit de panel de diseño personalizado y 10-15 anticuerpos oligoconjugados (Mission Bio, South San Francisco, CA, EUA). Los inmunofenotipos de las células de la médula ósea de pacientes con LMA se evaluaron mediante citometría de flujo de ocho colores en un instrumento FACSCanto II (BD Biosciences, San José, CA, EUA).
En total, los científicos secuenciaron más de 730.000 células para encontrar 543 mutaciones somáticas en 31 genes relacionados con el cáncer, el 98% de los cuales fueron validados ortogonalmente. Las mutaciones más comunes que detectaron fueron en NPM1, seguidas de las de DNMT3A y NRAS. Además, consiguieron que si bien se encontraron varias mutaciones que eran funcionalmente redundantes en los mismos pacientes, las alteraciones se encontraron a menudo en clones mutuamente excluyentes. Esto se extendió a las alteraciones que afectan a los genes de la vía de señalización del receptor tirosina quinasa (RTK)/Gas GTPasa (RAS)/MAP quinasa (MAPK), así como a las mutaciones IDH1 e IDH2 y a las mutaciones TET2 e IDH. Esto sugirió a los científicos que las células no necesitan dos mutaciones o que, cuando aparecen juntas, las mutaciones son tóxicas, lo que podría sugerir una posible vía de tratamiento para investigar.
Los investigadores también analizaron las correlaciones genotipo-fenotipo entre las células para encontrar, por ejemplo, que las células con mutaciones en NPM1 o IDH expresaban niveles más bajos de CD34 y HLA-DR, mientras que las células con una sola mutación en TP53 tenían un fenotipo CD34+ CD117+, pero que las mutaciones dobles en TP53 tenían un inmunofenotipo monocítico.
Koichi Takahashi, MD, PhD, autor principal del estudio, dijo: “Esta información también está disponible, de alguna manera, a partir de datos de secuenciación masiva longitudinal, pero creo que los datos de una sola célula proporcionan de manera única esta visión meticulosa de la dinámica clon por clon, lo que simplemente no es posible mediante la secuenciación masiva”. El estudio fue publicado el 21 de octubre de 2020 en la revista Nature Communications.
Enlace relacionado:
Centro de Cáncer MD Anderson de la Universidad de Texas
Bio-Rad Laboratories
Mission Bio
BD Biosciences
Últimas Hematología noticias
- Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
- Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
- Rastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
- Analizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
- Plataforma de hematología automatizada ofrece desempeño analítico de alto rendimiento
- Nueva herramienta analiza plaquetas sanguíneas de forma más rápida, sencilla y precisa
- Primer analizador de hematología de resultados rápidos informa medidas de infección y gravedad en el POC
- Prueba de diagnóstico de riesgo de hemorragia reduce complicaciones prevenibles en hospitales
- Verdadero analizador de hematología POC con muestreo capilar directo mejora facilidad de uso y rendimiento de pruebas
- Analizador de hemograma completo para el punto de atención con muestreo capilar directo mejora facilidad de uso y rendimiento de pruebas
- Examen de sangre podría predecir resultados en el departamento de emergencias y admisiones hospitalarias
- Nueva tecnología diagnostica inmunotrombosis mediante análisis de gases de aliento
- Sistema de hematología avanzado permite a laboratorios procesar hasta 119 resultados de hemogramas por hora
- Método único basado en IA automatiza análisis clínico de datos sanguíneos
- Herramienta portátil puede diagnosticar y monitorear enfermedad de células falciformes
- Analizadores de hematología de próxima generación eliminan obstáculos del flujo de trabajo y alcanzan un rendimiento rápido
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal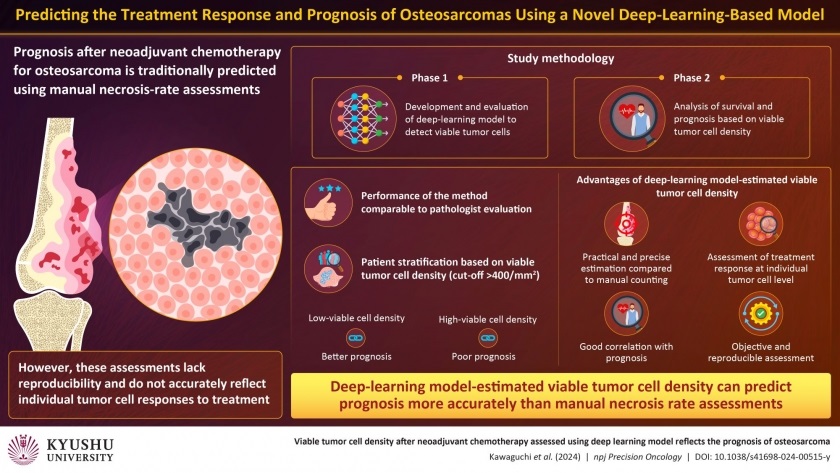
Inteligencia artificial detecta células tumorales viables para pronósticos precisos de cáncer de hueso después de quimioterapia
El osteosarcoma, el tumor óseo maligno más común, ha mostrado tasas de supervivencia mejoradas con cirugía y quimioterapia para casos localizados. Sin embargo, el pronóstico... Más
Nueva técnica identifica células cancerosas individuales en sangre para tratamientos específicos
La comunidad médica mundial reconoce cada vez más que la biopsia líquida es un enfoque transformador para mejorar la atención al paciente con cáncer. Este innovador método de diagnóstico implica detectar... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más












.jpg)
.jpg)