Se evalúa un panel respiratorio para la detección de las infecciones agudas del tracto respiratorio
|
Por el equipo editorial de LabMedica en español Actualizado el 14 Nov 2018 |

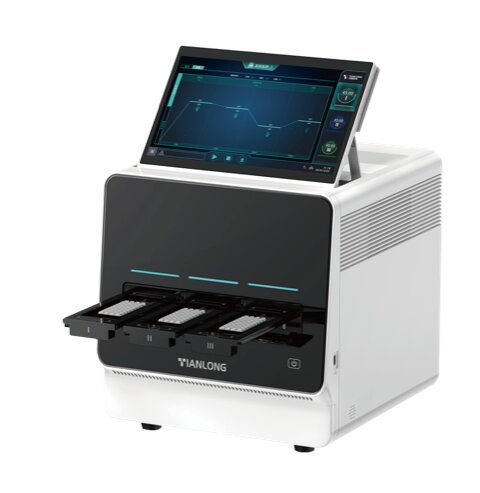
Imagen: El panel Respiratorio Allplex para la detección e identificación de 26 patógenos mediante RT-PCR en tiempo real en un solo paso (Fotografía cortesía de Seegene).
Las infecciones del tracto respiratorio superior (ITRS) son enfermedades causadas por una infección aguda que afecta al tracto respiratorio superior, incluidos la nariz, los senos nasales, la faringe o la laringe. Esto comúnmente incluye obstrucción nasal, dolor de garganta, amigdalitis, faringitis, laringitis, sinusitis, otitis media y el resfriado común.
La mayoría de las infecciones son de naturaleza viral y en otros casos la causa es bacteriana. Los virus no causan daño a las células del tracto respiratorio superior, sino que causan cambios en las uniones estrechas de las células epiteliales. Esto permite que el virus acceda a los tejidos debajo de las células epiteliales e inicie las respuestas inmunes innatas y adaptativas.
Los científicos del Hospital Universitario de Gante (Gante, Bélgica) y sus colegas, utilizaron una colección de muestras de control de calidad (QCMD) y de muestras clínicas analizadas previamente con métodos de rutina validados. Se analizó una colección de 111 muestras, 43 muestras de QCMD, 13 fluidos de lavado broncoalveolar y 55 aspirados/hisopos nasofaríngeos, con los Ensayos de Paneles Respiratorios Allplex (Seegene, Seúl, Corea).
Las muestras clínicas se analizaron previamente usando el ensayo qPCR de Patógenos Respiratorios FTD 21 (Fast Track Diagnostics, Sliema, Malta), una reacción en cadena de la polimerasa multiplex casera (PCR) para Bordetella o el Panel BioGX Sample-listo para neumonía atípica (Becton Dickinson, Franklin Lakes, NJ, EUA). Las muestras se almacenaron a -80°C antes del análisis con el panel Seegene Allplex, los ácidos nucleicos se extrajeron automáticamente con el kit NucliSENS Easymag (bioMérieux, Marcy-l'Étoile, Francia).
Los investigadores informaron que el ensayo Seegene Allplex identificó correctamente 41/43 muestras de QCMD (95,4%); dos muestras positivas para virus sincitial respiratorio (VSR) y metaneumovirus humano, respectivamente, solo se pudieron identificar correctamente después de repetir la prueba. En las 56 muestras clínicas, en total, se identificaron 97 patógenos: 65 patógenos (67,0%) se detectaron por métodos de rutina y ocho mediante la prueba Seegene, 24 patógenos (24,7%) solo por métodos de rutina y ocho patógenos (8,2%) solo por el panel Seegene. La mayoría de los resultados discordantes se detectaron en muestras con baja carga de patógenos (22/32, 68,8%) y en muestras que contienen patógenos múltiples (25/32, 78,1%). Se observó una concordancia total entre los métodos para influenza, VSR, adenovirus, Bordetella (para) pertussis y Chlamydia pneumoniae. Se observó discordancia para el metaneumovirus humano, el coronavirus OC43, el bocavirus y el virus de parainfluenza, principalmente el tipo 4.
Los autores concluyeron que, en general, el ensayo Seegene Allplex tuvo un buen desempeño para la detección rutinaria de objetivos respiratorios importantes. Se observó una concordancia aceptable entre la prueba Seegene y los otros ensayos de rutina. El estudio fue publicado el 11 de octubre de 2018 en la revista Acta Clinica Belgica.
Enlace relacionado:
Hospital Universitario de Gante
Seegene
Fast Track Diagnostics
Becton Dickinson
bioMérieux
La mayoría de las infecciones son de naturaleza viral y en otros casos la causa es bacteriana. Los virus no causan daño a las células del tracto respiratorio superior, sino que causan cambios en las uniones estrechas de las células epiteliales. Esto permite que el virus acceda a los tejidos debajo de las células epiteliales e inicie las respuestas inmunes innatas y adaptativas.
Los científicos del Hospital Universitario de Gante (Gante, Bélgica) y sus colegas, utilizaron una colección de muestras de control de calidad (QCMD) y de muestras clínicas analizadas previamente con métodos de rutina validados. Se analizó una colección de 111 muestras, 43 muestras de QCMD, 13 fluidos de lavado broncoalveolar y 55 aspirados/hisopos nasofaríngeos, con los Ensayos de Paneles Respiratorios Allplex (Seegene, Seúl, Corea).
Las muestras clínicas se analizaron previamente usando el ensayo qPCR de Patógenos Respiratorios FTD 21 (Fast Track Diagnostics, Sliema, Malta), una reacción en cadena de la polimerasa multiplex casera (PCR) para Bordetella o el Panel BioGX Sample-listo para neumonía atípica (Becton Dickinson, Franklin Lakes, NJ, EUA). Las muestras se almacenaron a -80°C antes del análisis con el panel Seegene Allplex, los ácidos nucleicos se extrajeron automáticamente con el kit NucliSENS Easymag (bioMérieux, Marcy-l'Étoile, Francia).
Los investigadores informaron que el ensayo Seegene Allplex identificó correctamente 41/43 muestras de QCMD (95,4%); dos muestras positivas para virus sincitial respiratorio (VSR) y metaneumovirus humano, respectivamente, solo se pudieron identificar correctamente después de repetir la prueba. En las 56 muestras clínicas, en total, se identificaron 97 patógenos: 65 patógenos (67,0%) se detectaron por métodos de rutina y ocho mediante la prueba Seegene, 24 patógenos (24,7%) solo por métodos de rutina y ocho patógenos (8,2%) solo por el panel Seegene. La mayoría de los resultados discordantes se detectaron en muestras con baja carga de patógenos (22/32, 68,8%) y en muestras que contienen patógenos múltiples (25/32, 78,1%). Se observó una concordancia total entre los métodos para influenza, VSR, adenovirus, Bordetella (para) pertussis y Chlamydia pneumoniae. Se observó discordancia para el metaneumovirus humano, el coronavirus OC43, el bocavirus y el virus de parainfluenza, principalmente el tipo 4.
Los autores concluyeron que, en general, el ensayo Seegene Allplex tuvo un buen desempeño para la detección rutinaria de objetivos respiratorios importantes. Se observó una concordancia aceptable entre la prueba Seegene y los otros ensayos de rutina. El estudio fue publicado el 11 de octubre de 2018 en la revista Acta Clinica Belgica.
Enlace relacionado:
Hospital Universitario de Gante
Seegene
Fast Track Diagnostics
Becton Dickinson
bioMérieux
Últimas Tecnología noticias
- Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
- Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
- Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
- Primera tecnología de su tipo para detectar glucosa en saliva humana
- Dispositivo electroquímico identifica personas con mayor riesgo de osteoporosis mediante una sola gota de sangre
- Nueva prueba no invasiva detecta infección por malaria sin muestra de sangre
- Dispositivos de detección optofluídicos portátiles podrían realizar simultáneamente una variedad de pruebas médicas
- Solución de software para punto de atención ayuda a manejar escenarios de pruebas POC dispares en ubicaciones de prueba de pacientes
- Biosensor electrónico detecta biomarcadores en muestras de sangre completa sin agregar reactivos
- Prueba innovadora detecta marcadores biológicos relacionados con una variedad mayor de cánceres
- Kit de detección rápida POC determina la salud intestinal a partir de muestras de suero sanguíneo y heces
- Dispositivo convierte teléfono inteligente en microscopio de fluorescencia por solo 50 dólares
- Lector de tubos portátil habilitado para Wi-Fi diseñado para una fácil portabilidad
- Novedosa plataforma de pruebas de diagnóstico asegura el tiempo de respuesta a situaciones de pandemia emergentes
- Transistor revolucionario podría permitir dispositivos portátiles para medir el sodio y el potasio en la sangre
- Sensor portátil de bajo costo detecta metales pesados en el sudor
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
QIAGEN (Venlo, Países Bajos) ha lanzado el analizador QIAstat-Dx 2.0, incluida la actualización del software 1.6. Esto representa un avance significativo con respecto al analizador QIAstat-Dx 1.... Más
Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
La pandemia de COVID-19 ha demostrado la necesidad de que los profesionales de la salud tengan pruebas de diagnóstico disponibles lo más cerca posible del paciente, proporcionando resultados... Más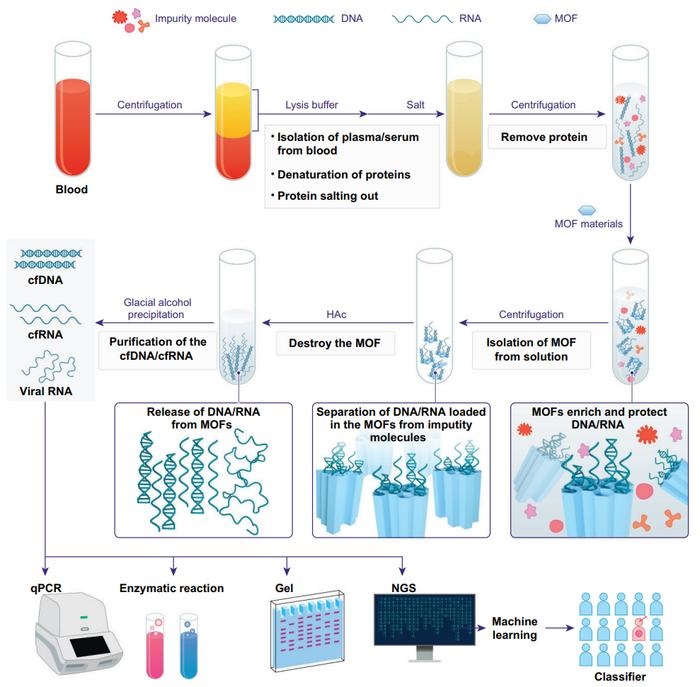
Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
La capacidad de diagnosticar enfermedades de forma temprana puede optimizar significativamente la eficacia de los tratamientos clínicos y mejorar las tasas de supervivencia. Un enfoque prometedor... Más
Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
La malaria, una enfermedad grave que a menudo provoca la muerte, se transmite por una especie específica de mosquito que infecta a los humanos con un parásito. Otros modos de transmisión... MásHematología
ver canal
Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
La neutropenia, una disminución de los neutrófilos (un tipo de glóbulo blanco crucial para combatir las infecciones), es un efecto secundario frecuente de ciertos tratamientos contra... Más
Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
Los trastornos de la hemoglobina se encuentran entre las enfermedades monogénicas más prevalentes a nivel mundial. Entre los diversos trastornos de la hemoglobina, la beta talasemia, un trastorno sanguíneo... MásRastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
Los glóbulos blancos, o leucocitos, son indicadores clave de la salud del sistema inmunológico de un individuo. Los recuentos altos o bajos de leucocitos pueden indicar la gravedad de una infección, indicar... MásAnalizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
Las variaciones en la concentración de células sanguíneas pueden ser indicativas de varias condiciones de salud, incluidas infecciones, enfermedades inflamatorias, trastornos sanguíneos... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásPatología
ver canal
Innovador dispositivo de extracción de sangre supera obstáculos comunes relacionados con la flebotomía
La incomodidad asociada con las extracciones de sangre tradicionales genera un problema importante: aproximadamente el 30 % de las pruebas de diagnóstico prescritas por los médicos nunca... Más
Dispositivo POC intraoperatorio distingue entre quistes ováricos benignos y malignos en 15 minutos
Los quistes ováricos representan un problema de salud importante para las mujeres en todo el mundo, y hasta el 10 % experimenta esta afección en algún momento de sus vidas.... Más
Prueba simple de biopsia de piel detecta el Parkinson y enfermedades neurodegenerativas relacionadas
La enfermedad de Parkinson y un grupo de trastornos neurodegenerativos relacionados conocidos como sinucleinopatías afectan a millones de personas en todo el mundo. Estas afecciones, incluida la... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más











.jpg)
.jpg)
.jpg)