Revelan genes del riesgo para mieloma múltiple
|
Por el equipo editorial de LabMedica en español Actualizado el 06 Mar 2018 |
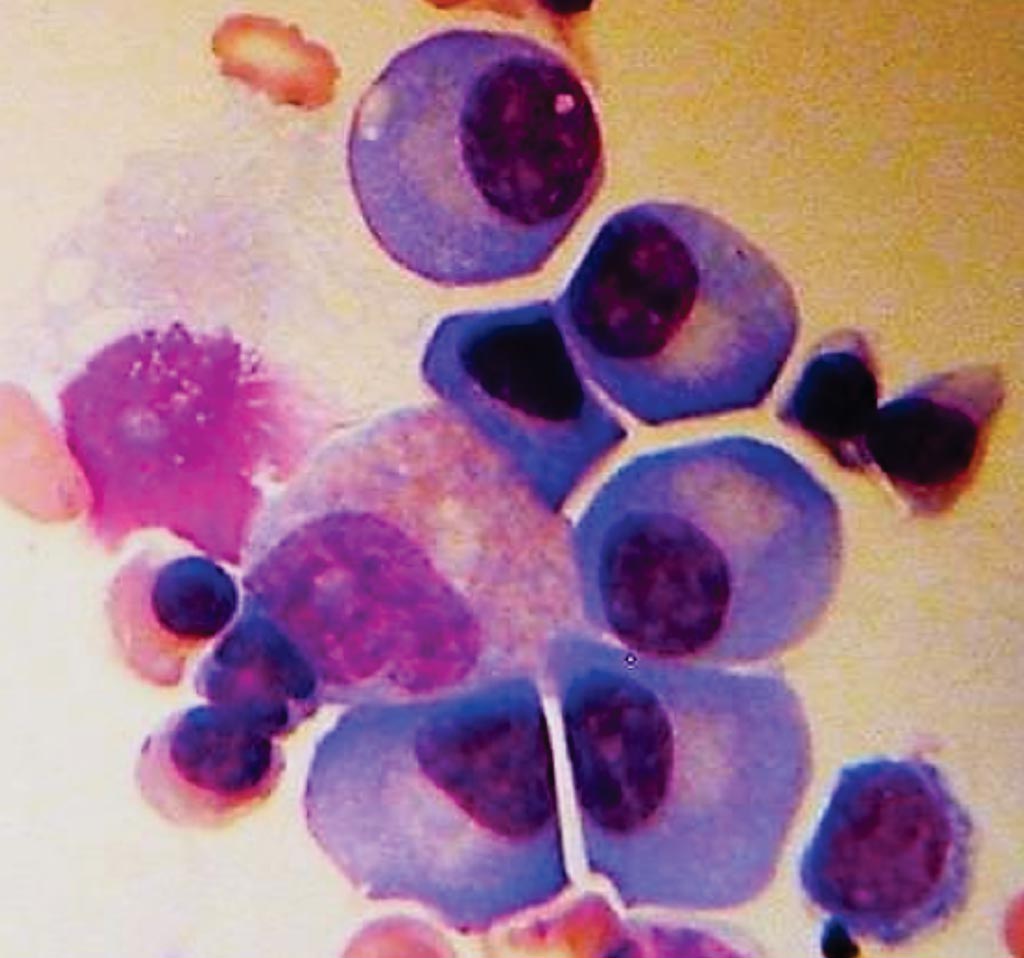
Imagen: Una biopsia de médula ósea que muestra células plasmáticas de un paciente con mieloma múltiple (Fotografía cortesía de la Sociedad Estadounidense de Oncología Clínica).
Se han descubierto dos genes con vínculos aparentes con el riesgo de mieloma múltiple heredado, a partir del análisis de varias familias estadounidenses grandes que, con frecuencia, se ven afectadas por el complejo cáncer sanguíneo de células plasmáticas.
El diseño de pedigrí de alto riesgo (HRP, por su sigla en inglés) es una estrategia establecida para descubrir variantes causales raras, altamente penetrantes, parecidas a los mendelianos. Sin embargo, su éxito en rasgos complejos ha sido modesto, principalmente debido a los desafíos de la heterogeneidad genética y los modelos de herencia complejos.
Un equipo internacional de científicos dirigido por los de la Facultad de Medicina de la Universidad de Utah (Salt Lake City, UT, EUA) utilizó una versión actualizada de un método de mapeo genético conocido como segmento genómico compartido (SGS) para acercarse a regiones comúnmente alteradas en los genomas de familias propensas al mieloma múltiple o “genealogías de alto riesgo” (HRP, por su sigla en inglés) de Utah. Al incorporar los datos de la secuencia del exoma para casi 1.000 individuos sin mieloma y más de 1,000 individuos afectados por mieloma múltiple o un trastorno precursor conocido como “gammapatía monoclonal de significado indeterminado” (MGUS), el equipo descubrió cambios sospechosos en dos genes: Peptidasa 45 específica de Ubiquitina (USP45) y Dominio de Interacción Rico en AT 1A (ARID1A), que parecen coincidir con el riesgo de mieloma múltiple.
El equipo utilizó arrays de SNP de alta densidad OmniExpress (Illumina, San Diego, CA, EUA) y secuenció individuos de 11 HRP de mieloma múltiple, identificados a través del Registro de Cáncer de Utah, y aplicaron el SGS para encontrar regiones compartidas del genoma en los cromosomas 6 y 1 con vínculos posibles con el mieloma múltiple. El equipo incorporó datos de secuencia de exomas para 28 individuos de los 11 pedigríes iniciales, junto con 126 exomas de un conjunto más amplio de 44 linajes de mieloma múltiple de EUA, Canadá y Francia, para identificar mutaciones raras y potencialmente nocivas en dos genes que caían en regiones de interés: USP45 y ARID1A.
En una colección de secuencias de exomas aún más amplia que abarcó 186 casos de mieloma múltiple de inicio temprano o MGUS familiar, 733 casos de mieloma múltiple esporádico analizados previamente y 964 controles no afectados, los investigadores descubrieron mutaciones adicionales que afectan a estos genes u otros genes que caen en las mismas vías de reparación del ADN de remodelación compleja de la cromatina como USP45 y ARID1A.
El equipo observó que “nuestros hallazgos de mieloma demuestran que nuestro método de pedigrí de alto riesgo puede identificar regiones genéticas de interés en pedigrís grandes de alto riesgo que también son relevantes para familias nucleares más pequeñas y el riesgo general de enfermedad. Hemos desarrollado una estrategia para el mapeo de genes en rasgos complejos que da cuenta de la heterogeneidad dentro de los HRP y corrige formalmente múltiples pruebas para permitir el descubrimiento estadísticamente riguroso”. El estudio fue publicado el 1 de febrero de 2018 en la revista Public Library of Science Genetics.
El diseño de pedigrí de alto riesgo (HRP, por su sigla en inglés) es una estrategia establecida para descubrir variantes causales raras, altamente penetrantes, parecidas a los mendelianos. Sin embargo, su éxito en rasgos complejos ha sido modesto, principalmente debido a los desafíos de la heterogeneidad genética y los modelos de herencia complejos.
Un equipo internacional de científicos dirigido por los de la Facultad de Medicina de la Universidad de Utah (Salt Lake City, UT, EUA) utilizó una versión actualizada de un método de mapeo genético conocido como segmento genómico compartido (SGS) para acercarse a regiones comúnmente alteradas en los genomas de familias propensas al mieloma múltiple o “genealogías de alto riesgo” (HRP, por su sigla en inglés) de Utah. Al incorporar los datos de la secuencia del exoma para casi 1.000 individuos sin mieloma y más de 1,000 individuos afectados por mieloma múltiple o un trastorno precursor conocido como “gammapatía monoclonal de significado indeterminado” (MGUS), el equipo descubrió cambios sospechosos en dos genes: Peptidasa 45 específica de Ubiquitina (USP45) y Dominio de Interacción Rico en AT 1A (ARID1A), que parecen coincidir con el riesgo de mieloma múltiple.
El equipo utilizó arrays de SNP de alta densidad OmniExpress (Illumina, San Diego, CA, EUA) y secuenció individuos de 11 HRP de mieloma múltiple, identificados a través del Registro de Cáncer de Utah, y aplicaron el SGS para encontrar regiones compartidas del genoma en los cromosomas 6 y 1 con vínculos posibles con el mieloma múltiple. El equipo incorporó datos de secuencia de exomas para 28 individuos de los 11 pedigríes iniciales, junto con 126 exomas de un conjunto más amplio de 44 linajes de mieloma múltiple de EUA, Canadá y Francia, para identificar mutaciones raras y potencialmente nocivas en dos genes que caían en regiones de interés: USP45 y ARID1A.
En una colección de secuencias de exomas aún más amplia que abarcó 186 casos de mieloma múltiple de inicio temprano o MGUS familiar, 733 casos de mieloma múltiple esporádico analizados previamente y 964 controles no afectados, los investigadores descubrieron mutaciones adicionales que afectan a estos genes u otros genes que caen en las mismas vías de reparación del ADN de remodelación compleja de la cromatina como USP45 y ARID1A.
El equipo observó que “nuestros hallazgos de mieloma demuestran que nuestro método de pedigrí de alto riesgo puede identificar regiones genéticas de interés en pedigrís grandes de alto riesgo que también son relevantes para familias nucleares más pequeñas y el riesgo general de enfermedad. Hemos desarrollado una estrategia para el mapeo de genes en rasgos complejos que da cuenta de la heterogeneidad dentro de los HRP y corrige formalmente múltiples pruebas para permitir el descubrimiento estadísticamente riguroso”. El estudio fue publicado el 1 de febrero de 2018 en la revista Public Library of Science Genetics.
Últimas Hematología noticias
- Prueba de sangre POC por punción digital determina riesgo de sepsis neutropénica en pacientes sometidos a quimioterapia
- Primera prueba rápida y asequible para beta talasemia demuestra precisión diagnóstica del 99 %
- Rastreador portátil de glóbulos blancos podría permitir pruebas rápidas de infecciones
- Analizador hematológico optofluídico inteligente del tamaño de la palma de la mano permite realizar pruebas POC de células sanguíneas del paciente
- Plataforma de hematología automatizada ofrece desempeño analítico de alto rendimiento
- Nueva herramienta analiza plaquetas sanguíneas de forma más rápida, sencilla y precisa
- Primer analizador de hematología de resultados rápidos informa medidas de infección y gravedad en el POC
- Prueba de diagnóstico de riesgo de hemorragia reduce complicaciones prevenibles en hospitales
- Verdadero analizador de hematología POC con muestreo capilar directo mejora facilidad de uso y rendimiento de pruebas
- Analizador de hemograma completo para el punto de atención con muestreo capilar directo mejora facilidad de uso y rendimiento de pruebas
- Examen de sangre podría predecir resultados en el departamento de emergencias y admisiones hospitalarias
- Nueva tecnología diagnostica inmunotrombosis mediante análisis de gases de aliento
- Sistema de hematología avanzado permite a laboratorios procesar hasta 119 resultados de hemogramas por hora
- Método único basado en IA automatiza análisis clínico de datos sanguíneos
- Herramienta portátil puede diagnosticar y monitorear enfermedad de células falciformes
- Analizadores de hematología de próxima generación eliminan obstáculos del flujo de trabajo y alcanzan un rendimiento rápido
Canales
Química Clínica
ver canal.jpg)
Prueba biomédica POC hace girar una gota de agua utilizando ondas sonoras para detección del cáncer
Los exosomas, pequeñas biopartículas celulares que transportan un conjunto específico de proteínas, lípidos y materiales genéticos, desempeñan un papel... Más
Prueba basada en células altamente confiable permite diagnóstico preciso de enfermedades endocrinas
Los métodos convencionales para medir el cortisol libre, la hormona del estrés del cuerpo, en la sangre o la saliva son bastante exigentes y requieren el procesamiento de muestras. Por lo tanto, el método... MásDiagnóstico Molecular
ver canal
Analizador de pruebas sindrómicas actualizado permite acceso remoto a resultados de pruebas
QIAGEN (Venlo, Países Bajos) ha lanzado el analizador QIAstat-Dx 2.0, incluida la actualización del software 1.6. Esto representa un avance significativo con respecto al analizador QIAstat-Dx 1.... Más
Prueba de PCR para infecciones respiratorias y de garganta detecta múltiples patógenos con síntomas coincidentes
La pandemia de COVID-19 ha demostrado la necesidad de que los profesionales de la salud tengan pruebas de diagnóstico disponibles lo más cerca posible del paciente, proporcionando resultados... Más
Técnica de enriquecimiento de ácido nucleico circulante en sangre permite diagnóstico no invasivo del cáncer de hígado
La capacidad de diagnosticar enfermedades de forma temprana puede optimizar significativamente la eficacia de los tratamientos clínicos y mejorar las tasas de supervivencia. Un enfoque prometedor... Más
Primera prueba molecular aprobada por la FDA para detectar malaria en donantes de sangre podría mejorar seguridad del paciente
La malaria, una enfermedad grave que a menudo provoca la muerte, se transmite por una especie específica de mosquito que infecta a los humanos con un parásito. Otros modos de transmisión... MásInmunología
ver canal
Método de prueba podría ayudar a más pacientes recibir tratamiento adecuado contra el cáncer
El tratamiento del cáncer no siempre es una solución única, pero el campo de la investigación del cáncer está dando grandes pasos para encontrar a los pacientes los tratamientos más eficaces para sus afecciones... Más
Prueba innovadora monitorea toxicidad de radioterapia en pacientes con cáncer
La concentración de ADN libre de células circulante (ADNlc) en el torrente sanguíneo es un indicador importante que puede ayudar a rastrear qué tan bien están funcionando... MásMicrobiología
ver canal
Análisis de sangre predice sepsis e insuficiencia orgánica en niños
La sepsis plantea un riesgo grave en el que una reacción inmune grave a la infección provoca daño a los órganos. Identificar la sepsis en niños es complejo ya que los... Más
Análisis de sangre para tuberculosis podría detectar millones de propagadores silenciosos
La tuberculosis (TB) es la enfermedad infecciosa más mortal del mundo y se cobra más de un millón de vidas al año, según informa la Organización Mundial de la Salud.... Más
Un análisis de sangre simple combinado con un modelo de riesgo personalizado mejora el diagnóstico de sepsis
La sepsis, una afección crítica que surge de la disfunción orgánica debido a una infección grave, puede progresar a una sepsis grave y un shock séptico, lo que provoca insuficiencia multiorgánica y un... Más
Nuevo análisis de sangre reduce tiempo de diagnóstico de infecciones por micobacterias no tuberculosas de meses a horas
Respirar micobacterias no tuberculosas (MNT) es una experiencia común para muchas personas. Estas bacterias están presentes en los sistemas de agua, el suelo y el polvo de todo el mundo y,... MásPatología
ver canal
Innovador dispositivo de extracción de sangre supera obstáculos comunes relacionados con la flebotomía
La incomodidad asociada con las extracciones de sangre tradicionales genera un problema importante: aproximadamente el 30 % de las pruebas de diagnóstico prescritas por los médicos nunca... Más
Dispositivo POC intraoperatorio distingue entre quistes ováricos benignos y malignos en 15 minutos
Los quistes ováricos representan un problema de salud importante para las mujeres en todo el mundo, y hasta el 10 % experimenta esta afección en algún momento de sus vidas.... Más
Prueba simple de biopsia de piel detecta el Parkinson y enfermedades neurodegenerativas relacionadas
La enfermedad de Parkinson y un grupo de trastornos neurodegenerativos relacionados conocidos como sinucleinopatías afectan a millones de personas en todo el mundo. Estas afecciones, incluida la... MásTecnología
ver canal
Biosensor de ADN permite diagnóstico temprano del cáncer de cuello uterino
El disulfuro de molibdeno (MoS2), reconocido por su potencial para formar nanoláminas bidimensionales como el grafeno, es un material que llama cada vez más la atención de la comunidad... Más
Dispositivos de microfluidos autocalentables pueden detectar enfermedades en pequeñas muestras de sangre o fluidos
Los microfluidos, que son dispositivos en miniatura que controlan el flujo de líquidos y facilitan reacciones químicas, desempeñan un papel clave en la detección de enfermedades... Más
Avance en tecnología de diagnóstico podría hacer que pruebas en el sitio sean ampliamente accesibles
Las pruebas caseras adquirieron una importancia significativa durante la pandemia de COVID-19, sin embargo, la disponibilidad de pruebas rápidas es limitada y la mayoría de ellas solo pueden conducir un... MásIndustria
ver canal
Congreso ECCMID cambia de nombre a ESCMID Global
En los últimos años, la Sociedad Europea de Microbiología Clínica y Enfermedades Infecciosas (ESCMID, Basilea, Suiza) ha evolucionado notablemente. La sociedad es ahora más... Más











.jpg)
.jpg)
.jpg)