Análisis rápido de flujo lateral detecta las variantes de la COVID-19 y diferencia la COVID-19 de otras enfermedades virales respiratorias
|
Por el equipo editorial de LabMedica en español Actualizado el 04 Mar 2021 |
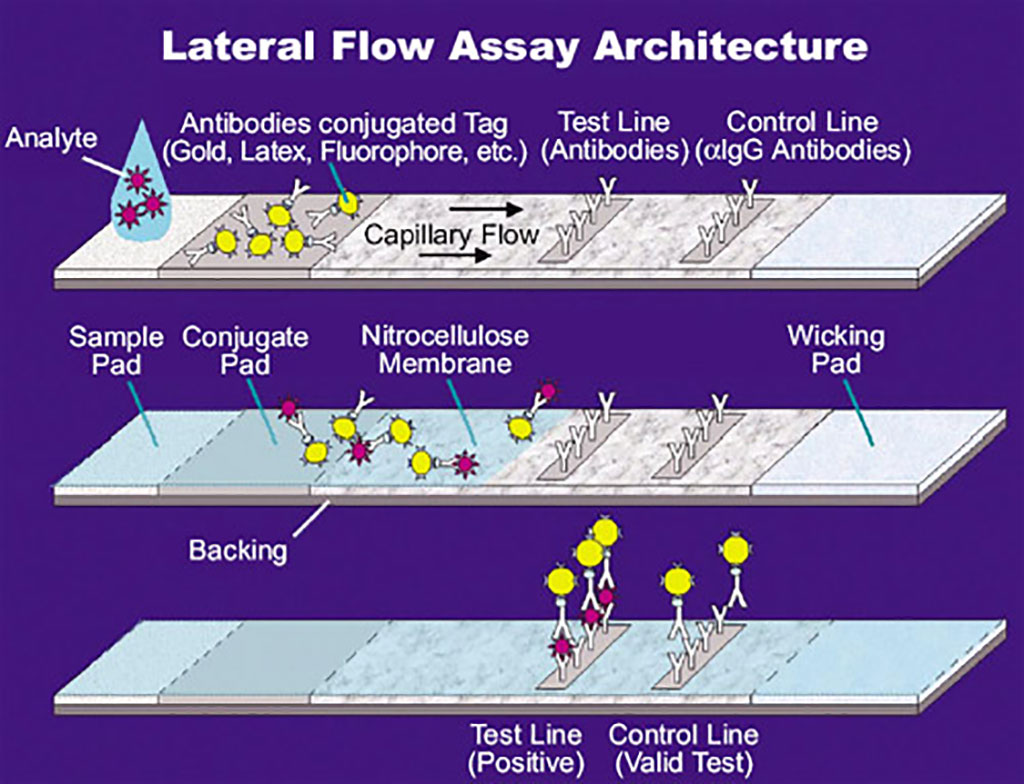
Imagen: Ilustración de un ensayo de flujo lateral (LFA) (Fotografía cortesía de la Administración Nacional de Aeronáutica y del Espacio de EUA a través de Wikimedia Commons)
Una publicación reciente informó el desarrollo de dos pruebas de diagnóstico rápido: una que detecta variantes de COVID-19 y otra que diferencia la COVID-19 de otras enfermedades virales respiratorias.
Los investigadores de la Facultad de Medicina de la Universidad de Minnesota (Minneapolis/St. Paul, EUA) utilizaron la herramienta de edición de genes CRISPR/Cas9 para desarrollar dos pruebas rápidas de diagnóstico de flujo lateral. Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013 se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) en una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada. El sistema CRISPR/Cas9 convencional de Streptococcus pyogenes se compone de dos partes: la enzima Cas9, que escinde la molécula de ADN y guías específicas de ARN que llevan la proteína Cas9 al gen diana en una hebra de ADN.
Los investigadores integraron reactivos disponibles comercialmente en un ensayo de flujo lateral (LFA) basado en CRISPR/Cas9, que podría detectar secuencias del coronavirus 2 del síndrome respiratorio agudo severo (SARS-CoV-2) con especificidad de una sola base. Este enfoque requería un equipo mínimo y representaba una plataforma simplificada para la implementación en el campo. También desarrollaron un ensayo rápido múltiplex de escisión de nucleasa CRISPR/Cas9 de fluorescencia, capaz de detectar y diferenciar el SARS-CoV-2, la influenza A y B y el virus sincitial respiratorio (VSR) en una sola reacción.
Las tiras reactivas del LFA emplearon isotiocianato de fluoresceína (FITC)/6-carboxifluoresceína (FAM) y biotina unidas para generar un resultado positivo. Por lo tanto, los investigadores utilizaron un cebador de PCR marcado con FITC/FAM y un Cas9 biotinilado inactivo con nucleasa (“muerto”) y un solo ARNsg específico para el gen ORF8a del SARS-Co-V-2 para marcar los amplicones para su detección mediante el LFA. Este enfoque fue capaz de resolución de un solo nucleótido y evitó falsos positivos de dímero de cebador o artefactos de amplificación no específicos que podrían ocurrir con el uso de cebadores en tándem marcados con FITC y biotina para los LFA.
“La aprobación de la vacuna contra el SARS-CoV-2 es muy prometedora, pero el tiempo entre las primeras dosis y la inmunidad de la población puede ser de meses”, dijo el primer autor, el Dr. Mark J. Osborn, profesor asistente de pediatría en la Facultad de Medicina de la Universidad de Minnesota. “Esta plataforma de pruebas puede ayudar a cerrar la brecha entre la inmunización y la inmunidad”.
Las pruebas rápidas de LFA se describieron en la edición en línea del 12 de febrero de 2021 de la revista Bioengineering.
Enlace relacionado:
Facultad de Medicina de la Universidad de Minnesota
Los investigadores de la Facultad de Medicina de la Universidad de Minnesota (Minneapolis/St. Paul, EUA) utilizaron la herramienta de edición de genes CRISPR/Cas9 para desarrollar dos pruebas rápidas de diagnóstico de flujo lateral. Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013 se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) en una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada. El sistema CRISPR/Cas9 convencional de Streptococcus pyogenes se compone de dos partes: la enzima Cas9, que escinde la molécula de ADN y guías específicas de ARN que llevan la proteína Cas9 al gen diana en una hebra de ADN.
Los investigadores integraron reactivos disponibles comercialmente en un ensayo de flujo lateral (LFA) basado en CRISPR/Cas9, que podría detectar secuencias del coronavirus 2 del síndrome respiratorio agudo severo (SARS-CoV-2) con especificidad de una sola base. Este enfoque requería un equipo mínimo y representaba una plataforma simplificada para la implementación en el campo. También desarrollaron un ensayo rápido múltiplex de escisión de nucleasa CRISPR/Cas9 de fluorescencia, capaz de detectar y diferenciar el SARS-CoV-2, la influenza A y B y el virus sincitial respiratorio (VSR) en una sola reacción.
Las tiras reactivas del LFA emplearon isotiocianato de fluoresceína (FITC)/6-carboxifluoresceína (FAM) y biotina unidas para generar un resultado positivo. Por lo tanto, los investigadores utilizaron un cebador de PCR marcado con FITC/FAM y un Cas9 biotinilado inactivo con nucleasa (“muerto”) y un solo ARNsg específico para el gen ORF8a del SARS-Co-V-2 para marcar los amplicones para su detección mediante el LFA. Este enfoque fue capaz de resolución de un solo nucleótido y evitó falsos positivos de dímero de cebador o artefactos de amplificación no específicos que podrían ocurrir con el uso de cebadores en tándem marcados con FITC y biotina para los LFA.
“La aprobación de la vacuna contra el SARS-CoV-2 es muy prometedora, pero el tiempo entre las primeras dosis y la inmunidad de la población puede ser de meses”, dijo el primer autor, el Dr. Mark J. Osborn, profesor asistente de pediatría en la Facultad de Medicina de la Universidad de Minnesota. “Esta plataforma de pruebas puede ayudar a cerrar la brecha entre la inmunización y la inmunidad”.
Las pruebas rápidas de LFA se describieron en la edición en línea del 12 de febrero de 2021 de la revista Bioengineering.
Enlace relacionado:
Facultad de Medicina de la Universidad de Minnesota
Últimas COVID-19 noticias
- Inmunosensor nuevo allana el camino para pruebas rápidas POC para COVID-19 y enfermedades infecciosas emergentes
- Encuentran etiologías de COVID prolongada en muestras de sangre con infección aguda
- Dispositivo novedoso detecta anticuerpos contra la COVID-19 en cinco minutos
- Prueba para COVID-19 mediante CRISPR detecta SARS-CoV-2 en 30 minutos usando tijeras genéticas
- Asocian disbiosis del microbioma intestinal con la COVID-19
- Validan prueba rápida novedosa de antígeno para el SARS-CoV-2 con respecto a su exactitud diagnóstica
- Prueba nueva COVID + Influenza + VSR ayudará a estar preparados para la ‘tripledemia’
- IA elimina las conjeturas de las pruebas de flujo lateral
- Prueba de antígeno del SARS-CoV-2 más rápida, jamás diseñada, permite realizar pruebas de COVID-19 no invasivas en cualquier entorno
- Pruebas rápidas de antígeno detectan las variantes ómicron, delta del SARS-CoV-2
- Prueba en sangre realizada durante la infección inicial predice el riesgo de COVID prolongada
- Investigadores afirman que hay que crear “reservistas” de laboratorio para responder más rápidamente a la próxima pandemia
- Estudio encuentra que los profesionales sanitarios mostraron mayor interés en tecnologías POC durante la pandemia
- Plataforma de análisis de bajo costo para la COVID-19 combina sensibilidad de la PCR y velocidad de pruebas de antígeno
- Prueba de sangre por punción digital identifica inmunidad a la COVID-19
- Kit de prueba rápida determina inmunidad contra la COVID-19 y sus variantes
Canales
Química Clínica
ver canal
Nanotubos de carbono ayudan a construir sensores precisos para monitoreo continuo de la salud
Los sensores actuales pueden medir diversos indicadores de salud, como los niveles de glucosa en sangre. Sin embargo, es necesario desarrollar materiales para sensores más precisos y sensibles que... Más
Dispositivo basado en papel mejora la precisión de prueba del VIH
En las regiones donde el acceso a las clínicas para realizar análisis de sangre rutinarios presenta obstáculos financieros y logísticos, los pacientes con VIH pueden recolectar... MásDiagnóstico Molecular
ver canal
Prueba de dímero D puede identificar pacientes con mayor riesgo de embolia pulmonar
La embolia pulmonar (EP) es una afección que se sospecha con frecuencia en los servicios de urgencias (SU) y puede ser potencialmente mortal si no se diagnostica correctamente. Lograr un diagnóstico... Más
Nuevos biomarcadores mejoran la detección temprana y seguimiento de la lesión renal
La lesión renal inducida por fármacos, también conocida como nefrotoxicidad, es un problema frecuente en la práctica clínica, que se produce cuando medicamentos espe... Más
Inmunoensayos de quimioluminiscencia respaldan diagnóstico de Alzheimer
Se requieren inmunoensayos robustos para la cuantificación de biomarcadores específicos en la enfermedad de Alzheimer (EA) para el diagnóstico de rutina. La medición de los... Más
Análisis de sangre identifica múltiples biomarcadores para diagnóstico rápido de lesiones de médula espinal
Los Institutos Nacionales de Salud estiman que 18.000 personas en Estados Unidos sufren lesiones de la médula espinal (LME) anualmente, lo que resulta en una asombrosa carga financiera de más de 9.... MásHematología
ver canal
Nuevo sistema de puntuación predice riesgo de cáncer a partir de un trastorno sanguíneo común
La citopenia clonal de significado incierto (CCSI) es un trastorno sanguíneo común en adultos mayores, caracterizado por mutaciones en las células sanguíneas y un recuento ... Más
Prueba prenatal no invasiva para determinar estado RhD del feto es 100 % precisa
En los Estados Unidos, aproximadamente el 15 % de las embarazadas son RhD negativas. Sin embargo, en aproximadamente el 40 % de estos casos, el feto también es RhD negativo, lo que hace innecesaria la... MásInmunología
ver canal
Análisis de sangre podría orientar decisiones futuras sobre tratamiento del cáncer
En el continuo avance de la medicina personalizada, un nuevo estudio ha aportado evidencia que respalda el uso de una herramienta que detecta moléculas derivadas del cáncer en la sangre de... Más
Prueba de líquido cefalorraquídeo predice efecto secundario peligroso del tratamiento del cáncer
En los últimos años, la inmunoterapia contra el cáncer se ha convertido en un enfoque prometedor que aprovecha el sistema inmunitario del paciente para combatir el cáncer.... MásMicrobiología
ver canal
Innovadora tecnología disgnóstica identifica infecciones bacterianas con precisión de casi 100 % en tres horas
La identificación rápida y precisa de microbios patógenos en muestras de pacientes es esencial para el tratamiento eficaz de enfermedades infecciosas agudas, como la sepsis.... Más
Sistema de identificación y PSA ayuda a diagnosticar enfermedades infecciosas y combatir RAM
Cada año, 11 millones de personas en todo el mundo mueren de sepsis, de las cuales 1,3 millones se deben a bacterias resistentes a los antibióticos. La resistencia a los antimicrobianos (RAM)... MásPatología
ver canal
Modelo de IA predice respuesta al tratamiento del cáncer de vejiga
Cada año en Estados Unidos, se diagnostican alrededor de 81.000 nuevos casos de cáncer de vejiga, lo que provoca aproximadamente 17.000 muertes al año. El cáncer de vejiga ... Más
Nuevo método basado en láser acelera diagnóstico del cáncer
Investigadores han desarrollado un método para mejorar el diagnóstico del cáncer y otras enfermedades. El colágeno, una proteína estructural clave, desempeña diversas funciones en la actividad celular.... Más
Nuevo modelo de IA predice efectos de variantes genéticas en enfermedades específicas
En los últimos años, la inteligencia artificial (IA) ha mejorado considerablemente nuestra capacidad para identificar un gran número de variantes genéticas en poblaciones cada... Más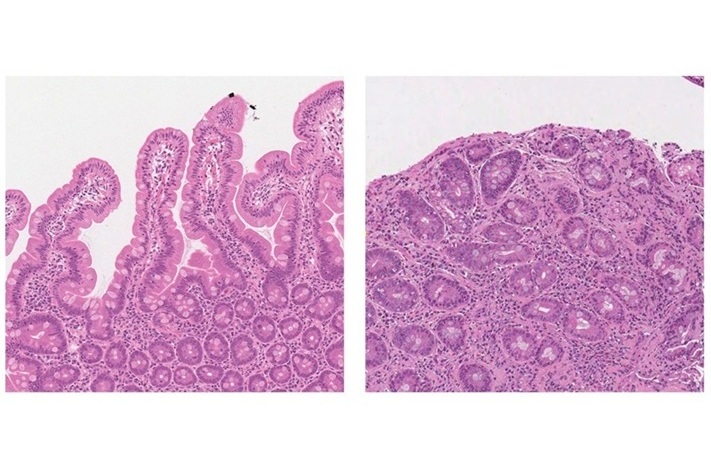
Herramienta de IA diagnostica enfermedad celíaca en imágenes de biopsia con precisión superior al 97%
La enfermedad celíaca es un trastorno autoinmune desencadenado por el consumo de gluten, que causa síntomas como calambres estomacales, diarrea, erupciones cutáneas, pérdida de peso, fatiga y anemia.... MásTecnología
ver canal
Teléfonos inteligentes podrían diagnosticar enfermedades mediante escáneres infrarrojos
Los rápidos avances tecnológicos pronto permitirán que las personas eviten procedimientos médicos invasivos simplemente subiendo una captura de pantalla de sus resultados de... Más
Nueva tecnología de sensores permite diagnóstico temprano de trastornos metabólicos y cardiovasculares
Los metabolitos son compuestos cruciales que impulsan las funciones vitales, desempeñando un papel clave en la producción de energía, la regulación de la actividad celular y... MásIndustria
ver canal