Innovadora tecnología identifica infecciones bacterianas con precisión de casi 100 % en tres horas
Actualizado el 03 Apr 2025
La identificación rápida y precisa de microbios patógenos en muestras de pacientes es esencial para el tratamiento eficaz de enfermedades infecciosas agudas, como la sepsis. La técnica de hibridación in situ con fluorescencia (FISH) facilita la detección e identificación rápidas de microbios al aprovechar las diferencias en sus secuencias genómicas, sin necesidad de cultivos o secuenciaciones que requieren mucho tiempo. Sin embargo, el creciente volumen de datos genómicos microbianos ha dificultado cada vez más el diseño de sondas adecuadas para mezclas microbianas. Ahora, se ha desarrollado un nuevo conjunto de sondas FISH basadas en ácidos nucleicos peptídicos (ANP), que ofrecen una especificidad óptima del objetivo mediante el análisis de variaciones en la secuencia del ARN ribosómico 16S en diferentes especies bacterianas. Debido a su mayor capacidad para penetrar bacterias y su mayor sensibilidad a los desajustes, estas sondas ANP identificaron con éxito siete especies bacterianas comúnmente asociadas con bacteriemia con una precisión que oscila entre el 96 % y el 99,9 % utilizando la técnica FISH optimizada. La detección se ve reforzada por la transferencia de energía por resonancia de Förster (FRET) entre sondas de ANP de unión adyacentes, lo que previene la reactividad cruzada entre especies. Este enfoque permite la identificación rápida y secuencial de especies bacterianas mediante fluoróforos químicamente escindibles, sin sacrificar la precisión. Gracias a su excepcional precisión y velocidad, estas técnicas son muy prometedoras para aplicaciones clínicas.
Un equipo de investigadores de UNIST (Ulsan, República de Corea) ha desarrollado un método de diagnóstico capaz de identificar patógenos infecciosos con una precisión cercana al 100 % en menos de tres horas. Este método es mucho más rápido y preciso que el cultivo bacteriano tradicional y el análisis de reacción en cadena de la polimerasa (PCR), y ofrece el potencial de reducir las tasas de mortalidad en condiciones críticas como la sepsis, donde la administración rápida de antibióticos es esencial. En su estudio, publicado en Biosensors and Bioelectronics, los investigadores presentaron un nuevo enfoque de diagnóstico que utiliza sondas basadas en ANP para detectar patógenos. La técnica FISH funciona detectando señales fluorescentes generadas cuando las moléculas de la sonda se unen a secuencias genéticas bacterianas específicas. Este método innovador utiliza dos moléculas de ANP a la vez, y los investigadores diseñan secuencias de ANP que se dirigen específicamente al ARN ribosómico de especies bacterianas particulares analizando las secuencias genómicas de 20.000 especies.
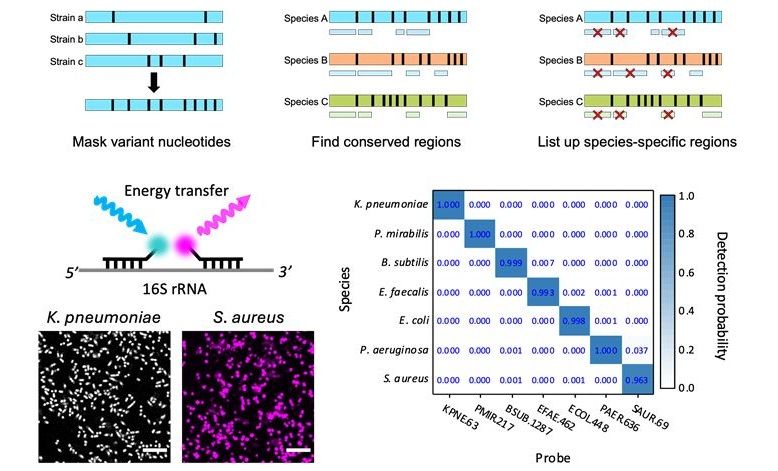
El ANP presenta una mayor sensibilidad a los desajustes de secuencia en comparación con las sondas convencionales basadas en ADN y una penetración superior a través de las paredes celulares bacterianas. Además, el requisito de que ambas moléculas de ANP se unan a su sitio diana antes de generar una señal reduce significativamente el riesgo de diafonía, lo que mejora la precisión cuando se superponen múltiples cepas bacterianas. En las pruebas, la tecnología detectó con éxito siete especies bacterianas, incluidas E. coli, Pseudomonas aeruginosa y Staphylococcus aureus , con una precisión superior al 99 % para todas las especies, excepto Staphylococcus aureus, que se detectó con una precisión del 96,3 %. La eficacia del método también se validó en muestras bacterianas mixtas, donde Enterococcus y E. coli se identificaron con una precisión superior al 99 % al analizarse conjuntamente. El equipo de investigación planea realizar más experimentos con muestras de sangre de pacientes reales para explorar las aplicaciones clínicas de este método.
“Este método ayudará en el diagnóstico de infecciones que requieren tratamiento antibiótico inmediato, como sepsis, infecciones del tracto urinario y neumonía, al tiempo que ayudará a reducir el uso innecesario de antibióticos”, dijo el profesor Hajun Kim del Departamento de Ingeniería Biomédica de la UNIST.
Enlaces relacionados:
UNIST