Análisis rápido CRISPR/Cas para el diagnóstico de fiebres virales en ambientes de baja tecnología
|
Por el equipo editorial de LabMedica en español Actualizado el 07 Sep 2020 |
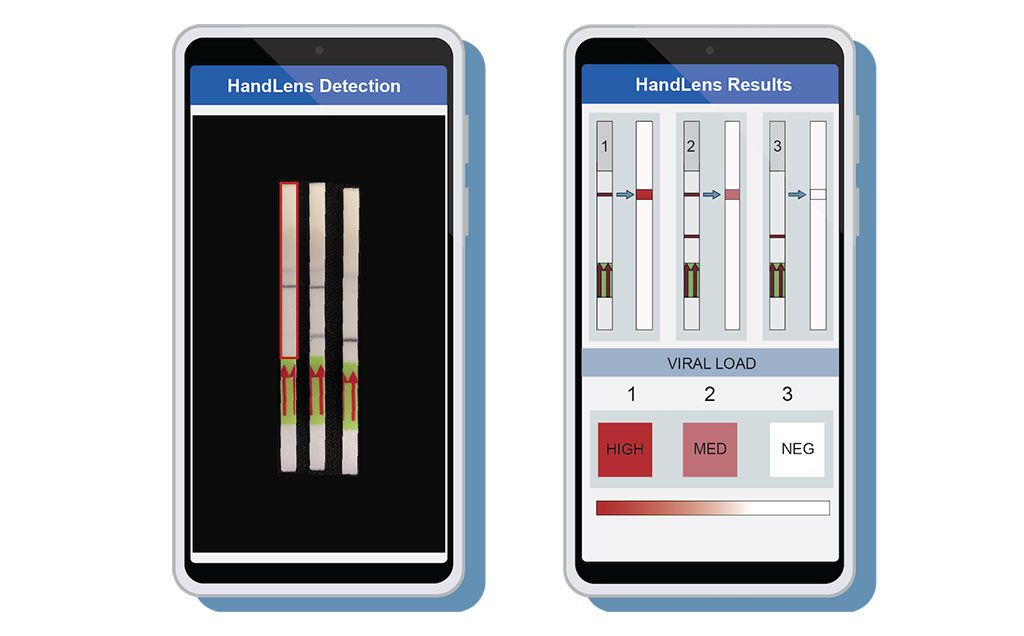
Imagen: Se diseñó una aplicación para teléfonos móviles llamada HandLens para leer e informar los resultados en las tiras de papel SHERLOCK (Fotografía cortesía de Anna Lachenauer, Facultad de Medicina de la Universidad de Stanford)
Las pruebas de diagnóstico rápido para los virus de la fiebre del Ébola y Lassa, basadas en el complejo CRISPR/Cas13a, dirigidas a la detección del ARN, se han probado con éxito en condiciones de campo en varios países africanos.
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
Últimas Tecnología noticias
- Algoritmo de firma ligera permite diagnósticos médicos más rápidos y precisos
- Tecnología de microchip desechable podría detectar selectivamente VIH en muestras de sangre completa
- Dispositivo microfluídico Dolor en un Chip determina tipos de dolor crónico desde muestras de sangre
- Innovador sensor fluorométrico sin etiquetas permite detección más sensible del ARN viral
- Teléfonos inteligentes podrían diagnosticar enfermedades mediante escáneres infrarrojos
- Nueva tecnología de sensores permite diagnóstico temprano de trastornos metabólicos y cardiovasculares
- Avance en impresión 3D permite desarrollo a gran escala de diminutos dispositivos microfluídicos
- Plataforma de sensores en papel transforma diagnóstico cardíaco
- Estudio explora impacto de pruebas POC en el futuro de los diagnósticos
- Sensor económico de respuesta rápida permite detección temprana y precisa del cáncer de pulmón
- Nanotecnología para diagnósticar cáncer de cuello uterino podría sustituir pruebas de Papanicolaou
- Plataforma de laboratorio en chip agilizar diagnóstico del cáncer
- Plataforma de biosensores detecta simultáneamente vitamina C y SARS-CoV-2
- Nuevo método analiza lágrimas para detectar enfermedades de forma temprana
- Sensores basados en FET abren camino a dispositivos de diagnóstico portátiles para detectar múltiples enfermedades
- Biosensor basado en papel para detectar glucosa mediante sudor revoluciona tratamiento de diabetes
Canales
Química Clínica
ver canal
Monitorización con espectrometría de masas predice e identifica recaída temprana del mieloma
El mieloma, un tipo de cáncer que afecta la médula ósea, es actualmente incurable, aunque muchos pacientes pueden vivir más de 10 años tras el diagnóstico.... Más
Herramienta química a nanoescala 'brillantemente luminosa' mejora detección de enfermedades
Miles de moléculas brillantes disponibles comercialmente, conocidas como fluoróforos, se utilizan comúnmente en imágenes médicas, detección de enfermedades, marcado... MásDiagnóstico Molecular
ver canal
Herramienta genética predice supervivencia de pacientes con cáncer de páncreas
Un marcador tumoral es una sustancia presente en el organismo que puede indicar la presencia de cáncer. Estas sustancias, que pueden incluir proteínas, genes, moléculas u otros compuestos... Más
Prueba de orina diagnostica cáncer de próstata inicial
El cáncer de próstata es una de las principales causas de muerte en hombres a nivel mundial. Un desafío importante para diagnosticar la enfermedad es la ausencia de biomarcadores confiables... MásHematología
ver canal
Nuevo sistema de puntuación predice riesgo de cáncer a partir de un trastorno sanguíneo común
La citopenia clonal de significado incierto (CCSI) es un trastorno sanguíneo común en adultos mayores, caracterizado por mutaciones en las células sanguíneas y un recuento ... Más
Prueba prenatal no invasiva para determinar estado RhD del feto es 100 % precisa
En los Estados Unidos, aproximadamente el 15 % de las embarazadas son RhD negativas. Sin embargo, en aproximadamente el 40 % de estos casos, el feto también es RhD negativo, lo que hace innecesaria la... MásInmunología
ver canal
Prueba de células madre predice resultado del tratamiento en cáncer de ovario resistente al platino
El cáncer de ovario epitelial suele responder inicialmente a la quimioterapia, pero con el tiempo, el tumor desarrolla resistencia a la terapia, lo que provoca su recrecimiento. Esta resistencia... Más
Análisis de sangre con aprendizaje automático predice respuesta a inmunoterapia en pacientes con linfoma
La terapia de células T con receptores de antígenos quiméricos (CAR) se ha convertido en uno de los avances recientes más prometedores en el tratamiento de los cánceres... MásPatología
ver canal
Modelo de IA predice respuesta a terapia contra cáncer de riñón
Cada año, cerca de 435.000 personas son diagnosticadas con carcinoma renal de células claras (CRcc), lo que lo convierte en el subtipo más prevalente de cáncer de riñón.... Más
Kits de ensayo de enzima DUB sensibles y específicos requieren configuración mínima sin preparación del sustrato
La ubiquitinación y la desubiquitinación son dos procesos fisiológicos importantes en el sistema ubiquitina-proteasoma, responsable de la degradación de proteínas en... MásTecnología
ver canal
Algoritmo de firma ligera permite diagnósticos médicos más rápidos y precisos
Cada material o molécula interactúa con la luz de forma única, creando un patrón distintivo, similar a una huella dactilar. La espectroscopia óptica, que consiste en... Más
Tecnología de microchip desechable podría detectar selectivamente VIH en muestras de sangre completa
A finales de 2023, aproximadamente 40 millones de personas en todo el mundo vivían con VIH, y alrededor de 630.000 personas murieron por enfermedades relacionadas con el sida ese mismo año.... MásIndustria
ver canal
Cepheid y Oxford Nanopore se unen para desarrollar soluciones con secuenciación automatizada
Cepheid (Sunnyvale, CA, EUA), una empresa líder en diagnóstico molecular, y Oxford Nanopore Technologies (Oxford, Reino Unido), la empresa detrás de una nueva generación de... Más