Secuenciación genómica de infección por SARM predice gravedad de la enfermedad
|
Por el equipo editorial de LabMedica en español Actualizado el 04 Jun 2014 |

Imagen: El Analizador de Genoma IIx (Fotografía cortesía de Illumina).
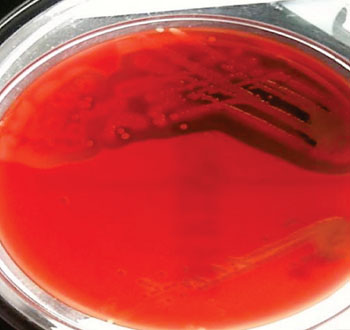
Imagen B: La cepa altamente tóxica de Staphylococcus aureus resistente a la meticilina (SARM) (arriba) y la cepa menos tóxica (abajo) cultivadas en placas de agar sangre (Fotografía cortesía de Ruth Massey).
Los patógenos bacterianos, como el Staphylococcus aureus resistente a la meticilina (SARM) causan, la enfermedad debido a la toxicidad o la capacidad de la bacteria de dañar el tejido del huésped.
La diseminación del patógeno resistente a los antibióticos sigue siendo una preocupación de salud pública, especialmente entre los médicos que están tratando de determinar las opciones de tratamiento apropiadas para los pacientes infectados.
Los microbiólogos de la Universidad de Bath (Reino Unido) y un equipo de científicos internacionales utilizaron secuencias de todo el genoma de 90 aislados de SARM para identificar más de 100 loci genéticos asociados con la toxicidad. Se evaluó la adhesión bacteriana a la fibronectina y el fibrinógeno humano y se calcularon las bacterias adherentes utilizando el método de cristal violeta y la absorbancia medida a A595 usando un lector de placas de microtitulación. La toxicidad de los aislados individuales fue analizada de tres formas.
Se estudió la identificación de la variación genética en los aislados clínicos utilizando bibliotecas únicas de índice de etiquetado creadas para cada muestra y se secuenciaron hasta 12 bibliotecas independientes en cada uno de los ocho canales en las células del analizador Genome Analyzer GAIIx (Illumina; San Diego, CA, EUA) con 75 lecturas de pares de bases finales.
Los autores encontraron que mediante el uso de las secuencias de todo el genoma a partir de 90 aislados de SARM fueron capaces de identificar más de 100 loci genéticos asociados a la toxicidad y, a pesar de pertenecer al mismo clon ST239, los aislados variaron en mucho con respecto a la toxicidad. Es importante destacar que los aislados altamente tóxicos compartieron una firma genética común. Mediante el estudio de esta firma en el genoma del SARM, los investigadores fueron capaces de predecir cuáles aislados eran los más tóxicos y por lo tanto más propensos a causar una enfermedad grave cuando se utilizaron para infectar a los ratones.
Ruth C. Massey, PhD, autora principal del estudio, dijo: “A medida que el costo y la velocidad de la secuenciación del genoma disminuye, se hace cada vez más factible secuenciar el genoma de un organismo infeccioso. En un entorno clínico, la secuenciación puede ser útil para decidir el tipo de tratamiento para el SARM. Por ejemplo, un médico puede tratar una infección altamente tóxica más agresivamente, incluyendo la formulación de ciertos antibióticos conocidos para reducir la expresión de la toxina. El paciente también puede recibir un seguimiento más de cerca en busca de las complicaciones y aislarlo de los demás para ayudar a controlar la propagación de la infección”. El estudio fue publicado el 9 de abril de 2014, en la revista Genome Research.
Enlaces relacionados:
University of Bath
Illumina
La diseminación del patógeno resistente a los antibióticos sigue siendo una preocupación de salud pública, especialmente entre los médicos que están tratando de determinar las opciones de tratamiento apropiadas para los pacientes infectados.
Los microbiólogos de la Universidad de Bath (Reino Unido) y un equipo de científicos internacionales utilizaron secuencias de todo el genoma de 90 aislados de SARM para identificar más de 100 loci genéticos asociados con la toxicidad. Se evaluó la adhesión bacteriana a la fibronectina y el fibrinógeno humano y se calcularon las bacterias adherentes utilizando el método de cristal violeta y la absorbancia medida a A595 usando un lector de placas de microtitulación. La toxicidad de los aislados individuales fue analizada de tres formas.
Se estudió la identificación de la variación genética en los aislados clínicos utilizando bibliotecas únicas de índice de etiquetado creadas para cada muestra y se secuenciaron hasta 12 bibliotecas independientes en cada uno de los ocho canales en las células del analizador Genome Analyzer GAIIx (Illumina; San Diego, CA, EUA) con 75 lecturas de pares de bases finales.
Los autores encontraron que mediante el uso de las secuencias de todo el genoma a partir de 90 aislados de SARM fueron capaces de identificar más de 100 loci genéticos asociados a la toxicidad y, a pesar de pertenecer al mismo clon ST239, los aislados variaron en mucho con respecto a la toxicidad. Es importante destacar que los aislados altamente tóxicos compartieron una firma genética común. Mediante el estudio de esta firma en el genoma del SARM, los investigadores fueron capaces de predecir cuáles aislados eran los más tóxicos y por lo tanto más propensos a causar una enfermedad grave cuando se utilizaron para infectar a los ratones.
Ruth C. Massey, PhD, autora principal del estudio, dijo: “A medida que el costo y la velocidad de la secuenciación del genoma disminuye, se hace cada vez más factible secuenciar el genoma de un organismo infeccioso. En un entorno clínico, la secuenciación puede ser útil para decidir el tipo de tratamiento para el SARM. Por ejemplo, un médico puede tratar una infección altamente tóxica más agresivamente, incluyendo la formulación de ciertos antibióticos conocidos para reducir la expresión de la toxina. El paciente también puede recibir un seguimiento más de cerca en busca de las complicaciones y aislarlo de los demás para ayudar a controlar la propagación de la infección”. El estudio fue publicado el 9 de abril de 2014, en la revista Genome Research.
Enlaces relacionados:
University of Bath
Illumina
Últimas Microbiología noticias
- Un panel gastrointestinal aprobado por la FDA detecta 24 patógenos
- Nuevo ensayo de RAM respalda el cribado rápido para el control de infecciones en hospitales
- Estudio revela que infecciones ocultas de mpox podrían impulsar su propagación continua
- Vigilancia genómica a gran escala rastrea bacterias resistentes en hospitales europeos
- Biosensor de antígeno detecta tuberculosis activa en una hora
- Panel rápido de susceptibilidad en hemocultivo amplía la cobertura para infecciones por gramnegativos
- Las características del microbioma oral e intestinal permiten identificar el cáncer gástrico temprano
- Un método de microscopía sin marcadores permite una detección más rápida y cuantitativa de la malaria
- Prueba del microbioma intestinal predice la recurrencia del melanoma tras la cirugía
- Genes de resistencia a los antibióticos detectados en recién nacidos a las pocas horas de nacer
- Prueba rápida colorimétrica estratifica cepas de estafilococo virulentas y resistentes
- Panel sindrómico permite identificación rápida de infecciones del torrente sanguíneo
- Nuevo objetivo bacteriano identificado para la detección temprana del noma
- Prueba rápida de orina acelera la selección de antibióticos para infecciones del tracto urinario
- El análisis genómico vincula cepas estreptocócicas emergentes con infecciones específicas
- La OMS respalda las pruebas rápidas en el punto de atención para mejorar la detección de tuberculosis
Canales
Química Clínica
ver canal
Un sensor basado en sangre detecta los primeros signos de Alzheimer y Parkinson
La incidencia de la enfermedad de Alzheimer y la enfermedad de Parkinson está aumentando a medida que la población envejece; sin embargo, el diagnóstico se basa principalmente en los... Más
Biomarcadores de biopsia líquida podrían mejorar el diagnóstico de la epilepsia infantil
La epilepsia infantil sigue siendo un trastorno neurológico importante que requiere biomarcadores precisos y no invasivos, ya que las pruebas convencionales, como la electroencefalografía... Más
Biomarcador en líquido mejora el diagnóstico y monitoreo del linfoma primario del SNC
El linfoma primario del sistema nervioso central (LPSNC) es una neoplasia maligna poco frecuente que afecta al cerebro, la médula espinal y los ojos, y que suele presentar un diagnóstico... Más
Nuevo valor de corte de CA19-9 ayuda a identificar pacientes con cáncer de páncreas de alto riesgo
El adenocarcinoma ductal pancreático (PDAC) se diagnostica con frecuencia en una etapa avanzada y sigue siendo uno de los tumores sólidos más letales. Los médicos suelen utilizar el antígeno carbohidrato... MásDiagnóstico Molecular
ver canal
Prueba sanguínea ultrasensible de MRD detecta recurrencia temprana del cáncer de mama
SAGA Diagnostics (Morrisville, Carolina del Norte, EE. UU.), una empresa especializada en la detección del cáncer basada en análisis de sangre e información tumoral, y en medicina... Más
Nuevo método de ARN origami facilita pruebas más rápidas para trastornos por expansión de repeticiones
Los trastornos de expansión de repeticiones causan afecciones como la distrofia miotónica, la enfermedad de Huntington y la esclerosis lateral amiotrófica (ELA), pero determinar con... Más
La FDA aprueba panel ampliado de biopsia líquida para el perfilado del cáncer avanzado
La caracterización tumoral oportuna y exhaustiva ayuda a los médicos a tomar decisiones sobre el tratamiento de pacientes con cáncer avanzado. Los métodos basados en muestras... Más
Prueba ampliada de genotipificación de DPYD ayuda a dosificar la quimioterapia de forma más segura
Las fluoropirimidinas, como el 5-fluorouracilo (5-FU), son fármacos de quimioterapia prescritos a más de dos millones de pacientes con cáncer cada año. Sin embargo, entre el 10 % y el 20 % de los pacientes... MásHematología
ver canal
Un umbral de ferritina más elevado podría mejorar la detección de deficiencia de hierro en niños
La deficiencia de hierro en niños en edad escolar puede afectar el desarrollo cerebral, el aprendizaje, el crecimiento y el rendimiento físico; sin embargo, la detección temprana de... Más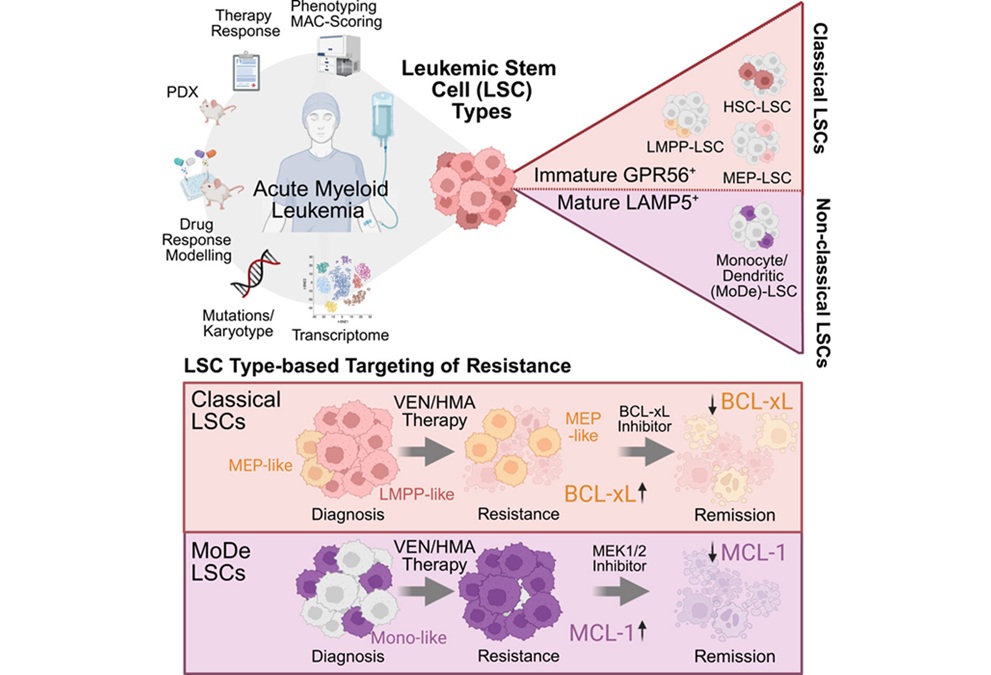
Los biomarcadores de células madre podrían orientar el tratamiento en la leucemia mieloide aguda
La leucemia mieloide aguda (LMA) es un cáncer de sangre agresivo que afecta con mayor frecuencia a adultos mayores y que, a pesar de los avances terapéuticos, aún presenta un pronóstico... MásInmunología
ver canal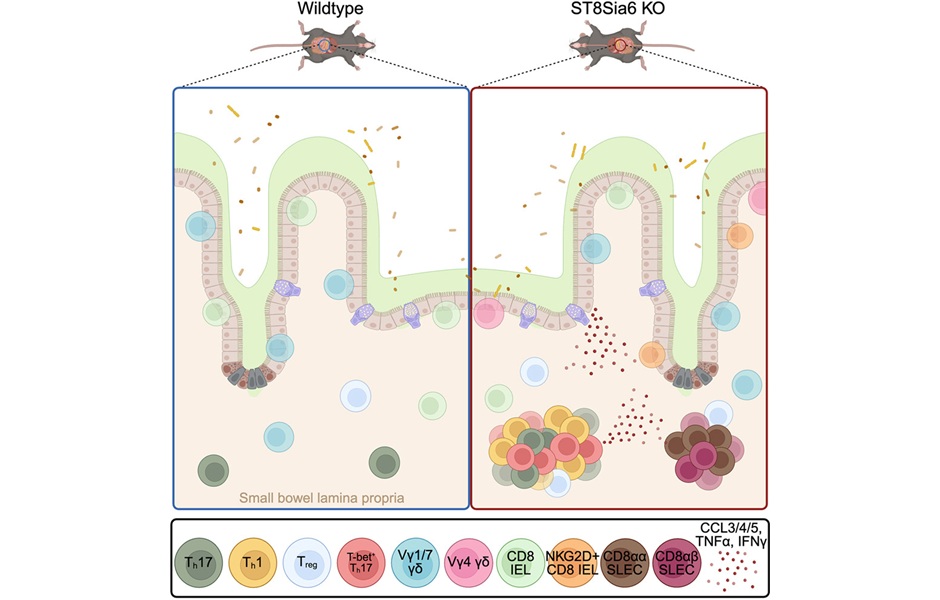
Enzima inmunitaria se vincula con la enfermedad inflamatoria intestinal resistente al tratamiento
La enfermedad inflamatoria intestinal (EII) afecta a casi 3 millones de personas en Estados Unidos y su prevalencia sigue en aumento. Los medicamentos que actúan sobre el factor de necrosis tumoral... Más
Análisis de sangre simple podría reemplazar biopsias para monitorizar el rechazo del trasplante pulmonar
Los receptores de trasplante de pulmón presentan algunas de las tasas más altas de rechazo celular agudo, y la vigilancia rutinaria suele basarse en biopsias quirúrgicas repetidas.... MásPatología
ver canal
Herramienta de IA extrae señales inmunitarias de biopsias para orientar la terapia del mieloma
El mieloma múltiple es una neoplasia maligna de la médula ósea en la que los pacientes pueden responder de forma muy diferente a los mismos tratamientos, lo que dificulta la toma de... Más
Prueba de patología con IA recibe designación de avance de la FDA para riesgo de cáncer de vejiga
El cáncer de vejiga no músculo-invasivo presenta resultados muy variables, lo que complica la vigilancia y la planificación del tratamiento. La evaluación del riesgo suele basarse en el estadio, el grado... Más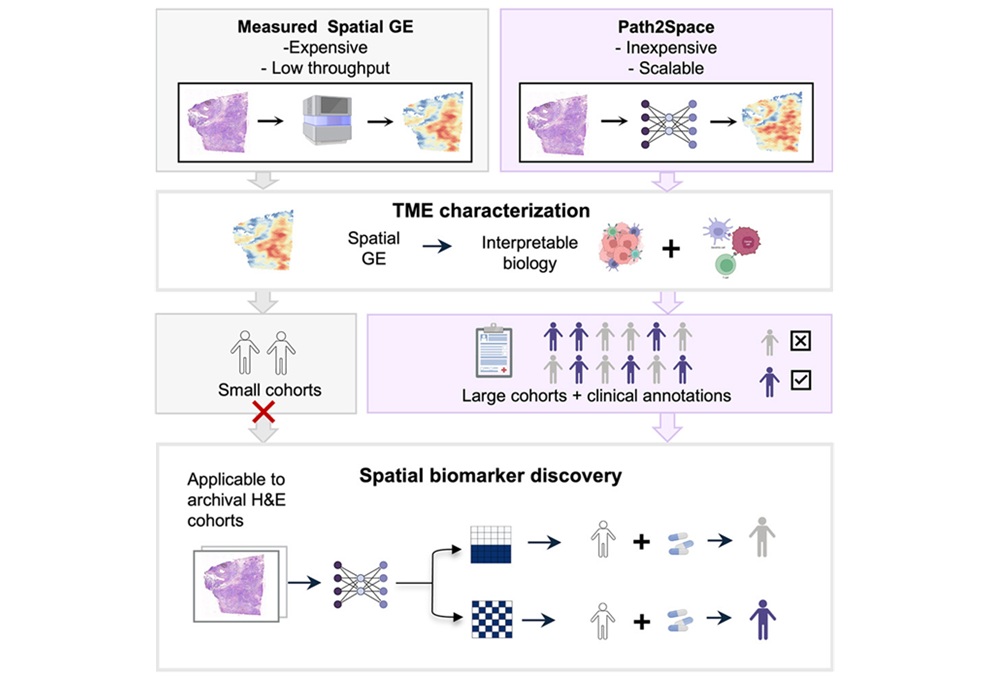
Herramienta de IA predice la expresión génica espacial del cáncer a partir de imágenes de patología
El análisis de la expresión génica puede aportar información sobre la biología tumoral y la selección del tratamiento, pero los ensayos espaciales siguen siendo... Más
Herramienta de patología digital con IA para la estratificación del riesgo en cáncer de mama
La evaluación del riesgo en el momento del diagnóstico es fundamental para guiar el tratamiento del cáncer de mama invasivo en estadio temprano, con receptor hormonal positivo y receptor 2 del factor de... MásTecnología
ver canal
Flujo de trabajo totalmente automatizado de muestra a resultado impulsa las pruebas de TB latente
La detección de la tuberculosis latente sigue representando una carga de trabajo considerable para los laboratorios clínicos a medida que se expanden los programas de cribado.... Más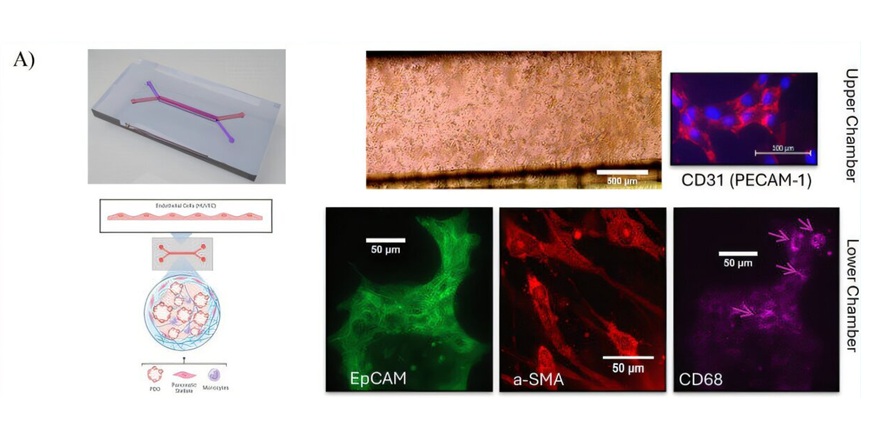
Plataforma de 'tumor en un chip' modela la respuesta al tratamiento del cáncer de páncreas
El cáncer de páncreas sigue siendo uno de los tipos de cáncer más difíciles de tratar, ya que los tumores se encuentran inmersos en un microambiente denso que influye... MásIndustria
ver canal
Fujifilm integra informes estructurados en el flujo de trabajo de patología digital
FUJIFILM Healthcare Americas Corporation (Lexington, MA, EE. UU.) y mTuitive (Centerville, MA, EE. UU.) han establecido una alianza estratégica para integrar la plataforma de informes de patología... Más