Prueba del mismo día identifica infecciones secundarias en pacientes de COVID-19
|
Por el equipo editorial de LabMedica en español Actualizado el 01 Dec 2021 |

Imagen: Metagenómica clínica (CMg) mediante secuenciación de nanoporos (Fotografía cortesía de Oxford Nanopore Technologies)
La unidad de cuidados intensivos (UCI) es un entorno dinámico con contacto frecuente entre el personal y el paciente para la monitorización invasiva, las intervenciones y el cuidado personal que, en conjunto, presentan el riesgo de infección secundaria o nosocomial. Cuando se atiende a pacientes críticamente enfermos en la UCI, los médicos pueden tomar muestras profundas de sus pulmones.
Actualmente, las muestras se envían a menudo a varios laboratorios donde se realizan diferentes cultivos bacterianos y fúngicos junto con otras pruebas moleculares complejas. Los resultados iniciales tardan de dos a cuatro días en saberse. El SARS-CoV-2 ha ejercido una presión considerable sobre las UCI, lo que tiene el potencial de aumentar la infección nosocomial, el tratamiento antimicrobiano y la resistencia a los antimicrobianos (RAM).
Un equipo de especialistas en enfermedades infecciosas dirigido por los del Hospital Guy y St. Thomas (Londres, Reino Unido), procesó muestras respiratorias clínicas sobrantes de 34 pacientes de la UCI con COVID-19, con sospecha de infecciones secundarias. Las muestras procesadas por el laboratorio clínico incluyeron muestras clínicas respiratorias (aspirados traqueales, lavados broncoalveolares (LBA) y lavados broncoalveolares no directos (NDL, un LBA recolectado sin el uso de un broncoscopio) para (i) cultivo microbiológico de rutina para patógenos bacterianos y fúngicos o detección de SARS-CoV-2 por PCR y (ii) sueros y LBA para la detección del antígeno de galactomanano (GM) cuando se sospecha una infección por Aspergillus.
Se prepararon placas de agar Sabouraud para la detección de Candida spp. y Aspergillus spp. y se incubaron durante cinco días a 37°C en condiciones aeróbicas. Las colonias bacterianas se identificaron utilizando MALDI-TOF (Bruker, Billerica, MA, EUA) excepto en el caso de Aspergillus spp. donde se realizó la microscopía. Se evaluó la metagenómica clínica (CMg) mediante secuenciación de nanoporos (Oxford Nanopore Technologies, Oxford Science Park, Reino Unido) en un estudio de prueba de concepto en 43 muestras respiratorias de 34 pacientes intubados, en siete unidades de cuidados intensivos (UCI) durante un período de 9 semanas durante la primera ola pandémica de COVID-19. El tamaño de los fragmentos y la calidad de las bibliotecas metagenómicas se analizaron mediante la plataforma de electroforesis automatizada TapeStation 4200 (Agilent Technologies, Santa Clara, CA, EUA).
Los investigadores informaron que un flujo de trabajo de CMg de 8 horas fue 92% sensible y 82% específico para la identificación bacteriana basada en muestras con cultivo positivo y cultivo negativo, respectivamente. La secuenciación de CMg informó la presencia o ausencia de genes β-lactámicos resistentes portados por Enterobacteriales que modificarían los antibióticos iniciales recomendados por las guías en todos los casos. CMg también fue 100% concordante con la PCR cuantitativa para detectar Aspergillus fumigatus de cuatro muestras positivas y 39 negativas. La tipificación molecular mediante datos de secuenciación de 24 horas identificó un brote de Klebsiella pneumoniae ST307 multirresistente que involucró a cuatro pacientes y un brote de Corynebacterium striatum multirresistente que involucró a 14 pacientes en tres UCI.
Jonathan D. Edgeworth, PhD, microbiólogo consultor y autor principal del estudio, dijo: “Tan pronto como comenzó la pandemia, nuestros científicos se dieron cuenta de que sería beneficioso secuenciar los genomas de todas las bacterias y hongos que causan infecciones en pacientes con COVID-19 mientras se encuentran en la UCI. En unas pocas semanas, demostramos que pueden diagnosticar infecciones secundarias, dirigir el tratamiento con antibióticos y detectar brotes mucho antes que las tecnologías actuales, todo a partir de una sola muestra”.
Los autores concluyeron que las pruebas de CMg proporcionan una detección exacta de patógenos y una predicción de la resistencia a los antibióticos en un flujo de trabajo de laboratorio del mismo día, con genomas ensamblados disponibles al día siguiente para la vigilancia genómica. La oferta de esta tecnología en un entorno de servicio podría cambiar fundamentalmente el enfoque del equipo multidisciplinario para manejar las infecciones de la UCI. El potencial para mejorar el tratamiento inicial dirigido y detectar rápidamente brotes insospechados de patógenos multirresistentes justifica una evaluación clínica más rápida de CMg. El estudio fue publicado el 17 de noviembre de 2021 en la revista Genome Medicine.
Enlace relacionado:
Hospital Guy y St. Thomas
Oxford Nanopore Technologies
Agilent Technologies
Actualmente, las muestras se envían a menudo a varios laboratorios donde se realizan diferentes cultivos bacterianos y fúngicos junto con otras pruebas moleculares complejas. Los resultados iniciales tardan de dos a cuatro días en saberse. El SARS-CoV-2 ha ejercido una presión considerable sobre las UCI, lo que tiene el potencial de aumentar la infección nosocomial, el tratamiento antimicrobiano y la resistencia a los antimicrobianos (RAM).
Un equipo de especialistas en enfermedades infecciosas dirigido por los del Hospital Guy y St. Thomas (Londres, Reino Unido), procesó muestras respiratorias clínicas sobrantes de 34 pacientes de la UCI con COVID-19, con sospecha de infecciones secundarias. Las muestras procesadas por el laboratorio clínico incluyeron muestras clínicas respiratorias (aspirados traqueales, lavados broncoalveolares (LBA) y lavados broncoalveolares no directos (NDL, un LBA recolectado sin el uso de un broncoscopio) para (i) cultivo microbiológico de rutina para patógenos bacterianos y fúngicos o detección de SARS-CoV-2 por PCR y (ii) sueros y LBA para la detección del antígeno de galactomanano (GM) cuando se sospecha una infección por Aspergillus.
Se prepararon placas de agar Sabouraud para la detección de Candida spp. y Aspergillus spp. y se incubaron durante cinco días a 37°C en condiciones aeróbicas. Las colonias bacterianas se identificaron utilizando MALDI-TOF (Bruker, Billerica, MA, EUA) excepto en el caso de Aspergillus spp. donde se realizó la microscopía. Se evaluó la metagenómica clínica (CMg) mediante secuenciación de nanoporos (Oxford Nanopore Technologies, Oxford Science Park, Reino Unido) en un estudio de prueba de concepto en 43 muestras respiratorias de 34 pacientes intubados, en siete unidades de cuidados intensivos (UCI) durante un período de 9 semanas durante la primera ola pandémica de COVID-19. El tamaño de los fragmentos y la calidad de las bibliotecas metagenómicas se analizaron mediante la plataforma de electroforesis automatizada TapeStation 4200 (Agilent Technologies, Santa Clara, CA, EUA).
Los investigadores informaron que un flujo de trabajo de CMg de 8 horas fue 92% sensible y 82% específico para la identificación bacteriana basada en muestras con cultivo positivo y cultivo negativo, respectivamente. La secuenciación de CMg informó la presencia o ausencia de genes β-lactámicos resistentes portados por Enterobacteriales que modificarían los antibióticos iniciales recomendados por las guías en todos los casos. CMg también fue 100% concordante con la PCR cuantitativa para detectar Aspergillus fumigatus de cuatro muestras positivas y 39 negativas. La tipificación molecular mediante datos de secuenciación de 24 horas identificó un brote de Klebsiella pneumoniae ST307 multirresistente que involucró a cuatro pacientes y un brote de Corynebacterium striatum multirresistente que involucró a 14 pacientes en tres UCI.
Jonathan D. Edgeworth, PhD, microbiólogo consultor y autor principal del estudio, dijo: “Tan pronto como comenzó la pandemia, nuestros científicos se dieron cuenta de que sería beneficioso secuenciar los genomas de todas las bacterias y hongos que causan infecciones en pacientes con COVID-19 mientras se encuentran en la UCI. En unas pocas semanas, demostramos que pueden diagnosticar infecciones secundarias, dirigir el tratamiento con antibióticos y detectar brotes mucho antes que las tecnologías actuales, todo a partir de una sola muestra”.
Los autores concluyeron que las pruebas de CMg proporcionan una detección exacta de patógenos y una predicción de la resistencia a los antibióticos en un flujo de trabajo de laboratorio del mismo día, con genomas ensamblados disponibles al día siguiente para la vigilancia genómica. La oferta de esta tecnología en un entorno de servicio podría cambiar fundamentalmente el enfoque del equipo multidisciplinario para manejar las infecciones de la UCI. El potencial para mejorar el tratamiento inicial dirigido y detectar rápidamente brotes insospechados de patógenos multirresistentes justifica una evaluación clínica más rápida de CMg. El estudio fue publicado el 17 de noviembre de 2021 en la revista Genome Medicine.
Enlace relacionado:
Hospital Guy y St. Thomas
Oxford Nanopore Technologies
Agilent Technologies
Últimas Microbiología noticias
- OMS recomienda pruebas POC, hisopos de lengua y agrupamiento de esputo para diagnóstico de TB
- Nuevo método de imágenes podría ayudar a predecir infecciones intestinales peligrosas
- La secuenciación rápida podría transformar la atención de la tuberculosis
- Virus intestinales ocultos vinculados al riesgo de cáncer colorrectal
- Panel de tres pruebas para detección de infecciones por duelas del hígado
- Prueba rápida promete respuestas inmediatas a infecciones resistentes a medicamentos
- Tecnología con CRISPR neutraliza bacterias resistentes a antibióticos
- Nuevo estudio identifica características del microbioma intestinal asociadas con enfermedad de Alzheimer
- Plataforma de IA permite detección rápida de patógenos de C. auris resistentes a fármacos
- Nueva prueba mide eficacia de antibióticos para eliminar bacterias
- Nuevas normas para antimicrobianos atienden tuberculosis para optimizar diagnóstico
- Método de diagnóstico de ITU ofrece resultados de resistencia a antibióticos 24 horas antes
- Avances en análisis microbiano mejora predicción de enfermedades
- Método de diagnóstico en sangre identifica infecciones IVRI pediátricas
- Prueba de diagnóstico rápido es estándar de oro para detección de sepsis
- Prueba rápida de tuberculosis POC proporciona resultados en 15 minutos
Canales
Química Clínica
ver canal
Un sensor de IA detecta trastornos neurológicos con una sola gota de saliva
Trastornos neurológicos como el Parkinson y el Alzheimer suelen desarrollarse gradualmente y presentar síntomas sutiles en sus primeras etapas. Dado que los signos tempranos suelen ser vagos... MásNuevo índice sanguíneo permite la detección más temprana de la fibrosis hepática
La enfermedad del hígado graso metabólico es muy prevalente y a menudo asintomática; sin embargo, puede progresar a fibrosis, cirrosis e insuficiencia hepática.... MásDiagnóstico Molecular
ver canal
Huella inmunitaria en sangre predice efectos secundarios de nuevos fármacos para Alzheimer
Las nuevas terapias con anticuerpos para la enfermedad de Alzheimer han demostrado ser prometedoras para ralentizar su progresión, pero su uso generalizado se ha visto limitado por un efecto secundario... Más
Análisis de sangre predice demencia en mujeres hasta 25 años antes del inicio de los síntomas
La demencia y la enfermedad de Alzheimer suelen desarrollarse silenciosamente durante muchos años antes de que aparezcan los síntomas. Detectar el riesgo con antelación permitiría... MásHematología
ver canal
Prueba rápida en cartuchos busca ampliar acceso al diagnóstico de trastornos de hemoglobina
La anemia de células falciformes y la beta talasemia son trastornos de la hemoglobina que a menudo requieren la derivación a laboratorios especializados para un diagnóstico definitivo,... Más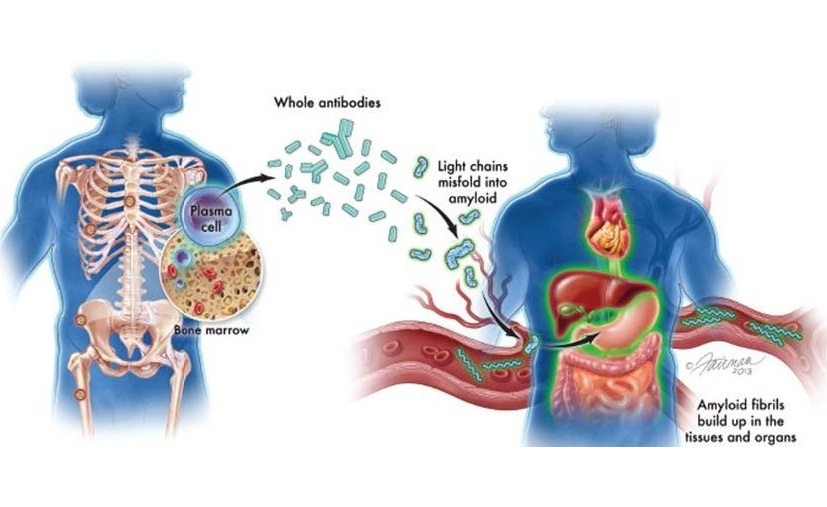
Nuevas directrices buscan mejorar diagnóstico de amiloidosis AL
La amiloidosis de cadenas ligeras (AL) es un trastorno poco común y potencialmente mortal de la médula ósea, en el que las proteínas amiloides anormales se acumulan en los órganos. Aproximadamente 3.... MásInmunología
ver canal
Firmas de mutación del cáncer mejoran la predicción de la respuesta a inmunoterapia
Las células cancerosas acumulan miles de mutaciones genéticas, pero no todas afectan a los tumores de la misma manera. Algunas hacen que las células cancerosas sean más visibles... Más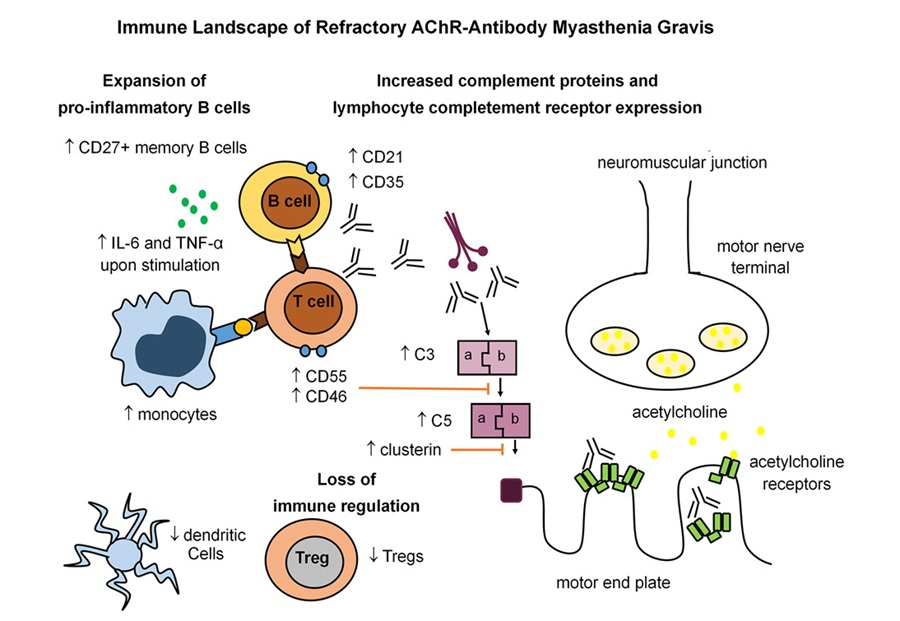
Firma inmunitaria identificada en miastenia gravis resistente al tratamiento
La miastenia gravis es un trastorno autoinmune poco común en el que el ataque inmunitario a la unión neuromuscular causa debilidad fluctuante que puede afectar la visión, el movimiento,... MásPatología
ver canal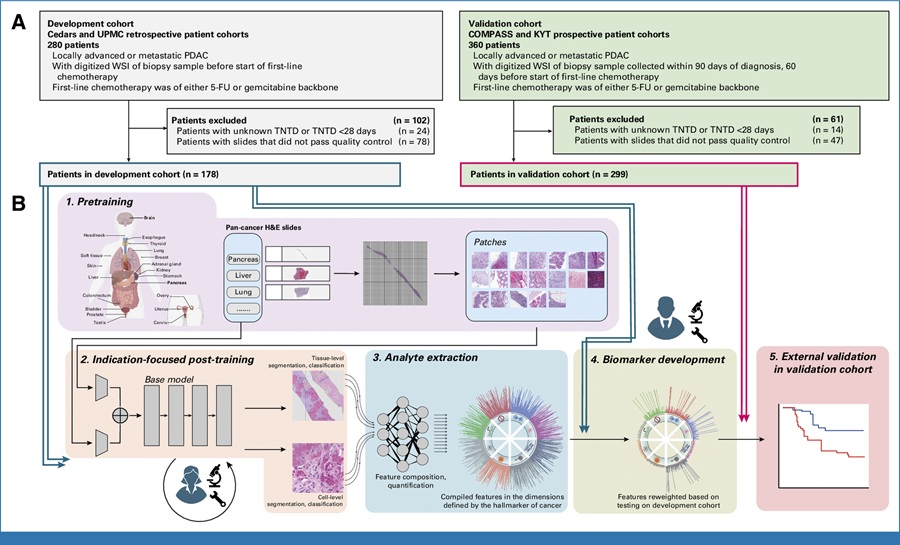
Herramienta de IA predice la respuesta a la quimioterapia a partir de portaobjetos de biopsia
La selección de la quimioterapia de primera línea para el cáncer de páncreas avanzado generalmente implica probar uno de dos regímenes aprobados y cambiarlo si la respuesta... Más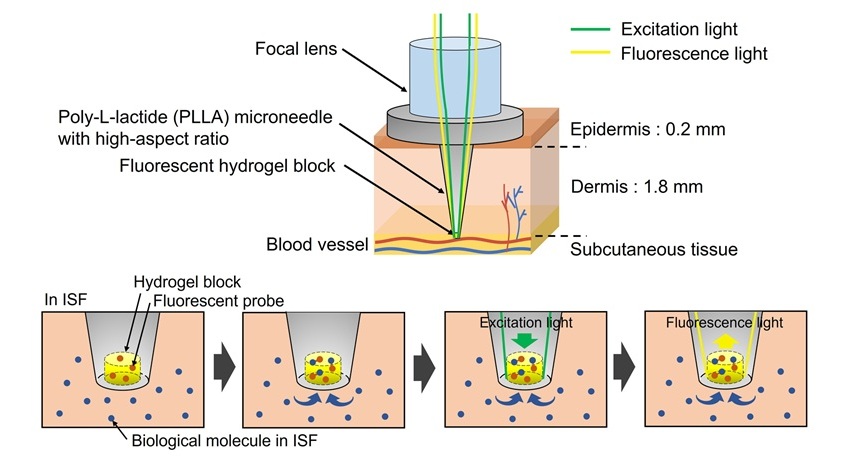
Primer dispositivo óptico con microagujas del mundo permite pruebas clínicas sin extracción de sangre
La extracción de sangre es uno de los procedimientos clínicos más comunes, pero puede resultar difícil o incómoda para muchos pacientes, especialmente para los adultos... MásTecnología
ver canal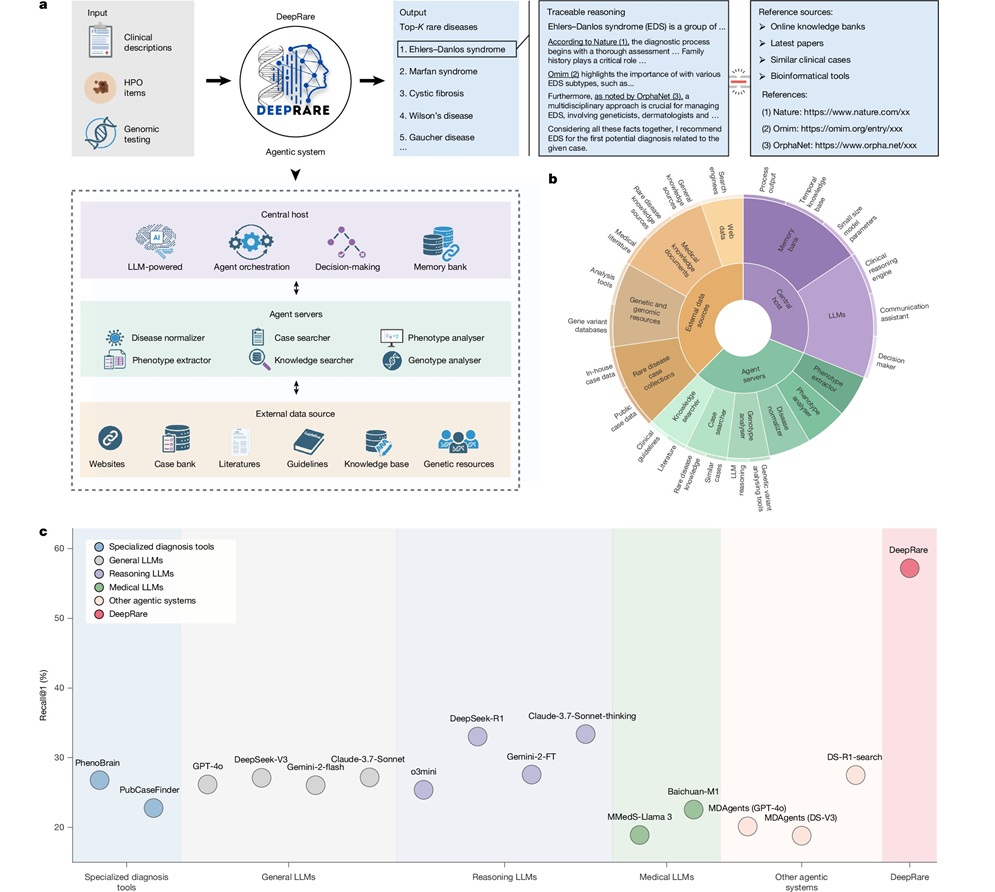
Modelo de IA supera a clínicos en la detección de enfermedades raras
Se estima que las enfermedades raras afectan a 300 millones de personas en todo el mundo; sin embargo, el diagnóstico suele ser largo y propenso a errores. Muchas de estas afecciones presentan signos... Más
Diagnóstico por IA demuestra alta precisión en detección de infecciones articulares periprotésicas
La infección articular periprotésica (IAP) es una complicación poco frecuente pero grave que afecta entre el 1 % y el 2 % de las cirugías primarias de reemplazo articular.... MásIndustria
ver canal
Agilent Technologies adquiere la empresa de diagnóstico patológico Biocare Medical
Agilent Technologies (Santa Clara, California, EE. UU.) ha firmado un acuerdo definitivo para adquirir Biocare Medical (Pacheco, California, EE. UU.), ampliando así su cartera de productos de p... Más