La secuenciación del genoma completo ayuda al diagnóstico de enfermedades raras
|
Por el equipo editorial de LabMedica en español Actualizado el 13 Apr 2021 |

Imagen: El analizador MassARRAY Dx es un analizador genético multiplex de sobremesa que simplifica el entorno complejo de la genética clínica, con datos fáciles de interpretar, detección flexible de biomarcadores y desempeño robusto (Fotografía cortesía de Agena Biosciences)
Los diagnósticos de enfermedades genéticas están en revolución, debido a los descubrimientos en la tecnología de secuenciación y de análisis de datos. El potencial para transformar la medicina clínica usando la genómica es alto, especialmente dentro del ámbito de las enfermedades raras.
Las enfermedades raras constituyen un grupo grande y heterogéneo de diagnósticos que incluyen más de 8.000 condiciones distintas de las cuales la gran mayoría tiene una base genética. Cada enfermedad individual es rara, pero cuando se consideran como un grupo, las enfermedades raras son comunes con una prevalencia total de aproximadamente de 6% a 8%.
Científicos moleculares médicos del Instituto Karolinska (Estocolmo, Suecia) y sus colegas, secuenciaron los genomas de 3.219 pacientes en un programa de cinco años. La secuenciación clínica del genoma completo (SGC) fue implementada gradualmente en el Centro de Medicina Genómica Karolinska-Enfermedades Raras (GMCK-RD), en el transcurso de cinco años. Al inicio la secuenciación fue realizada en el HiSeq X Ten, pero se cambió al NovaSeq 6000 (Illumina, San Diego, CA, EUA) en diciembre de 2018.
Generalmente, las muestras fueron analizadas de manera escalonada, en las que primero se analizaron para variantes asociadas con la presunta enfermedad del paciente, algunas veces con paneles muy grandes de genes de aproximadamente 4.000 genes, ante de ser escaladas para análisis adicional o análisis de genoma completo, si no se hizo un diagnóstico. Para asegurar que no hay mezcla de la muestra durante el procesamiento de SGC, una alícuota del ADN extraído fue genotipificada para 51 SNPs usando tecnología MassARRAY (Agena Biosciences, San Diego, CA, EUA).
Los científicos descubrieron variantes en 754 genes de enfermedades diferentes, con la mayoría afectando comúnmente los genes COL2A1 y FKRP. Varias variantes también fueron recurrentes, algunas de las cuales eran mutaciones fundadoras conocidas, como Leu27Ile en FKRP, que fueron homocigotas en 12 personas con distrofia muscular de la cintura de las extremidades, y expansiones homocigotas en el gen RFC1 entre personas con ataxia cerebelosa, neuropatía, y síndrome de arreflexia vestibular. Sin embargo, otros pacientes tenían variantes que se sabe surgen recurrentemente como mutaciones de novo, como una que afecta el gen PRRT2 que causa convulsiones.
Para algunos pacientes tener un diagnóstico molecular puede cambiar su tratamiento. Como señaló el equipo, pacientes con errores innatos del metabolismo de inicio agudo con frecuencia se tratan con infusión de glucosa, pero para los pacientes con deficiencia de piruvato deshidrogenasa, esto puede ser peligroso. En cambio, esos pacientes son tratados con una dieta cetogénica. Los científicos generaron diagnósticos moleculares para 1.287 pacientes, o 40%, con un tiempo medio de entrega de resultados de 13 días.
Anna Wedell, MD, PhD, una profesora de medicina molecular y cirugía y una coautora senior del estudio, dijo: “La mayoría de los pacientes no se habrían sometido a investigaciones genéticas con los métodos convencionales. Hemos integrado WGS profundamente en la clínica, haciendo que la genómica esté disponible en escenarios completamente nuevos incluyendo las situaciones médicas agudas para una amplia gama de grupos de enfermedades”. El estudio fue publicado el 17 de marzo de 2021 en la revista “Genome Medicine”.
Enlace relacionado:
Instituto Karolinska
Illumina
Agena Biosciences
Las enfermedades raras constituyen un grupo grande y heterogéneo de diagnósticos que incluyen más de 8.000 condiciones distintas de las cuales la gran mayoría tiene una base genética. Cada enfermedad individual es rara, pero cuando se consideran como un grupo, las enfermedades raras son comunes con una prevalencia total de aproximadamente de 6% a 8%.
Científicos moleculares médicos del Instituto Karolinska (Estocolmo, Suecia) y sus colegas, secuenciaron los genomas de 3.219 pacientes en un programa de cinco años. La secuenciación clínica del genoma completo (SGC) fue implementada gradualmente en el Centro de Medicina Genómica Karolinska-Enfermedades Raras (GMCK-RD), en el transcurso de cinco años. Al inicio la secuenciación fue realizada en el HiSeq X Ten, pero se cambió al NovaSeq 6000 (Illumina, San Diego, CA, EUA) en diciembre de 2018.
Generalmente, las muestras fueron analizadas de manera escalonada, en las que primero se analizaron para variantes asociadas con la presunta enfermedad del paciente, algunas veces con paneles muy grandes de genes de aproximadamente 4.000 genes, ante de ser escaladas para análisis adicional o análisis de genoma completo, si no se hizo un diagnóstico. Para asegurar que no hay mezcla de la muestra durante el procesamiento de SGC, una alícuota del ADN extraído fue genotipificada para 51 SNPs usando tecnología MassARRAY (Agena Biosciences, San Diego, CA, EUA).
Los científicos descubrieron variantes en 754 genes de enfermedades diferentes, con la mayoría afectando comúnmente los genes COL2A1 y FKRP. Varias variantes también fueron recurrentes, algunas de las cuales eran mutaciones fundadoras conocidas, como Leu27Ile en FKRP, que fueron homocigotas en 12 personas con distrofia muscular de la cintura de las extremidades, y expansiones homocigotas en el gen RFC1 entre personas con ataxia cerebelosa, neuropatía, y síndrome de arreflexia vestibular. Sin embargo, otros pacientes tenían variantes que se sabe surgen recurrentemente como mutaciones de novo, como una que afecta el gen PRRT2 que causa convulsiones.
Para algunos pacientes tener un diagnóstico molecular puede cambiar su tratamiento. Como señaló el equipo, pacientes con errores innatos del metabolismo de inicio agudo con frecuencia se tratan con infusión de glucosa, pero para los pacientes con deficiencia de piruvato deshidrogenasa, esto puede ser peligroso. En cambio, esos pacientes son tratados con una dieta cetogénica. Los científicos generaron diagnósticos moleculares para 1.287 pacientes, o 40%, con un tiempo medio de entrega de resultados de 13 días.
Anna Wedell, MD, PhD, una profesora de medicina molecular y cirugía y una coautora senior del estudio, dijo: “La mayoría de los pacientes no se habrían sometido a investigaciones genéticas con los métodos convencionales. Hemos integrado WGS profundamente en la clínica, haciendo que la genómica esté disponible en escenarios completamente nuevos incluyendo las situaciones médicas agudas para una amplia gama de grupos de enfermedades”. El estudio fue publicado el 17 de marzo de 2021 en la revista “Genome Medicine”.
Enlace relacionado:
Instituto Karolinska
Illumina
Agena Biosciences
Últimas Diagnóstico Molecular noticias
- Análisis de sangre sencillo permite detectar múltiples enfermedades a partir de una sola muestra
- Prueba rápida de RT-PCR en el punto de atención diferencia influenza A/B y SARS-CoV-2 en minutos
- Prueba de ADNtc en sangre mejora la evaluación del cáncer de garganta relacionado con el VPH
- Análisis del ARN revela dianas terapéuticas en tumores sólidos
- Prueba identifica pacientes con cáncer de mama que podrían evitar la cirugía
- La secuenciación del genoma completo en la atención médica rutinaria amplía la detección de enfermedades raras
- Nueva herramienta de IA mejora la detección de causas genéticas en enfermedades raras
- Plataforma de PCR adaptativa mejora la consistencia en flujos de trabajo de NGS de lotes pequeños
- Nueva prueba molecular mejora la precisión del diagnóstico del cáncer de vías biliares
- Prueba portátil basada en CRISPR permite identificar rápidamente ITS y marcadores de resistencia
- Prueba de ADN tumoral circulante en plasma predice recurrencia en cáncer de mama tras terapia neoadyuvante
- Nuevo panel respiratorio amplía la detección de patógenos a 25 objetivos
- Un simple hisopado nasal podría revelar signos tempranos de la enfermedad de Alzheimer
- Biomarcador en sangre predice los resultados cognitivos tras paro cardíaco
- Análisis de sangre ayuda a orientar tratamiento en mujeres mayores con cáncer de mama
- Una biopsia líquida permite un diagnóstico más rápido del cáncer infantil en África
Canales
Química Clínica
ver canal
Prueba de metabolitos en sangre detecta deterioro cognitivo temprano
La identificación temprana de personas con riesgo de demencia sigue siendo difícil, ya que los síntomas suelen aparecer solo después de una neurodegeneración significativa.... MásAnalizadores automatizados de nueva generación aumentan el rendimiento en química clínica y pruebas de electrolitos
Los laboratorios clínicos siguen enfrentándose a la escasez de personal, el espacio limitado y el creciente volumen de pruebas, lo que ejerce presión sobre los flujos de trabajo de... Más
Análisis de sangre basado en IA detecta múltiples trastornos cerebrales a partir de una sola muestra
Diagnosticar la causa de los síntomas cognitivos relacionados con la edad sigue siendo un desafío, ya que las manifestaciones clínicas de las enfermedades neurodegenerativas a menudo se superponen y pueden... MásHematología
ver canal
Plataforma abierta de multiómica identifica subtipos pronósticos en cánceres hematológicos
Los cánceres hematológicos abarcan diversas entidades cuya biología y comportamiento clínico se comprenden mejor mediante análisis integradores en grandes cohortes.... Más
Prueba rápida en cartuchos busca ampliar acceso al diagnóstico de trastornos de hemoglobina
La anemia de células falciformes y la beta talasemia son trastornos de la hemoglobina que a menudo requieren la derivación a laboratorios especializados para un diagnóstico definitivo,... MásInmunología
ver canalMétodo de cribado combinado permite identificar casos de lepra en etapas tempranas
La lepra sigue siendo un problema importante de salud pública, con más de 200.000 casos nuevos notificados anualmente en todo el mundo, y la enfermedad temprana a menudo escapa a la detección... Más
Prueba de anticuerpos en sangre identifica tuberculosis activa y distingue la infección latente
La tuberculosis activa (TB) sigue siendo una de las principales causas de muerte y enfermedad en todo el mundo; sin embargo, distinguir la enfermedad contagiosa de la infección latente continúa... MásMicrobiología
ver canal
Nuevo objetivo bacteriano identificado para la detección temprana del noma
La noma es una infección orofacial de rápida progresión que comienza como gingivitis y puede destruir los tejidos orales y faciales, afectando principalmente a niños pequeños... Más
Prueba rápida de orina acelera la selección de antibióticos para infecciones del tracto urinario
Las infecciones del tracto urinario son una causa frecuente de prescripción de antibióticos y han provocado más de 800.000 hospitalizaciones en Inglaterra en los últimos cinco... Más
El análisis genómico vincula cepas estreptocócicas emergentes con infecciones específicas
Las infecciones por Streptococcus dysgalactiae subespecie equisimilis (SDSE) están aumentando en todo el mundo e incluyen variantes que pueden provocar enfermedades graves. Investigadores informan... Más
La OMS respalda las pruebas rápidas en el punto de atención para mejorar la detección de tuberculosis
La tuberculosis (TB) sigue siendo una de las principales causas de muerte por enfermedades infecciosas, con más de 3.300 fallecimientos y 29.000 nuevos casos diarios. Los retrasos en el diagnóstico... MásPatología
ver canal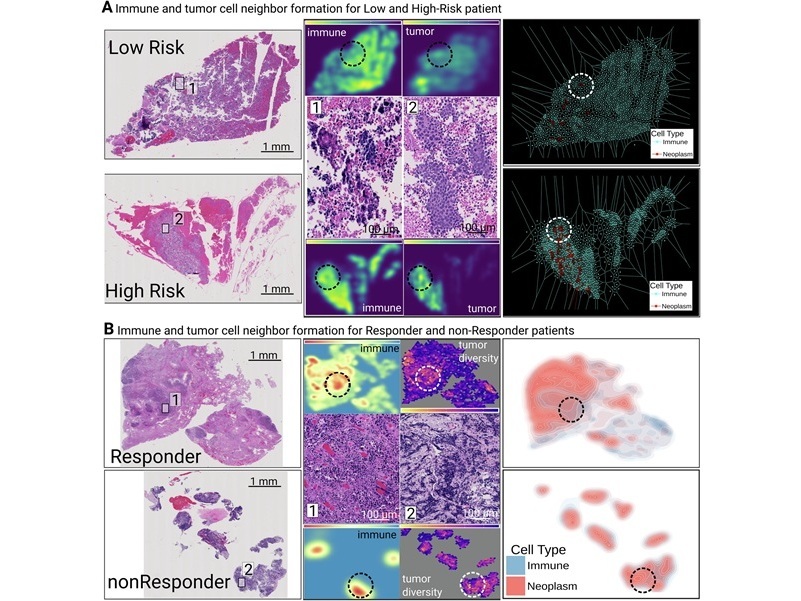
Herramienta de IA predice respuesta a la quimioterapia en cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas suele presentarse en una etapa avanzada y progresa rápidamente, lo que deja poco tiempo para personalizar la terapia de primera línea. Actualmente, los médicos carecen... Más_image.png)
Biomarcador tumoral específico predice respuesta a inmunoterapia neoadyuvante en cáncer gástrico
El cáncer gástrico es la quinta neoplasia maligna más común y la cuarta causa principal de mortalidad por cáncer en todo el mundo, y China soporta casi la mitad de la carga global.... Más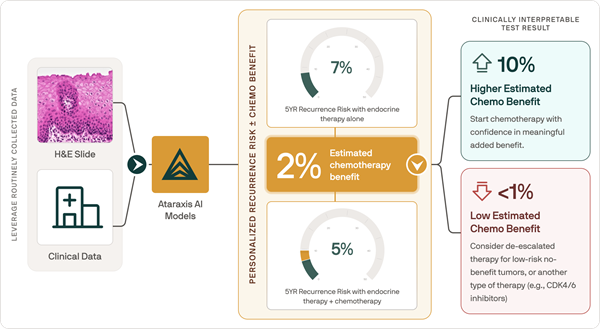
Nueva prueba de IA predice resultados de quimioterapia específicos para cada paciente con cáncer de mama
La selección de la quimioterapia adyuvante para el cáncer de mama en estadio temprano suele basarse en el riesgo de recurrencia y los promedios poblacionales, en lugar del beneficio individualizado... MásTecnología
ver canal
Nueva herramienta de IA permite seleccionar rápidamente el tratamiento en leucemia pediátrica
Los niños con leucemia linfoblástica aguda de células T se enfrentan a una enfermedad agresiva que sigue siendo difícil de tratar. Si bien las tasas de remisión han mejorado,... Más
Diseño innovador de espectrometría de masas podría permitir la detección de abundancias ultrabajas
La espectrometría de masas es fundamental para identificar y cuantificar moléculas en muestras biológicas complejas, pero los instrumentos convencionales suelen analizar los iones... MásIndustria
ver canal
Takara Bio USA y Hamilton se asocian para automatizar la preparación de bibliotecas NGS
Takara Bio USA, Inc. (San José, California, EE. UU.), una filial de propiedad total de Takara Bio Inc., y Hamilton Company (Reno, Nevada, EE. UU.) anunciaron un acuerdo de desarrollo y comercia... Más