Secuenciación podría complementar otros métodos de cribado de recién nacidos
|
Por el equipo editorial de LabMedica en español Actualizado el 16 Sep 2020 |
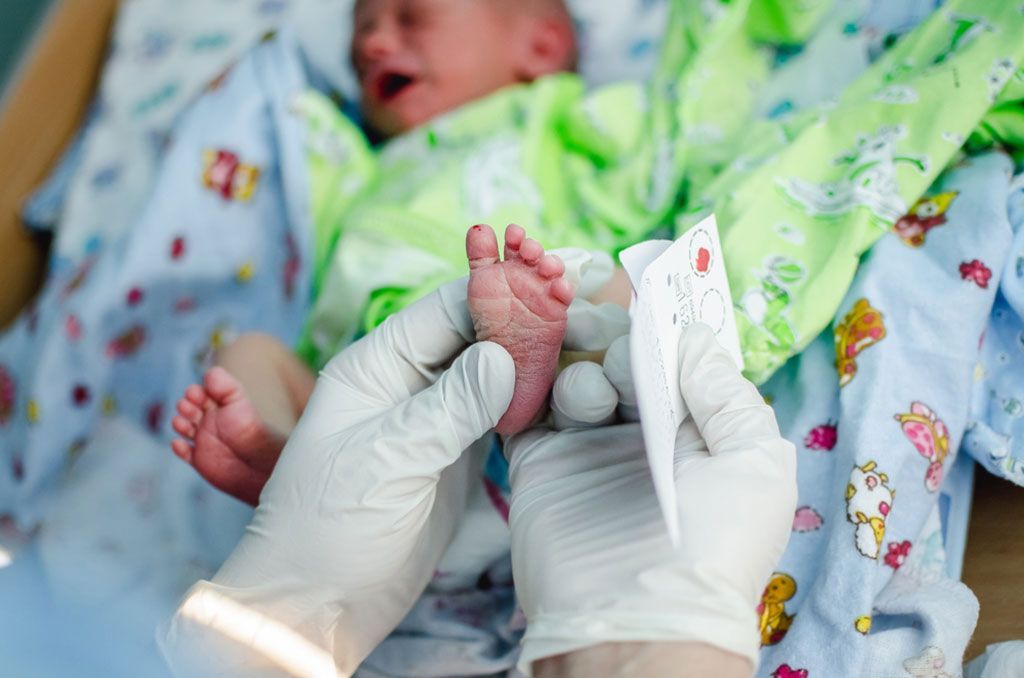
Imagen: La secuenciación del exoma del recién nacido podría complementar otros métodos de cribado de los recién nacidos (Fotografía cortesía de Sushytska).
El examen de cribado de los recién nacidos (NBS) se estableció como un programa de salud pública en la década de 1960 y es crucial para facilitar la detección de ciertas afecciones médicas en las que la intervención temprana puede prevenir problemas de salud graves y potencialmente mortales.
La secuenciación genómica puede expandir potencialmente la detección de trastornos hereditarios raros, pero muchas preguntas rodean su posible uso para este propósito. Es posible que los métodos basados en la secuenciación no reemplacen el cribado del recién nacido con base bioquímica o fenotípica, pero pueden complementar esos enfoques.
Los genetistas de la Universidad de Carolina del Norte en Chapel Hill (Chapel Hill, NC, EUA) y sus colegas, examinaron el uso de la secuenciación del exoma (SE) para el NBS en el proyecto de Cribado Universal para la Secuenciación del Exoma del Recién Nacido de Carolina del Norte (NC NEXUS), que compara el rendimiento de la SE utilizada en un contexto de detección versus diagnóstico. Reclutaron, en un estudio, a 17 niños con errores innatos del metabolismo, 28 niños con pérdida auditiva y 61 bebés sanos. A cada niño se le realizó un cribado neonatal basado en secuenciación de próxima generación utilizando un panel de 466 genes. De las 46 variantes detectadas en esta cohorte mediante la secuenciación del exoma, 43 se confirmaron ortogonalmente en un laboratorio certificado por CLIA.
El equipo informó que, dentro de la cohorte metabólica, el cribado basado en secuenciación descubrió un resultado anormal en 15 de los 17 participantes. Por ejemplo, siete niños que tenían fenilcetonuria tenían variantes patológicas en HAP, siete niños con deficiencia de acil-coA deshidrogenasa de cadena media, tenían variantes patogénicas en ACADM y un niño con deficiencia primaria de carnitina era homocigoto para una variante patógena sin sentido de SLC22A5.
Sin embargo, en la cohorte de pérdida auditiva, el cribado neonatal basado en secuenciación de próxima generación arrojó resultados positivos solo en cinco de los 28 participantes. Entre ellos había dos niños que eran heterocigotos compuestos para variantes en un gen del síndrome de Usher y un niño que tenía una deleción de cambio de marco de un par de bases en el gen GJB2, que está relacionado con la sordera no sindrómica DFNB1.
En la cohorte completa, el cribado basado en la secuenciación identificó a cuatro niños con resultados positivos, una variante relacionada con la hipercolesterolemia familiar, una variante sin sentido asociada con una deficiencia leve de ornitina transcarbamilasa (OTC), una variante del sitio de empalme en DSC2 vinculada a la displasia ventricular derecha arritmogénica, autosómica, dominante y dos variantes de F11 relacionadas con la deficiencia autosómica recesiva del factor XI.
Los autores concluyeron que, dado que el cribado basado en secuenciación omitió algunos resultados metabólicos y de pérdida auditiva, probablemente no reemplazaría los métodos de cribado actuales, pero que se podía usar en conjunto con ellos. Estos hallazgos sugieren que la secuenciación podría ser útil como complemento de los métodos tradicionales de NBS y que con una mejor detección de variantes y bases de datos interpretativas más extensas, el valor predictivo positivo del cribado genómico puede mejorar. El estudio fue publicado el 26 de agosto de 2020 en la revista American Journal of Human Genetics.
Enlace relacionado:
Universidad de Carolina del Norte en Chapel Hill
La secuenciación genómica puede expandir potencialmente la detección de trastornos hereditarios raros, pero muchas preguntas rodean su posible uso para este propósito. Es posible que los métodos basados en la secuenciación no reemplacen el cribado del recién nacido con base bioquímica o fenotípica, pero pueden complementar esos enfoques.
Los genetistas de la Universidad de Carolina del Norte en Chapel Hill (Chapel Hill, NC, EUA) y sus colegas, examinaron el uso de la secuenciación del exoma (SE) para el NBS en el proyecto de Cribado Universal para la Secuenciación del Exoma del Recién Nacido de Carolina del Norte (NC NEXUS), que compara el rendimiento de la SE utilizada en un contexto de detección versus diagnóstico. Reclutaron, en un estudio, a 17 niños con errores innatos del metabolismo, 28 niños con pérdida auditiva y 61 bebés sanos. A cada niño se le realizó un cribado neonatal basado en secuenciación de próxima generación utilizando un panel de 466 genes. De las 46 variantes detectadas en esta cohorte mediante la secuenciación del exoma, 43 se confirmaron ortogonalmente en un laboratorio certificado por CLIA.
El equipo informó que, dentro de la cohorte metabólica, el cribado basado en secuenciación descubrió un resultado anormal en 15 de los 17 participantes. Por ejemplo, siete niños que tenían fenilcetonuria tenían variantes patológicas en HAP, siete niños con deficiencia de acil-coA deshidrogenasa de cadena media, tenían variantes patogénicas en ACADM y un niño con deficiencia primaria de carnitina era homocigoto para una variante patógena sin sentido de SLC22A5.
Sin embargo, en la cohorte de pérdida auditiva, el cribado neonatal basado en secuenciación de próxima generación arrojó resultados positivos solo en cinco de los 28 participantes. Entre ellos había dos niños que eran heterocigotos compuestos para variantes en un gen del síndrome de Usher y un niño que tenía una deleción de cambio de marco de un par de bases en el gen GJB2, que está relacionado con la sordera no sindrómica DFNB1.
En la cohorte completa, el cribado basado en la secuenciación identificó a cuatro niños con resultados positivos, una variante relacionada con la hipercolesterolemia familiar, una variante sin sentido asociada con una deficiencia leve de ornitina transcarbamilasa (OTC), una variante del sitio de empalme en DSC2 vinculada a la displasia ventricular derecha arritmogénica, autosómica, dominante y dos variantes de F11 relacionadas con la deficiencia autosómica recesiva del factor XI.
Los autores concluyeron que, dado que el cribado basado en secuenciación omitió algunos resultados metabólicos y de pérdida auditiva, probablemente no reemplazaría los métodos de cribado actuales, pero que se podía usar en conjunto con ellos. Estos hallazgos sugieren que la secuenciación podría ser útil como complemento de los métodos tradicionales de NBS y que con una mejor detección de variantes y bases de datos interpretativas más extensas, el valor predictivo positivo del cribado genómico puede mejorar. El estudio fue publicado el 26 de agosto de 2020 en la revista American Journal of Human Genetics.
Enlace relacionado:
Universidad de Carolina del Norte en Chapel Hill
Últimas Diagnóstico Molecular noticias
- Método de biopsia líquida identifica origen de la enfermedad con una sola gota de sangre
- Prueba rápida basada en respuesta del huésped distingue infecciones bacterianas y virales en minutos
- Un solo análisis de sangre predice las enfermedades cardíacas 15 años antes de su aparición
- Un analizador de precisión revela las "proteínas camaleónicas" que causan enfermedades
- Un estudio revela errores generalizados en la denominación de variantes genéticas
- Nuevos biomarcadores indican mayor riesgo de cáncer de hígado en pacientes con hepatitis B crónica
- Biomarcador sanguíneo de Alzheimer mejora detección de enfermedades cardíacas y renales
- Huella inmunitaria en sangre predice efectos secundarios de nuevos fármacos para Alzheimer
- Análisis de sangre predice demencia en mujeres hasta 25 años antes del inicio de los síntomas
- Prueba diagnóstica clínica detecta variantes genéticas adicionales en pacientes con leucemia aguda
- Aptámeros de ADN ofrecen nueva herramienta para un análisis de sangre sencillo para Alzheimer
- Las biopsias líquidas revelan resistencia a la terapia en cáncer de próstata metastásico
- Las pruebas rápidas de VRS reducen la prescripción de antibióticos en niños
- Biopsia líquida basada en IA detecta señales de fibrosis hepática, cirrosis y enfermedad crónica
- Análisis de sangre podría detectar preeclampsia antes de que aparezcan síntomas
- Análisis de sangre con IA detecta antes el riesgo de recaída tras trasplante
Canales
Química Clínica
ver canal
Primer inmunoensayo IVD para detectar variante genética de riesgo de Alzheimer recibe marcado CE
La enfermedad de Alzheimer representa hasta el 70 % de los casos de demencia en todo el mundo y se prevé que afecte a casi 150 millones de personas para 2050, lo que subraya la necesidad de dia... Más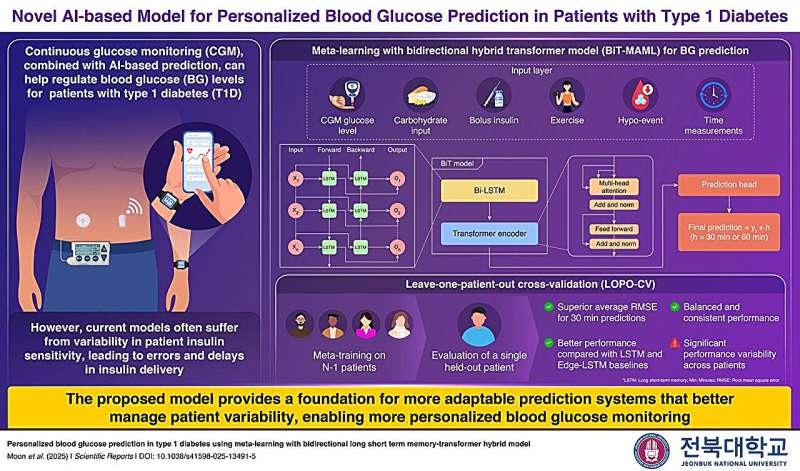
Modelo de IA permite predicciones personalizadas de glucosa en diabetes tipo 1
La diabetes tipo 1 (DT1) requiere un control riguroso de la glucosa en sangre y una dosificación precisa de insulina, ya que incluso pequeños errores pueden provocar fluctuaciones peligrosas.... MásHematología
ver canal
Prueba rápida en cartuchos busca ampliar acceso al diagnóstico de trastornos de hemoglobina
La anemia de células falciformes y la beta talasemia son trastornos de la hemoglobina que a menudo requieren la derivación a laboratorios especializados para un diagnóstico definitivo,... Más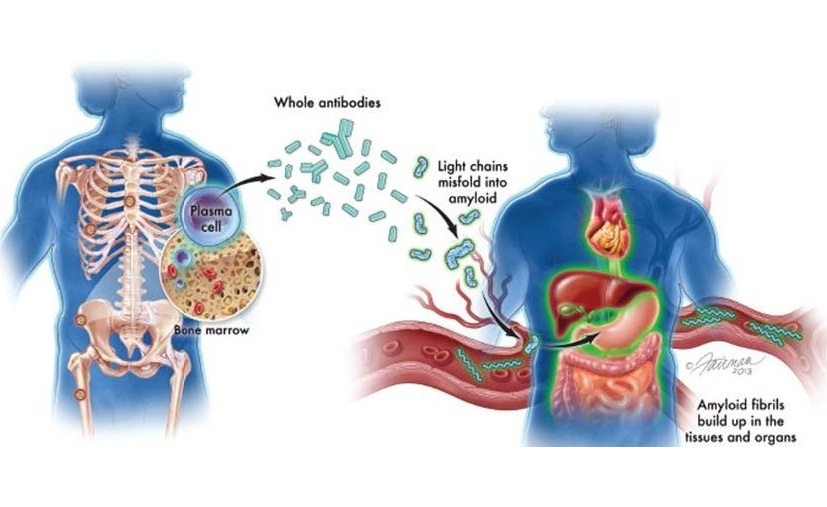
Nuevas directrices buscan mejorar diagnóstico de amiloidosis AL
La amiloidosis de cadenas ligeras (AL) es un trastorno poco común y potencialmente mortal de la médula ósea, en el que las proteínas amiloides anormales se acumulan en los órganos. Aproximadamente 3.... MásInmunología
ver canal
Firmas de mutación del cáncer mejoran la predicción de la respuesta a inmunoterapia
Las células cancerosas acumulan miles de mutaciones genéticas, pero no todas afectan a los tumores de la misma manera. Algunas hacen que las células cancerosas sean más visibles... Más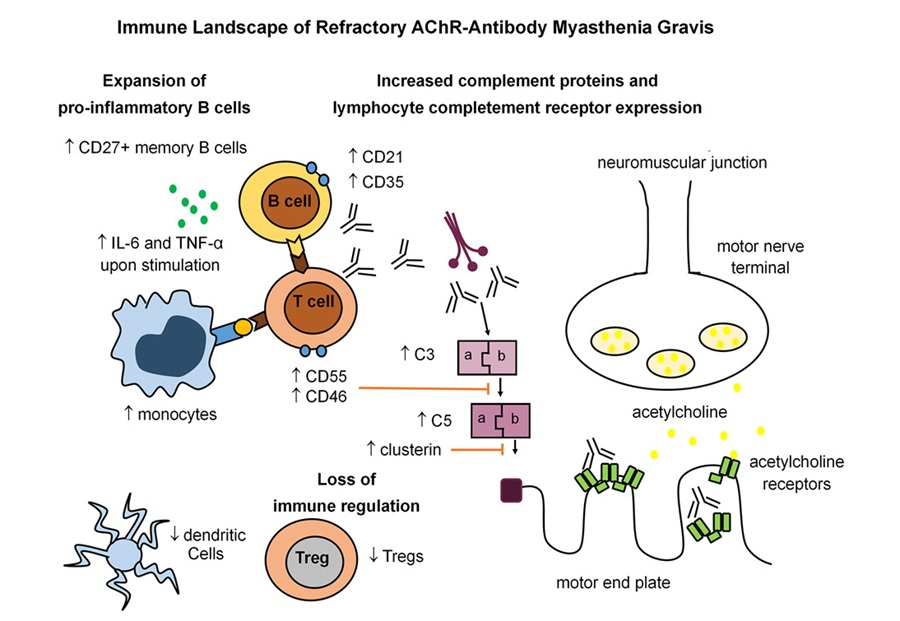
Firma inmunitaria identificada en miastenia gravis resistente al tratamiento
La miastenia gravis es un trastorno autoinmune poco común en el que el ataque inmunitario a la unión neuromuscular causa debilidad fluctuante que puede afectar la visión, el movimiento,... MásMicrobiología
ver canal
OMS recomienda pruebas POC, hisopos de lengua y agrupamiento de esputo para diagnóstico de TB
La tuberculosis (TB) sigue siendo una de las principales causas de muerte por enfermedades infecciosas en el mundo; sin embargo, millones de casos no se diagnostican o se detectan demasiado tarde.... Más
Nuevo método de imágenes podría ayudar a predecir infecciones intestinales peligrosas
Las infecciones por Clostridioides difficile afectan a aproximadamente medio millón de personas en Estados Unidos cada año y son una de las principales causas de diarrea infecciosa en entornos... MásPatología
ver canal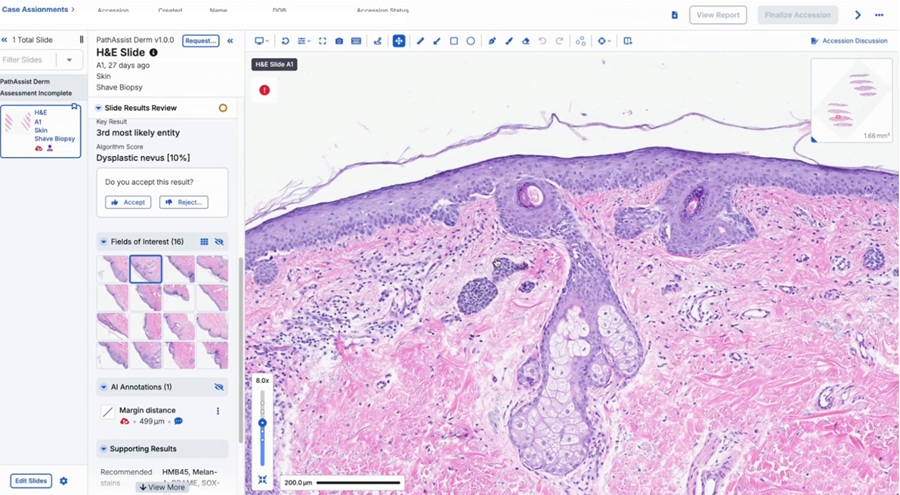
Herramienta con IA transforma flujo de trabajo en dermatopatología
El cáncer de piel representa el mayor número de diagnósticos de cáncer en Estados Unidos, lo que ejerce una presión sostenida sobre los servicios de patología.... Más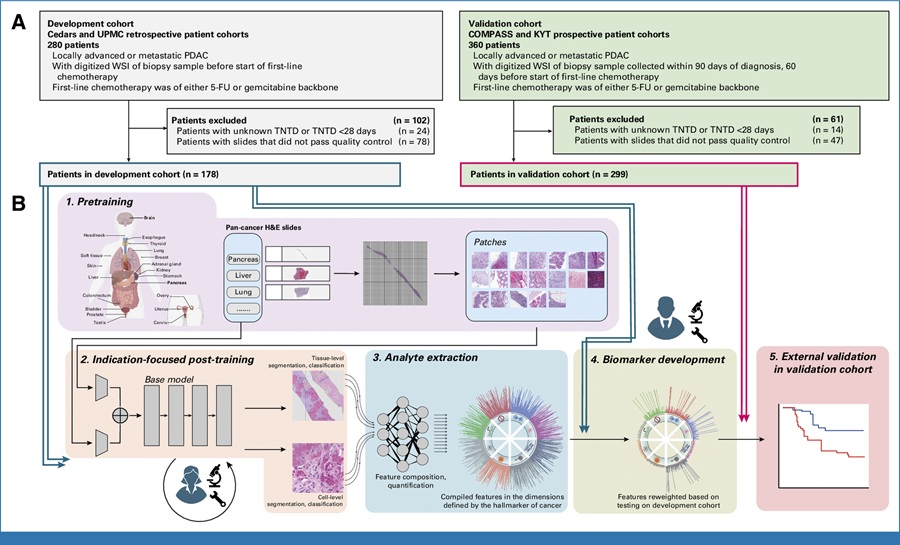
Herramienta de IA predice la respuesta a la quimioterapia a partir de portaobjetos de biopsia
La selección de la quimioterapia de primera línea para el cáncer de páncreas avanzado generalmente implica probar uno de dos regímenes aprobados y cambiarlo si la respuesta... MásTecnología
ver canal
Nueva pipeta electrónica mejora flujos de trabajo con control por pantalla táctil
El pipeteo manual sigue siendo un paso rutinario pero propenso a errores que puede afectar la reproducibilidad y el rendimiento en laboratorios clínicos y de investigación.... Más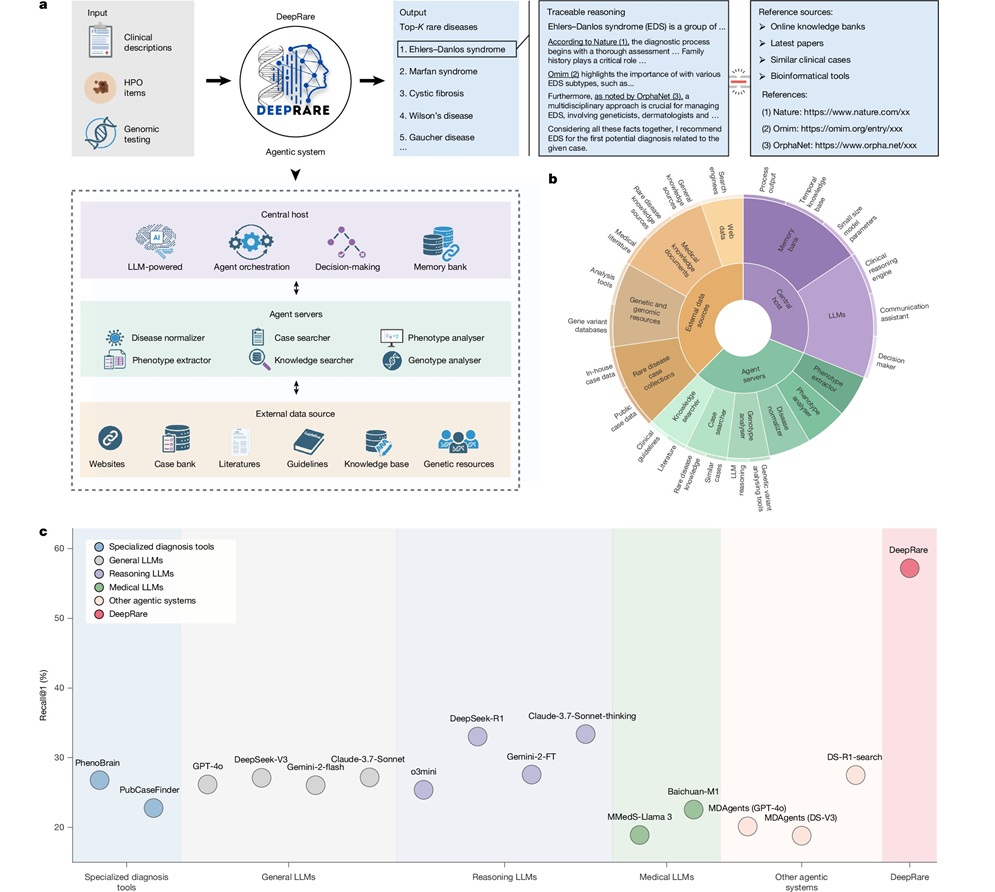
Modelo de IA supera a clínicos en la detección de enfermedades raras
Se estima que las enfermedades raras afectan a 300 millones de personas en todo el mundo; sin embargo, el diagnóstico suele ser largo y propenso a errores. Muchas de estas afecciones presentan signos... MásIndustria
ver canal
Agilent Technologies adquiere la empresa de diagnóstico patológico Biocare Medical
Agilent Technologies (Santa Clara, California, EE. UU.) ha firmado un acuerdo definitivo para adquirir Biocare Medical (Pacheco, California, EE. UU.), ampliando así su cartera de productos de p... Más