Desarrollan prueba novedosa para detectar e identificar patógenos
|
Por el equipo editorial de LabMedica en español Actualizado el 05 Oct 2021 |
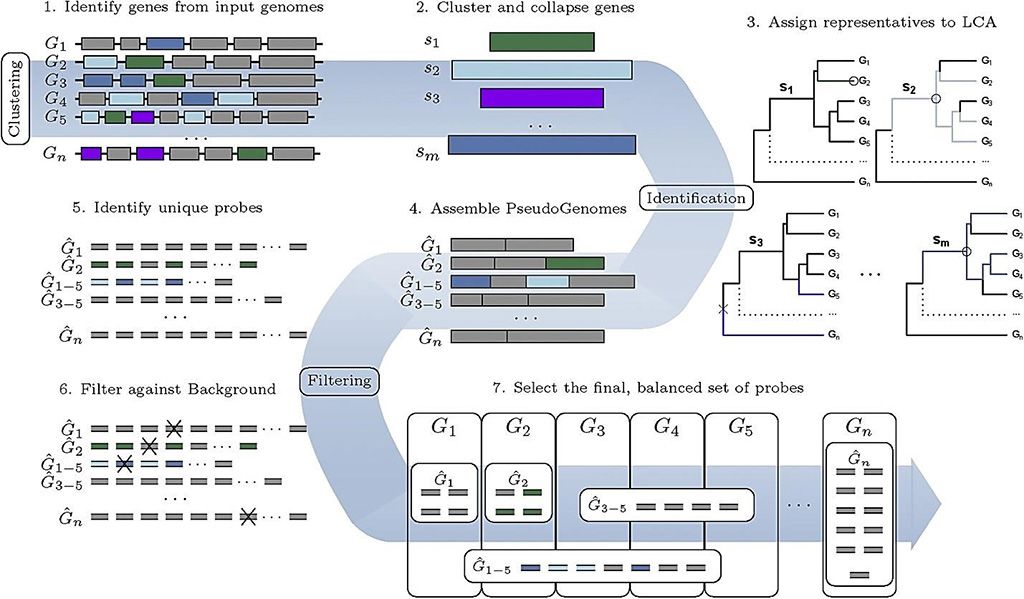
Imagen: El flujo de trabajo de la línea de productos en proyecto, HUBDesign: diseño de sonda para la captura simultánea y dirigida de diversos objetivos metagenómicos (Fotografía cortesía de la Universidad McMaster)
Los patógenos en entornos clínicos o de vida silvestre, como las muestras de sangre o saliva, por ejemplo, son particularmente difíciles de aislar, ya que pueden constituir fácilmente menos de una millonésima parte de una muestra, especialmente en las primeras etapas de una infección, cuando las concentraciones todavía son bajas y la detección es más crítica para los pacientes.
Una amplia gama de esfuerzos de estudios metagenómicos se ven obstaculizados por el mismo desafío: bajas concentraciones de objetivos de interés combinadas con cantidades abrumadoras de señal de fondo. Aunque se puede utilizar PCR o captura de ADN sin tratamiento previo cuando hay una pequeña cantidad de organismos de interés, los desafíos de diseño se vuelven insostenibles para una gran cantidad de objetivos.
Un equipo de científicos de la Universidad McMaster (Hamilton, ON, Canadá) y sus colegas desarrollaron una herramienta sofisticada nueva que podría ayudar a proporcionar una alerta temprana de virus raros y desconocidos en el medio ambiente e identificar patógenos bacterianos potencialmente mortales que causan sepsis. El nuevo algoritmo es una herramienta avanzada que puede ayudar a desarrollar sondas para capturar trazas de patógenos, tanto conocidos como desconocidos provenientes de una amplia variedad de situaciones, como la transmisión de infecciones de animal a humano como el SARS-CoV-2 o los reservorios de monitoreo en el medio ambiente por posibles patógenos emergentes.
El equipo probó con éxito las sondas en toda la familia de coronavirus, incluido el SARS-CoV-2. Las sondas proporcionan un atajo al apuntar, aislar e identificar, las secuencias de ADN, de manera específica y simultánea, que se comparten entre organismos relacionados, con mayor frecuencia debido a la historia evolutiva o la ascendencia. Para demostrar las capacidades y la eficacia de la herramienta, el Diseño de Cebos Jerárquicos Únicos (The Hierarchical Unique Bait Design, HUBDesign), diseñaron y probaron dos conjuntos de sondas: un conjunto de sondas de coronavirus capaz de detectar simultáneamente todos los coronavirus secuenciados y un conjunto de sondas dirigidas a patógenos bacterianos asociados con la sepsis.
La mayoría (62,5%) de las sondas tienen objetivos específicos para un virus. De las sondas que se dirigen a varios virus, la mayoría (78,1%) se dirigen a dos o tres. Los tres conjuntos restantes de sondas se dirigen a loci específicos de merbecovirus y embecovirus (ambos son subgéneros de Betacoronavirus) y loci comunes al género Deltacoronavirus. Tanto el SARS-CoV-2 como el HCoV-NL63 tienen sondas en dos niveles en la jerarquía.
El conjunto de sondas HUBDesign para patógenos de la sepsis contenía 26.870 sondas dirigidas a patógenos bacterianos, que cubren el 2,09% de todos los nucleótidos en el conjunto de datos de entrada a una profundidad media de cobertura de 3,64x. Los investigadores demostraron la efectividad de las sondas para capturar la increíble variedad de patógenos asociados con la sepsis, una condición potencialmente mortal y de rápido desarrollo que ocurre cuando el cuerpo reacciona de forma exagerada a una infección que generalmente comienza en los pulmones, el tracto urinario, la piel o el tracto gastrointestinal.
Hendrik Poinar, PhD, profesor de Genética Evolutiva Molecular y autor principal del estudio, dijo: “Actualmente necesitamos formas más rápidas, económicas y concisas de detectar patógenos en muestras humanas y ambientales que democraticen la caza y esta línea de productos en proyecto hace exactamente eso”. El estudio fue publicado el 15 de septiembre de 2021 en la revista Cell Reports Methods.
Enlace relacionado:
Universidad McMaster
Una amplia gama de esfuerzos de estudios metagenómicos se ven obstaculizados por el mismo desafío: bajas concentraciones de objetivos de interés combinadas con cantidades abrumadoras de señal de fondo. Aunque se puede utilizar PCR o captura de ADN sin tratamiento previo cuando hay una pequeña cantidad de organismos de interés, los desafíos de diseño se vuelven insostenibles para una gran cantidad de objetivos.
Un equipo de científicos de la Universidad McMaster (Hamilton, ON, Canadá) y sus colegas desarrollaron una herramienta sofisticada nueva que podría ayudar a proporcionar una alerta temprana de virus raros y desconocidos en el medio ambiente e identificar patógenos bacterianos potencialmente mortales que causan sepsis. El nuevo algoritmo es una herramienta avanzada que puede ayudar a desarrollar sondas para capturar trazas de patógenos, tanto conocidos como desconocidos provenientes de una amplia variedad de situaciones, como la transmisión de infecciones de animal a humano como el SARS-CoV-2 o los reservorios de monitoreo en el medio ambiente por posibles patógenos emergentes.
El equipo probó con éxito las sondas en toda la familia de coronavirus, incluido el SARS-CoV-2. Las sondas proporcionan un atajo al apuntar, aislar e identificar, las secuencias de ADN, de manera específica y simultánea, que se comparten entre organismos relacionados, con mayor frecuencia debido a la historia evolutiva o la ascendencia. Para demostrar las capacidades y la eficacia de la herramienta, el Diseño de Cebos Jerárquicos Únicos (The Hierarchical Unique Bait Design, HUBDesign), diseñaron y probaron dos conjuntos de sondas: un conjunto de sondas de coronavirus capaz de detectar simultáneamente todos los coronavirus secuenciados y un conjunto de sondas dirigidas a patógenos bacterianos asociados con la sepsis.
La mayoría (62,5%) de las sondas tienen objetivos específicos para un virus. De las sondas que se dirigen a varios virus, la mayoría (78,1%) se dirigen a dos o tres. Los tres conjuntos restantes de sondas se dirigen a loci específicos de merbecovirus y embecovirus (ambos son subgéneros de Betacoronavirus) y loci comunes al género Deltacoronavirus. Tanto el SARS-CoV-2 como el HCoV-NL63 tienen sondas en dos niveles en la jerarquía.
El conjunto de sondas HUBDesign para patógenos de la sepsis contenía 26.870 sondas dirigidas a patógenos bacterianos, que cubren el 2,09% de todos los nucleótidos en el conjunto de datos de entrada a una profundidad media de cobertura de 3,64x. Los investigadores demostraron la efectividad de las sondas para capturar la increíble variedad de patógenos asociados con la sepsis, una condición potencialmente mortal y de rápido desarrollo que ocurre cuando el cuerpo reacciona de forma exagerada a una infección que generalmente comienza en los pulmones, el tracto urinario, la piel o el tracto gastrointestinal.
Hendrik Poinar, PhD, profesor de Genética Evolutiva Molecular y autor principal del estudio, dijo: “Actualmente necesitamos formas más rápidas, económicas y concisas de detectar patógenos en muestras humanas y ambientales que democraticen la caza y esta línea de productos en proyecto hace exactamente eso”. El estudio fue publicado el 15 de septiembre de 2021 en la revista Cell Reports Methods.
Enlace relacionado:
Universidad McMaster
Últimas Diagnóstico Molecular noticias
- Nuevo método de ARN origami facilita pruebas más rápidas para trastornos por expansión de repeticiones
- La FDA aprueba panel ampliado de biopsia líquida para el perfilado del cáncer avanzado
- Prueba ampliada de genotipificación de DPYD ayuda a dosificar la quimioterapia de forma más segura
- Prueba microbiana de saliva podría ayudar a clasificar el riesgo de cáncer de esófago
- Ensayo de perfilado genómico autorizado por la FDA guía la selección terapéutica en tumores sólidos
- Perfil multiómico ayuda a predecir la respuesta al BCG y la recurrencia en cáncer de vejiga
- Nueva herramienta computacional revela impulsor genético de la neuropatía idiopática
- Firmas específicas del cáncer de mama vinculan la inestabilidad genómica con los resultados clínicos
- Prueba de sangre detecta falta de respuesta temprana en cáncer de próstata metastásico
- Prueba de sangre de ADNtc podría guiar la radioterapia en pacientes con metástasis limitadas
- Prueba sanguínea aprobada por la FDA guía la terapia adyuvante del cáncer de vejiga
- El perfil genómico tumoral identifica el cáncer de vesícula biliar de alto riesgo
- Nuevo algoritmo mejora la detección de fusiones genéticas en leucemia linfoblástica aguda de células B
- Prueba PCR multiplex rápida detecta 11 patógenos gastrointestinales a partir de una sola muestra
- “Reloj de envejecimiento” basado en sangre ayuda a predecir el riesgo de demencia
- Un marcador proteico sensible ayuda al diagnóstico del cáncer de próstata de células pequeñas
Canales
Química Clínica
ver canal
Nuevo valor de corte de CA19-9 ayuda a identificar pacientes con cáncer de páncreas de alto riesgo
El adenocarcinoma ductal pancreático (PDAC) se diagnostica con frecuencia en una etapa avanzada y sigue siendo uno de los tumores sólidos más letales. Los médicos suelen utilizar el antígeno carbohidrato... Más
Biomarcadores sanguíneos muestran potencial para predecir el riesgo de psicosis
La psicosis suele manifestarse en la adolescencia o al inicio de la edad adulta y puede afectar gravemente el funcionamiento social y laboral. Las alucinaciones, los delirios y el pensamiento desorganizado... MásHematología
ver canal
Un umbral de ferritina más elevado podría mejorar la detección de deficiencia de hierro en niños
La deficiencia de hierro en niños en edad escolar puede afectar el desarrollo cerebral, el aprendizaje, el crecimiento y el rendimiento físico; sin embargo, la detección temprana de... Más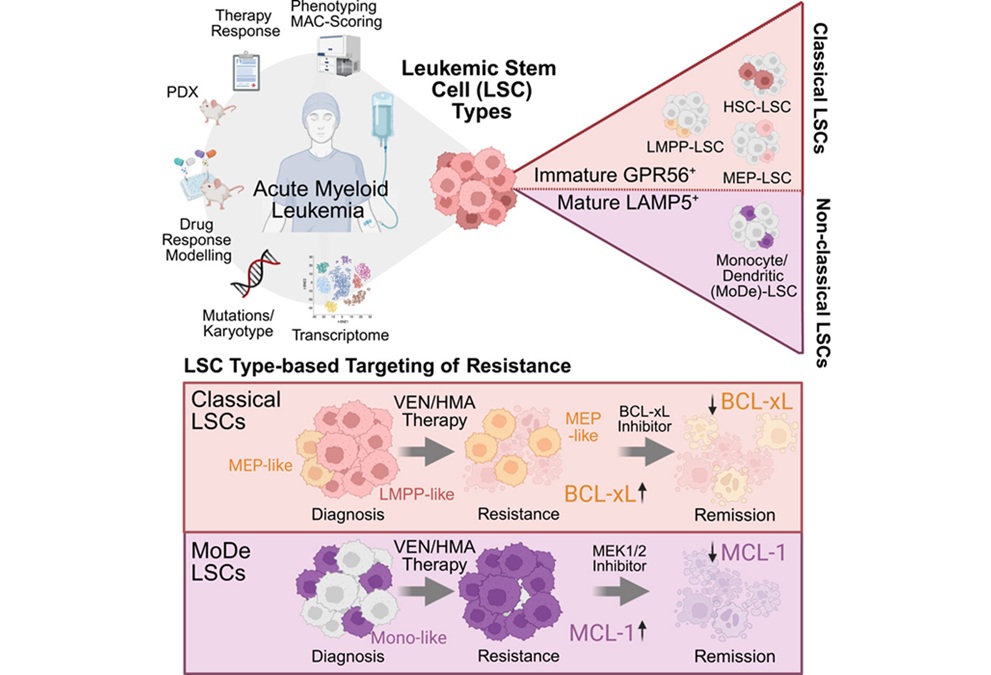
Los biomarcadores de células madre podrían orientar el tratamiento en la leucemia mieloide aguda
La leucemia mieloide aguda (LMA) es un cáncer de sangre agresivo que afecta con mayor frecuencia a adultos mayores y que, a pesar de los avances terapéuticos, aún presenta un pronóstico... MásInmunología
ver canal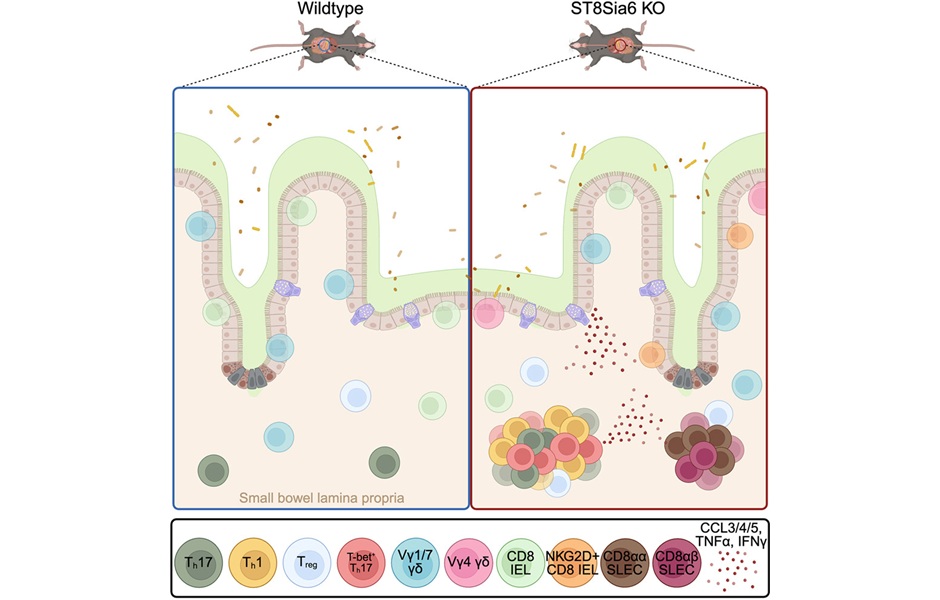
Enzima inmunitaria se vincula con la enfermedad inflamatoria intestinal resistente al tratamiento
La enfermedad inflamatoria intestinal (EII) afecta a casi 3 millones de personas en Estados Unidos y su prevalencia sigue en aumento. Los medicamentos que actúan sobre el factor de necrosis tumoral... Más
Análisis de sangre simple podría reemplazar biopsias para monitorizar el rechazo del trasplante pulmonar
Los receptores de trasplante de pulmón presentan algunas de las tasas más altas de rechazo celular agudo, y la vigilancia rutinaria suele basarse en biopsias quirúrgicas repetidas.... MásMicrobiología
ver canal
Nuevo ensayo de RAM respalda el cribado rápido para el control de infecciones en hospitales
A medida que la resistencia a los antimicrobianos se extiende por todo el mundo, las infecciones asociadas a la atención sanitaria suponen una carga cada vez mayor para los hospitales, lo que aumenta la... Más
Estudio revela que infecciones ocultas de mpox podrían impulsar su propagación continua
La viruela símica, o mpox, sigue circulando a pesar de la vacunación, y muchos casos no muestran ningún vínculo conocido con una pareja sintomática. El papel de las personas... MásPatología
ver canal
Prueba de patología con IA recibe designación de avance de la FDA para riesgo de cáncer de vejiga
El cáncer de vejiga no músculo-invasivo presenta resultados muy variables, lo que complica la vigilancia y la planificación del tratamiento. La evaluación del riesgo suele basarse en el estadio, el grado... Más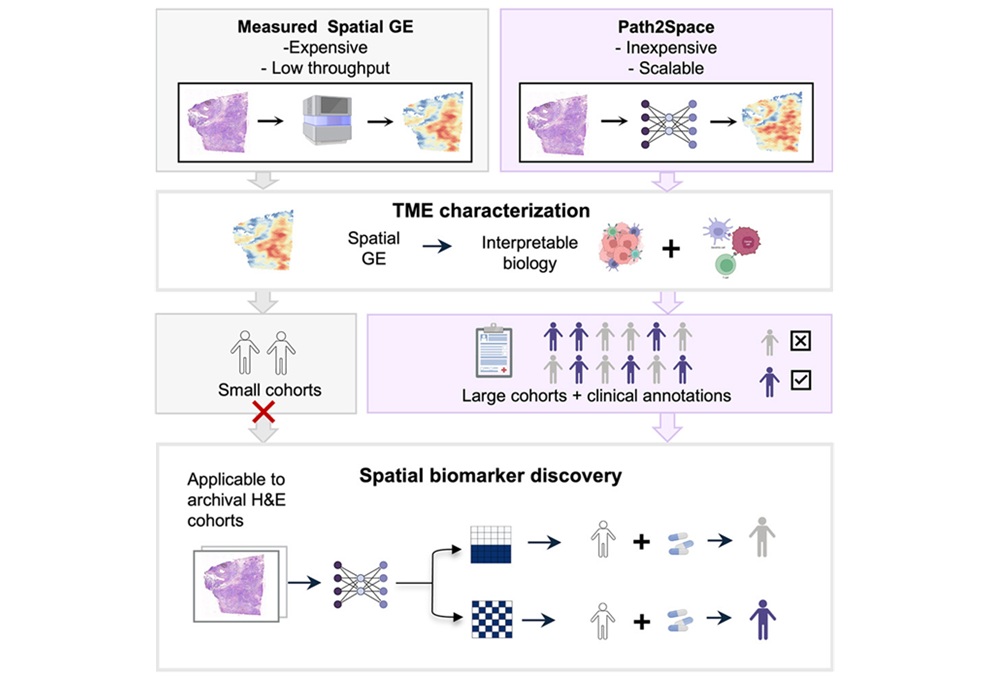
Herramienta de IA predice la expresión génica espacial del cáncer a partir de imágenes de patología
El análisis de la expresión génica puede aportar información sobre la biología tumoral y la selección del tratamiento, pero los ensayos espaciales siguen siendo... Más
Herramienta de patología digital con IA para la estratificación del riesgo en cáncer de mama
La evaluación del riesgo en el momento del diagnóstico es fundamental para guiar el tratamiento del cáncer de mama invasivo en estadio temprano, con receptor hormonal positivo y receptor 2 del factor de... MásTecnología
ver canal
Flujo de trabajo totalmente automatizado de muestra a resultado impulsa las pruebas de TB latente
La detección de la tuberculosis latente sigue representando una carga de trabajo considerable para los laboratorios clínicos a medida que se expanden los programas de cribado.... Más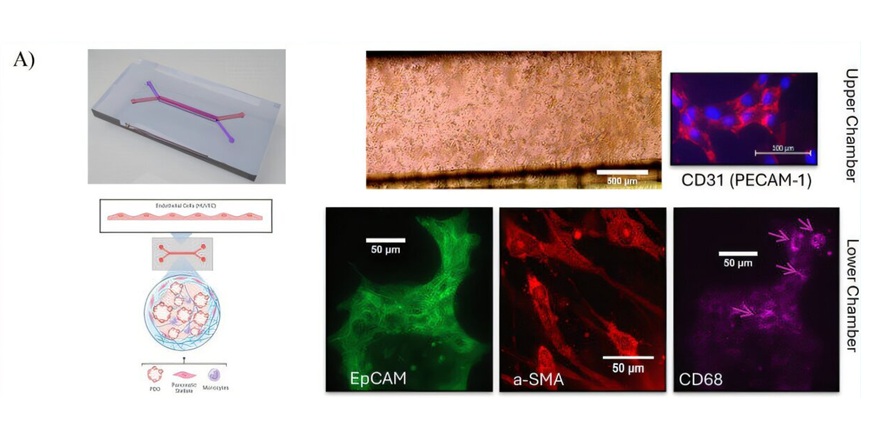
Plataforma de 'tumor en un chip' modela la respuesta al tratamiento del cáncer de páncreas
El cáncer de páncreas sigue siendo uno de los tipos de cáncer más difíciles de tratar, ya que los tumores se encuentran inmersos en un microambiente denso que influye... MásIndustria
ver canal
Analizador multifuncional impulsado por IA gana el Premio Alemán de Innovación
Los servicios de hematología se prestan cada vez más en entornos de atención distribuidos, donde la dotación limitada de personal y los flujos de trabajo complejos pueden prolongar... Más