Análisis rápido CRISPR/Cas para el diagnóstico de fiebres virales en ambientes de baja tecnología
|
Por el equipo editorial de LabMedica en español Actualizado el 07 Sep 2020 |
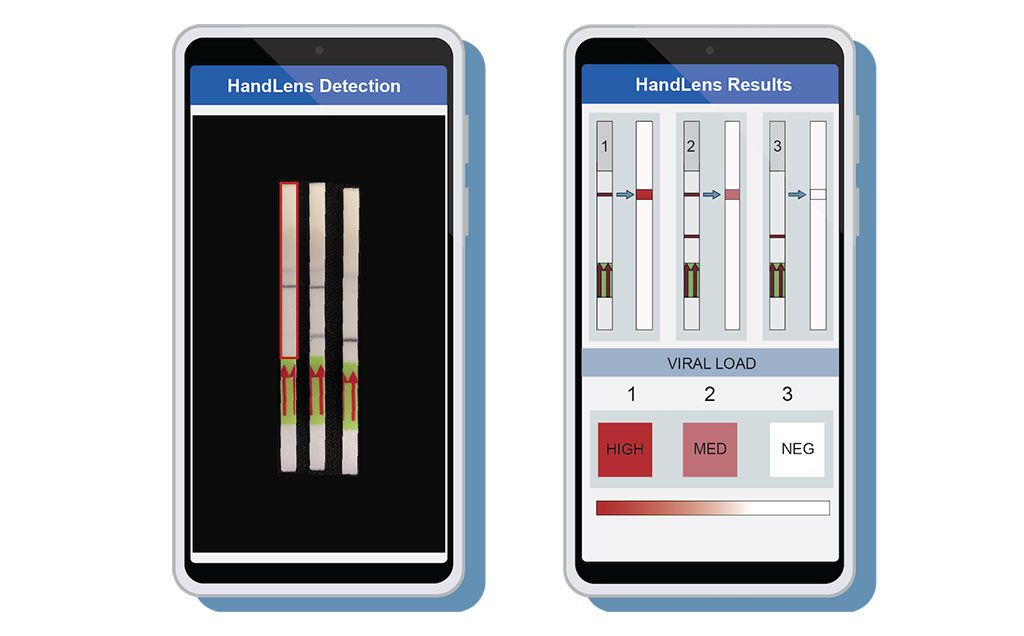
Imagen: Se diseñó una aplicación para teléfonos móviles llamada HandLens para leer e informar los resultados en las tiras de papel SHERLOCK (Fotografía cortesía de Anna Lachenauer, Facultad de Medicina de la Universidad de Stanford)
Las pruebas de diagnóstico rápido para los virus de la fiebre del Ébola y Lassa, basadas en el complejo CRISPR/Cas13a, dirigidas a la detección del ARN, se han probado con éxito en condiciones de campo en varios países africanos.
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
COVID-19 no es la única enfermedad que existe. Los recientes brotes de fiebres hemorrágicas virales (VHF), incluida la enfermedad por el virus del Ébola (EVE) y la fiebre de Lassa (LF), ponen de relieve la necesidad urgente de realizar pruebas sensibles y desplegables para diagnosticar estas devastadoras enfermedades humanas. En este sentido, los investigadores del Instituto Broad de MIT y Harvard (Cambridge, MA, EUA) y sus colaboradores, desarrollaron diagnósticos basados en CRISPR-Cas13a, dirigidos al virus del Ébola (EBOV) y al virus Lassa (LASV), con lecturas de flujo lateral y fluorescentes.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente interespaciadas) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. A cada repetición le siguen segmentos cortos de “ADN espaciador” de exposiciones anteriores a un virus bacteriano o plásmido. Desde 2013, se ha utilizado el sistema CRISPR/Cas9 en la investigación para la edición de genes (agregar, interrumpir o cambiar la secuencia de genes específicos) y la regulación de genes. Al administrar la enzima Cas9 y los ARN guía apropiados (ARNsg) a una célula, el genoma del organismo se puede cortar en cualquier ubicación deseada.
Los recientes esfuerzos computacionales para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación del ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, guiado por ARN, dirigido a la detección del ARN, que tiene un gran potencial para aplicaciones precisas, robustas y escalables, guiadas por ARN dirigidas a la detección de ARN.
En el desarrollo de un método para diagnósticos desplegables y rápidamente adaptables, los investigadores trabajaron con la plataforma SHERLOCK (siglas en inglés para Desbloqueo de Reportero Enzimático Específico de Alta Sensibilidad), basada en CRISPR. SHERLOCK utiliza la proteína Cas13a dirigida al ARN para la detección sensible y específica del ácido nucleico viral. Este método funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también puede ser cuantificada. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple tira de papel, en un equipo de laboratorio o para proporcionar una lectura electroquímica que se puede leer con un teléfono móvil.
SHERLOCK se puede combinar con el método HUDSON (Calentamiento de Muestras de Diagnóstico no Extraídas para Eliminar Nucleasas), que inactiva patógenos y libera ácido nucleico mediante una desnaturalización química y térmica combinada, eliminando la necesidad de una extracción de ácidos nucleicos basada en columna o en perlas. Este proceso hace que las muestras de los pacientes sean más seguras para que el personal clínico las manipule en entornos de baja tecnología y elimina la necesidad de extraer el material genético de un virus de las muestras, antes del análisis.
Para completar el paquete, los investigadores también desarrollaron una aplicación para teléfonos móviles llamada HandLens, que puede leer e informar inmediatamente los resultados de las tiras de papel SHERLOCK. Esta herramienta puede ayudar en situaciones en las que la tira de papel emite una señal débil que es difícil de interpretar para un médico.
Los investigadores utilizaron la técnica SHERLOCK junto con HUDSON y HandLens en Nigeria durante un reciente brote de fiebre de Lassa y en Sierra Leona y la República Democrática del Congo durante los brotes del virus del Ébola. Los resultados revelaron que los ensayos SHERLOCK funcionaron de manera tan consistente o mejor que otras metodologías de diagnóstico, lo que demuestra el potencial de la plataforma para el uso clínico en áreas con recursos limitados.
La técnica SHERLOCK para el diagnóstico rápido de enfermedades virales se describió en la edición en línea del 17 de agosto de 2020 de la revista Nature Communications.
Enlace relacionado:
Instituto Broad de MIT y Harvard
Últimas Microbiología noticias
- Biosensor de antígeno detecta tuberculosis activa en una hora
- Panel rápido de susceptibilidad en hemocultivo amplía la cobertura para infecciones por gramnegativos
- Las características del microbioma oral e intestinal permiten identificar el cáncer gástrico temprano
- Un método de microscopía sin marcadores permite una detección más rápida y cuantitativa de la malaria
- Prueba del microbioma intestinal predice la recurrencia del melanoma tras la cirugía
- Genes de resistencia a los antibióticos detectados en recién nacidos a las pocas horas de nacer
- Prueba rápida colorimétrica estratifica cepas de estafilococo virulentas y resistentes
- Panel sindrómico permite identificación rápida de infecciones del torrente sanguíneo
- Nuevo objetivo bacteriano identificado para la detección temprana del noma
- Prueba rápida de orina acelera la selección de antibióticos para infecciones del tracto urinario
- El análisis genómico vincula cepas estreptocócicas emergentes con infecciones específicas
- La OMS respalda las pruebas rápidas en el punto de atención para mejorar la detección de tuberculosis
- Método basado en el aliento distingue infecciones bacterianas de forma rápida
- OMS recomienda pruebas POC, hisopos de lengua y agrupamiento de esputo para diagnóstico de TB
- Nuevo método de imágenes podría ayudar a predecir infecciones intestinales peligrosas
- La secuenciación rápida podría transformar la atención de la tuberculosis
Canales
Química Clínica
ver canal
Prueba ultrasensible detecta un biomarcador clave de un subtipo de demencia frontotemporal
La demencia afecta a más de 57 millones de personas en todo el mundo y se prevé que esta cifra casi se duplique en las próximas dos décadas, lo que supone una gran carga para... Más
Los análisis sanguíneos de rutina años antes del embarazo podrían identificar el riesgo de preeclampsia
La hipertensión arterial durante el embarazo es frecuente y puede derivar en preeclampsia, por lo que es fundamental un seguimiento exhaustivo en las consultas prenatales. Sin embargo, la mayoría... MásDiagnóstico Molecular
ver canal
Prueba de sangre mapea microambiente tumoral para predecir respuesta a la inmunoterapia
La inmunoterapia ha transformado el tratamiento del cáncer, pero su beneficio duradero se limita a un subconjunto de pacientes, y los médicos aún carecen de herramientas fiables para... Más
Análisis de ADN en heces monitorea la actividad de la enfermedad en la EII
La enfermedad inflamatoria intestinal (EII) afecta a entre 6 y 8 millones de personas en todo el mundo y se suele monitorizar mediante colonoscopia y análisis de heces. Dado que la actividad de... MásHematología
ver canal
Análisis de sangre permite la detección temprana de recaída del mieloma múltiple
Las biopsias de médula ósea siguen siendo fundamentales para diagnosticar y monitorizar el mieloma múltiple, pero el procedimiento es doloroso, invasivo y a menudo se repite con el tiempo.... Más
Identifican un “interruptor protector” en el linfoma difuso de células B grandes
El linfoma difuso de células B grandes (LDCBG) es la forma más común de linfoma no Hodgkin y suele presentar un comportamiento clínico agresivo. Si bien muchos pacientes responden... MásInmunología
ver canal
Las pruebas en el punto de atención podrían ampliar el acceso al diagnóstico de Mpox
Los brotes de mpox en regiones no endémicas han puesto de manifiesto la necesidad de diagnósticos rápidos y accesibles para limitar la transmisión. La reacción en cadena... Más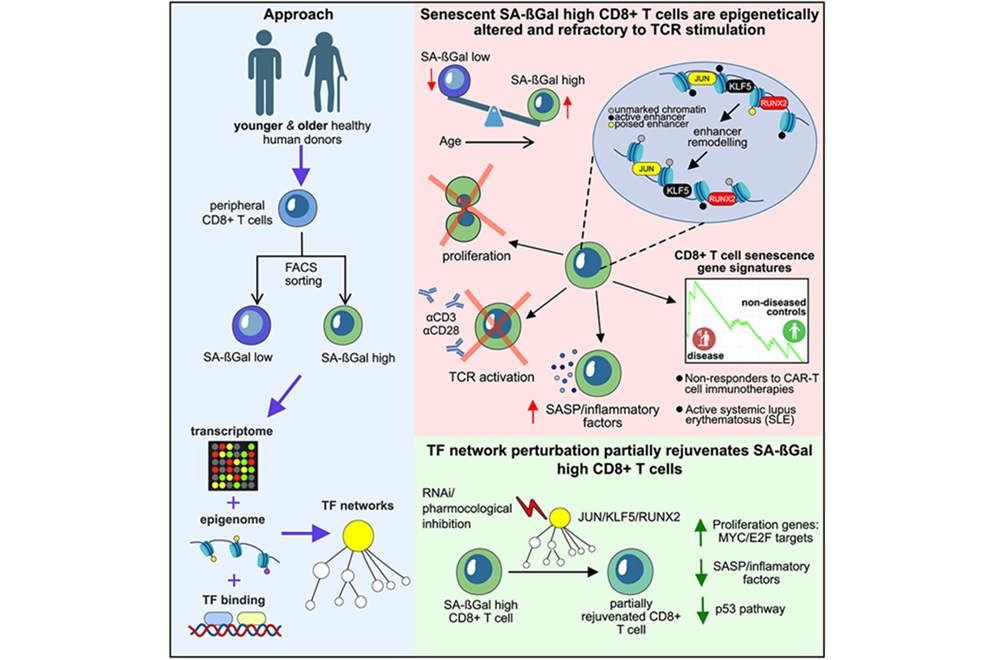
El perfil de senescencia de las células T podría predecir respuestas a la terapia CAR-T
La terapia con células T con receptor de antígeno quimérico (CAR) puede lograr remisiones notables y duraderas, aunque muchos pacientes obtienen un beneficio mínimo o nulo.... MásPatología
ver canal
Herramienta de patología digital con IA para la estratificación del riesgo en cáncer de mama
La evaluación del riesgo en el momento del diagnóstico es fundamental para guiar el tratamiento del cáncer de mama invasivo en estadio temprano, con receptor hormonal positivo y receptor 2 del factor de... Más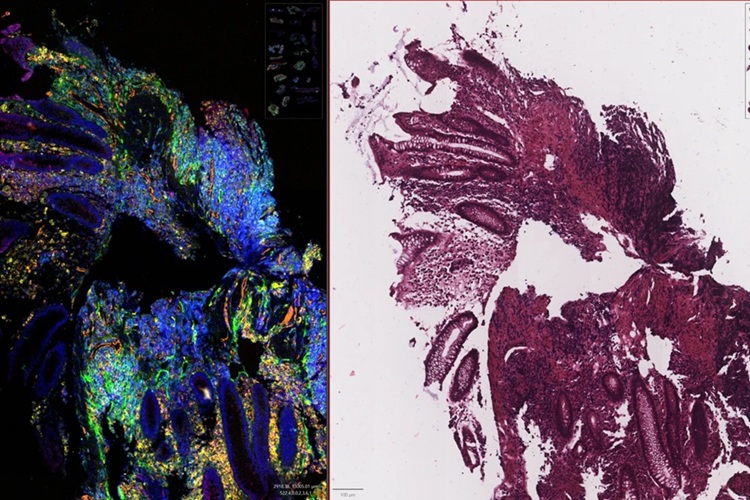
Nueva herramienta de IA revela señales genéticas ocultas en portaobjetos H&E de rutina
Los patólogos de todo el mundo utilizan preparaciones teñidas con hematoxilina y eosina (H&E) para examinar la arquitectura tisular; sin embargo, estas tinciones no revelan la actividad... Más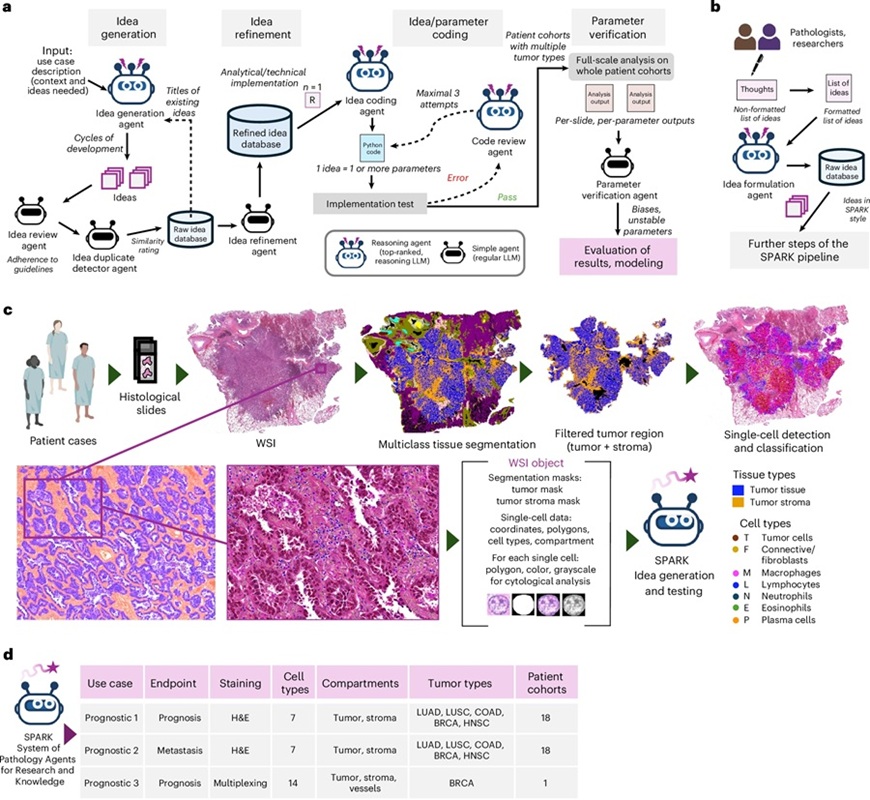
Sistema de IA analiza muestras patológicas rutinarias para predecir resultados del cáncer
La transformación digital de la patología está ampliando la forma en que se evalúan los cánceres en la práctica clínica habitual. La inteligencia artificial... Más
Nuevo enfoque de mapeo tisular identifica una forma de alto riesgo de enfermedad renal diabética
La nefropatía diabética es una de las principales causas de enfermedad renal crónica y enfermedad renal terminal, que afecta al 20 %-40 % de las personas con diabetes y a más de 107 millones de personas... MásTecnología
ver canal
Plataforma de 'tumor en un chip' modela la respuesta al tratamiento del cáncer de páncreas
El cáncer de páncreas sigue siendo uno de los tipos de cáncer más difíciles de tratar, ya que los tumores se encuentran inmersos en un microambiente denso que influye... Más
Nueva plataforma captura vesículas extracelulares para la detección temprana del cáncer
El diagnóstico precoz sigue siendo la forma más eficaz de reducir la mortalidad por cáncer; sin embargo, muchas pruebas de detección no detectan la enfermedad en sus etapas iniciales.... MásIndustria
ver canal
Roche adquirirá PathAI por hasta 1.050 millones de dólares para fortalecer su cartera de diagnósticos con IA
Roche ha firmado un acuerdo definitivo de fusión para adquirir PathAI, una empresa especializada en patología digital e inteligencia artificial para laboratorios de patología y la... Más