Sistema de microarrays basados en CRISPR permite pruebas masivas para patógenos virales
|
Por el equipo editorial de LabMedica en español Actualizado el 11 May 2020 |

Imagen: Fotografía del chip de micropozos CARMEN (Fotografía cortesía de Michael James Butts)
Un novedoso sistema de diagnóstico microfluídico basado en ácidos nucleicos es capaz de detectar un virus específico de un catálogo de más de 160 patógenos humanos, incluido el coronavirus COVID-19, simultáneamente en más de mil muestras.
Para permitir la vigilancia de rutina y las aplicaciones de diagnóstico integrales, existe la necesidad de tecnologías de detección que se puedan ampliar para analizar muchas muestras y, al mismo tiempo, detectar múltiples patógenos individuales. Para lograr esto, los investigadores del Instituto Broad del MIT y Harvard (Cambridge, MA, EUA) desarrollaron una plataforma de diagnóstico llamada CARMEN (sigla en inglés para Reacciones Arregladas Combinadas para la Evaluación Multiplexada de Ácidos Nucleicos). El sistema CARMEN depende de gotas de nanolitros que contienen reactivos de detección de ácido nucleico basados en CRISPR/Cas 13.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente y separadas entre sí) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. Cada repetición es seguida por segmentos cortos de “ADN espaciador” de exposiciones previas a un virus o plásmido bacteriano.
Los esfuerzos computacionales recientes para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación de ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, dirigido por el ARN contra el ARN y que tiene un gran potencial para aplicaciones precisas, robustas y escalables de orientación por el ARN contra el ARN.
La plataforma CARMEN consta de un chip de goma, un poco más grande que un teléfono inteligente, que contiene decenas de miles de micropozos diseñados para contener un par de gotitas del tamaño de nanolitros. Una gota contiene material genético viral de una muestra y la otra contiene reactivos de detección de virus.
La detección de ácidos nucleicos virales se realiza mediante una modificación del protocolo SHERLOCK. Este es un método para la detección de moléculas individuales de objetivos de ácido nucleico y significa desbloqueo específico del reportero enzimático de alta sensibilidad. Funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también se puede cuantificar. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple prueba de tira de papel, en equipos de laboratorio o para proporcionar una lectura electroquímica que se pueda leer con un teléfono móvil.
En la plataforma CARMEN, las gotas de nanolitros que contienen reactivos de detección de ácido nucleico basados en CRISPR se autoorganizan en la matriz de micropozos para emparejarse con las gotas de muestras amplificadas, analizando cada muestra contra cada ARN CRISPR (ARNcr) en replicado. La combinación de detección CARMEN y Cas13 (CARMEN-Cas13) permitió realizar pruebas robustas de más de 4.500 pares de ARNc-objetivo en una sola matriz. El protocolo completo, desde la extracción de ARN hasta los resultados, requirió menos de ocho horas.
Empleando el método CARMEN-Cas13, los investigadores desarrollaron un ensayo multiplexado que simultáneamente diferenciaba 169 virus asociados con humanos con más de 10 secuencias genómicas publicadas e incorporaba rápidamente un ARNcr adicional para detectar el agente causante del coronavirus pandémico COVID-19. CARMEN-Cas13 permitió además el subtipo integral de cepas de influenza A y la identificación multiplexada de docenas de mutaciones de resistencia a los medicamentos contra el VIH.
“Este enfoque miniaturizado para el diagnóstico es eficiente en recursos y fácil de implementar”, dijo el coautor principal, el Dr. Paul Blainey, profesor asociado de ingeniería biológica en el Instituto de Tecnología de Massachusetts. “Las nuevas herramientas requieren creatividad e innovación, y con estos avances en química y microfluídica, estamos entusiasmados con el potencial de CARMEN a medida que la comunidad trabaja para vencer a la COVID-19 y las futuras amenazas de enfermedades infecciosas”.
El método CARMEN-Cas13 se describió en la edición en línea del 29 de abril de 2020 de la revista Nature.
Enlace relacionado:
Instituto Broad del MIT y Harvard
Para permitir la vigilancia de rutina y las aplicaciones de diagnóstico integrales, existe la necesidad de tecnologías de detección que se puedan ampliar para analizar muchas muestras y, al mismo tiempo, detectar múltiples patógenos individuales. Para lograr esto, los investigadores del Instituto Broad del MIT y Harvard (Cambridge, MA, EUA) desarrollaron una plataforma de diagnóstico llamada CARMEN (sigla en inglés para Reacciones Arregladas Combinadas para la Evaluación Multiplexada de Ácidos Nucleicos). El sistema CARMEN depende de gotas de nanolitros que contienen reactivos de detección de ácido nucleico basados en CRISPR/Cas 13.
Los CRISPR (repeticiones palindrómicas cortas agrupadas regularmente y separadas entre sí) son segmentos de ADN procariótico que contienen repeticiones cortas de secuencias de bases. Cada repetición es seguida por segmentos cortos de “ADN espaciador” de exposiciones previas a un virus o plásmido bacteriano.
Los esfuerzos computacionales recientes para identificar nuevos sistemas CRISPR descubrieron un nuevo tipo de enzima dirigida al ARN, Cas13. La diversa familia Cas13 contiene al menos cuatro subtipos conocidos, incluidos Cas13a (anteriormente C2c2), Cas13b, Cas13c y Cas13d. Se demostró que Cas13a se une y escinde el ARN, protegiendo a las bacterias de los fagos de ARN y sirviendo como una plataforma poderosa para la manipulación de ARN. Se sugirió que Cas13a podría funcionar como parte de un sistema CRISPR/Cas versátil, dirigido por el ARN contra el ARN y que tiene un gran potencial para aplicaciones precisas, robustas y escalables de orientación por el ARN contra el ARN.
La plataforma CARMEN consta de un chip de goma, un poco más grande que un teléfono inteligente, que contiene decenas de miles de micropozos diseñados para contener un par de gotitas del tamaño de nanolitros. Una gota contiene material genético viral de una muestra y la otra contiene reactivos de detección de virus.
La detección de ácidos nucleicos virales se realiza mediante una modificación del protocolo SHERLOCK. Este es un método para la detección de moléculas individuales de objetivos de ácido nucleico y significa desbloqueo específico del reportero enzimático de alta sensibilidad. Funciona amplificando secuencias genéticas y programando una molécula CRISPR para detectar la presencia de una firma genética específica en una muestra, que también se puede cuantificar. Cuando encuentra esas firmas, la enzima CRISPR se activa y libera una señal robusta. Esta señal se puede adaptar para trabajar en una simple prueba de tira de papel, en equipos de laboratorio o para proporcionar una lectura electroquímica que se pueda leer con un teléfono móvil.
En la plataforma CARMEN, las gotas de nanolitros que contienen reactivos de detección de ácido nucleico basados en CRISPR se autoorganizan en la matriz de micropozos para emparejarse con las gotas de muestras amplificadas, analizando cada muestra contra cada ARN CRISPR (ARNcr) en replicado. La combinación de detección CARMEN y Cas13 (CARMEN-Cas13) permitió realizar pruebas robustas de más de 4.500 pares de ARNc-objetivo en una sola matriz. El protocolo completo, desde la extracción de ARN hasta los resultados, requirió menos de ocho horas.
Empleando el método CARMEN-Cas13, los investigadores desarrollaron un ensayo multiplexado que simultáneamente diferenciaba 169 virus asociados con humanos con más de 10 secuencias genómicas publicadas e incorporaba rápidamente un ARNcr adicional para detectar el agente causante del coronavirus pandémico COVID-19. CARMEN-Cas13 permitió además el subtipo integral de cepas de influenza A y la identificación multiplexada de docenas de mutaciones de resistencia a los medicamentos contra el VIH.
“Este enfoque miniaturizado para el diagnóstico es eficiente en recursos y fácil de implementar”, dijo el coautor principal, el Dr. Paul Blainey, profesor asociado de ingeniería biológica en el Instituto de Tecnología de Massachusetts. “Las nuevas herramientas requieren creatividad e innovación, y con estos avances en química y microfluídica, estamos entusiasmados con el potencial de CARMEN a medida que la comunidad trabaja para vencer a la COVID-19 y las futuras amenazas de enfermedades infecciosas”.
El método CARMEN-Cas13 se describió en la edición en línea del 29 de abril de 2020 de la revista Nature.
Enlace relacionado:
Instituto Broad del MIT y Harvard
Últimas Microbiología noticias
- Nuevo objetivo bacteriano identificado para la detección temprana del noma
- Prueba rápida de orina acelera la selección de antibióticos para infecciones del tracto urinario
- El análisis genómico vincula cepas estreptocócicas emergentes con infecciones específicas
- La OMS respalda las pruebas rápidas en el punto de atención para mejorar la detección de tuberculosis
- Método basado en el aliento distingue infecciones bacterianas de forma rápida
- OMS recomienda pruebas POC, hisopos de lengua y agrupamiento de esputo para diagnóstico de TB
- Nuevo método de imágenes podría ayudar a predecir infecciones intestinales peligrosas
- La secuenciación rápida podría transformar la atención de la tuberculosis
- Virus intestinales ocultos vinculados al riesgo de cáncer colorrectal
- Panel de tres pruebas para detección de infecciones por duelas del hígado
- Prueba rápida promete respuestas inmediatas a infecciones resistentes a medicamentos
- Tecnología con CRISPR neutraliza bacterias resistentes a antibióticos
- Nuevo estudio identifica características del microbioma intestinal asociadas con enfermedad de Alzheimer
- Plataforma de IA permite detección rápida de patógenos de C. auris resistentes a fármacos
- Nueva prueba mide eficacia de antibióticos para eliminar bacterias
- Nuevas normas para antimicrobianos atienden tuberculosis para optimizar diagnóstico
Canales
Química Clínica
ver canal
Un estudio revela que la medición de ApoB es más eficaz que LDL para guiar la terapia lipídica
Los análisis de sangre rutinarios que miden las lipoproteínas de baja densidad (LDL), comúnmente conocidas como colesterol "malo", se utilizan ampliamente para orientar la terapia hipolipemiante, pero... Más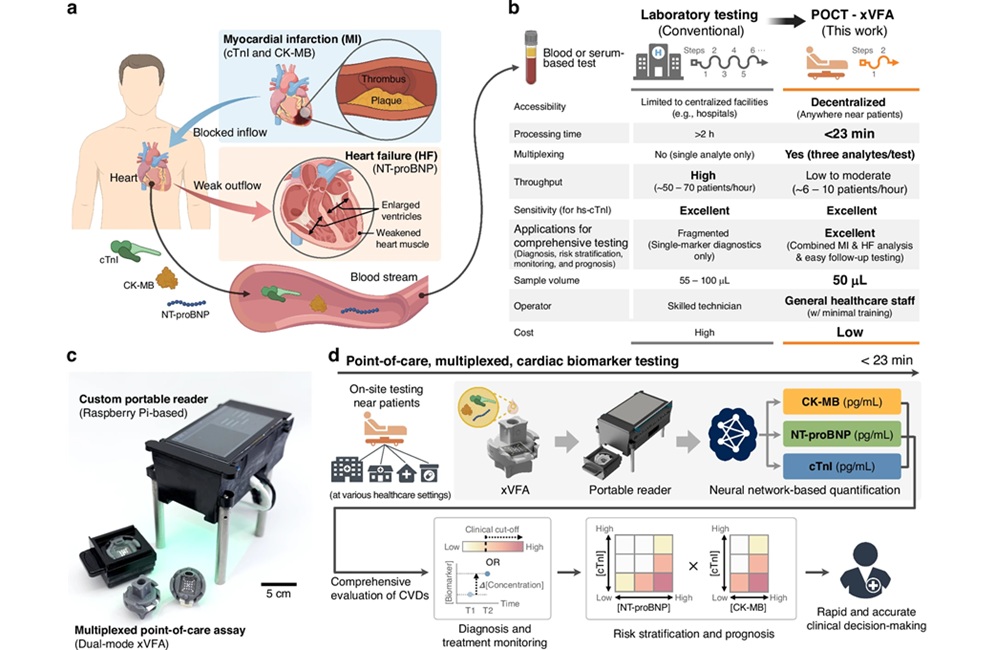
Prueba en el punto de atención basada en IA cuantifica múltiples biomarcadores cardíacos
Las enfermedades cardiovasculares son una de las principales causas de muerte, responsables de casi 20 millones de fallecimientos anuales. La detección temprana del infarto de miocardio y la insuficiencia... Más
Prueba de metabolitos en sangre detecta deterioro cognitivo temprano
La identificación temprana de personas con riesgo de demencia sigue siendo difícil, ya que los síntomas suelen aparecer solo después de una neurodegeneración significativa.... MásAnalizadores automatizados de nueva generación aumentan el rendimiento en química clínica y pruebas de electrolitos
Los laboratorios clínicos siguen enfrentándose a la escasez de personal, el espacio limitado y el creciente volumen de pruebas, lo que ejerce presión sobre los flujos de trabajo de... MásDiagnóstico Molecular
ver canal
Marcadores genéticos predicen respuesta y efectos secundarios de fármacos GLP-1 en la pérdida de peso
Los agonistas del receptor del péptido similar al glucagón tipo 1 (GLP-1), como la semaglutida y la tirzepatida, se utilizan ampliamente para el control del peso, pero la respuesta individual... Más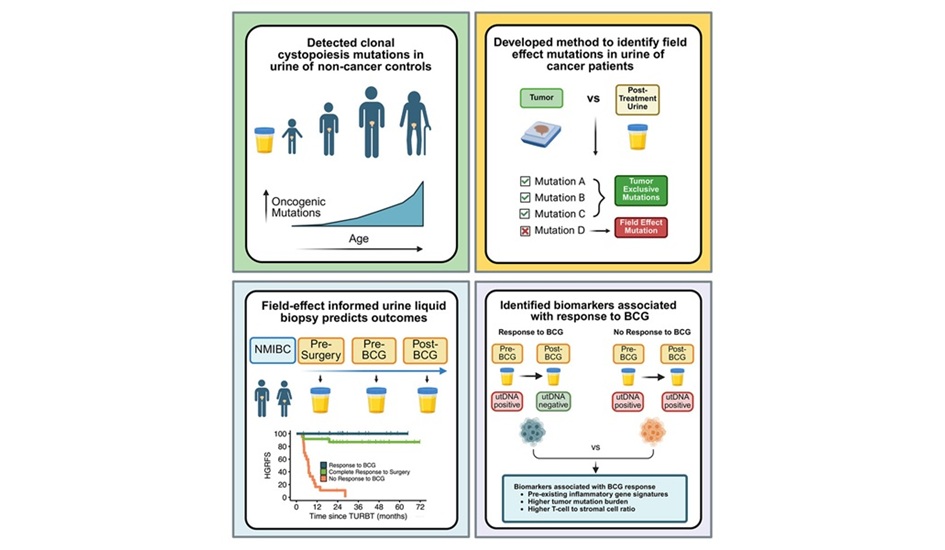
Prueba de orina no invasiva predice recurrencia tras tratamiento con BCG en cáncer de vejiga
El cáncer de vejiga es uno de los tipos de cáncer más comunes en Estados Unidos y suele recidivar incluso cuando se diagnostica en la etapa no músculo-invasiva (NMIBC).... MásHematología
ver canal
Parámetros rutinarios de análisis de sangre vinculan la anemia con el riesgo de cáncer y la mortalidad
La anemia detectada en la atención médica rutinaria puede indicar una patología subyacente y es frecuente en adultos. Dado que se define por niveles de hemoglobina por debajo del rango... Más
Nuevo ensayo de función plaquetaria permite monitorizar la terapia antiplaquetaria
Para muchos laboratorios clínicos, el seguimiento de la respuesta a la terapia antiplaquetaria sigue siendo un reto. Los ensayos basados en la agregación plaquetaria y los sistemas de cartuchos... MásInmunología
ver canalMétodo de cribado combinado permite identificar casos de lepra en etapas tempranas
La lepra sigue siendo un problema importante de salud pública, con más de 200.000 casos nuevos notificados anualmente en todo el mundo, y la enfermedad temprana a menudo escapa a la detección... Más
Prueba de anticuerpos en sangre identifica tuberculosis activa y distingue la infección latente
La tuberculosis activa (TB) sigue siendo una de las principales causas de muerte y enfermedad en todo el mundo; sin embargo, distinguir la enfermedad contagiosa de la infección latente continúa... MásPatología
ver canalLa IA ayuda a los clínicos con informes complejos de patología oncológica
Los equipos de oncología dependen cada vez más de informes de patología que integran histopatología, inmunohistoquímica y pruebas de biomarcadores en rápida e... Más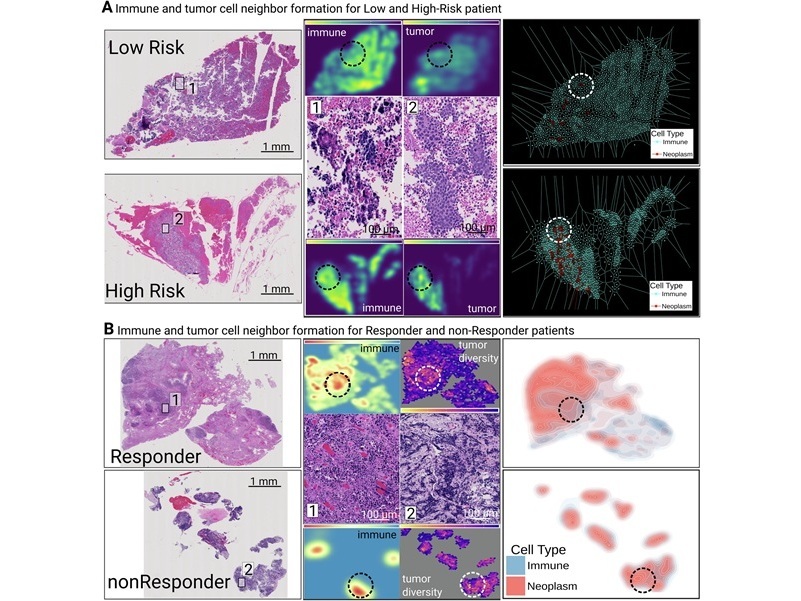
Herramienta de IA predice respuesta a la quimioterapia en cáncer de pulmón de células pequeñas
El cáncer de pulmón de células pequeñas suele presentarse en una etapa avanzada y progresa rápidamente, lo que deja poco tiempo para personalizar la terapia de primera línea. Actualmente, los médicos carecen... Más_image.png)
Biomarcador tumoral específico predice respuesta a inmunoterapia neoadyuvante en cáncer gástrico
El cáncer gástrico es la quinta neoplasia maligna más común y la cuarta causa principal de mortalidad por cáncer en todo el mundo, y China soporta casi la mitad de la carga global.... Más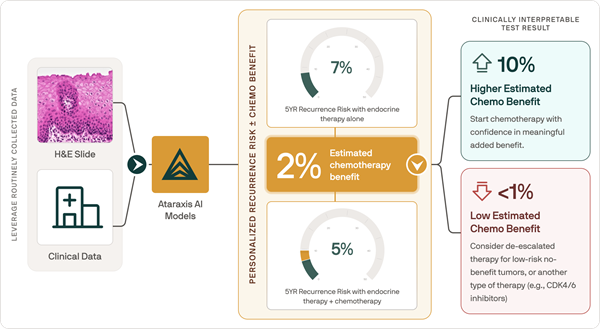
Nueva prueba de IA predice resultados de quimioterapia específicos para cada paciente con cáncer de mama
La selección de la quimioterapia adyuvante para el cáncer de mama en estadio temprano suele basarse en el riesgo de recurrencia y los promedios poblacionales, en lugar del beneficio individualizado... MásTecnología
ver canal
Prueba de esputo no invasiva detecta el cáncer de pulmón en etapa temprana
La detección precoz sigue siendo fundamental para mejorar los resultados en el cáncer de pulmón; sin embargo, los médicos se encuentran cada vez con mayor frecuencia con nódulos pulmonares indeterminados,... Más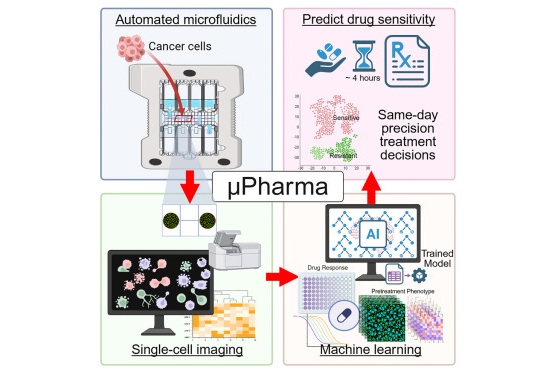
Nueva herramienta de IA permite seleccionar rápidamente el tratamiento en leucemia pediátrica
Los niños con leucemia linfoblástica aguda de células T se enfrentan a una enfermedad agresiva que sigue siendo difícil de tratar. Si bien las tasas de remisión han mejorado,... MásIndustria
ver canal
Takara Bio USA y Hamilton se asocian para automatizar la preparación de bibliotecas NGS
Takara Bio USA, Inc. (San José, California, EE. UU.), una filial de propiedad total de Takara Bio Inc., y Hamilton Company (Reno, Nevada, EE. UU.) anunciaron un acuerdo de desarrollo y comercia... Más






.jpg)