Análisis rápido de un solo paso para la detección en el campo de la malaria asintomática
Por el equipo editorial de LabMedica en español
Actualizado el 30 Sep 2020
Un nuevo sistema de ensayo ultrasensible, basado en CRISPR, pudo detectar los cuatro tipos principales de parásitos causantes de la malaria y se simplificó para uso en lugares que carecen de equipo de laboratorio avanzado y de técnicos altamente capacitados necesarios para las pruebas como RT-qPCR, que se utilizan extensivamente para monitorear la pandemia de COVID-19.Actualizado el 30 Sep 2020
Los portadores asintomáticos de paludismo causado por parásitos de la especie Plasmodium (P. falciparum, P. vivax, P. ovale y P. malariae) dificultan el control y la erradicación del paludismo. Lograr la erradicación de la malaria requiere diagnósticos ultrasensibles para infecciones de baja densidad de parásitos (menos de 100 parásitos por microlitro de sangre) que se puedan utilizar en entornos con recursos limitados (SPI). Los métodos moleculares, como la PCR, tienen una alta sensibilidad y especificidad, pero siguen siendo tecnologías de alta complejidad poco prácticas para los entornos con recursos limitados.
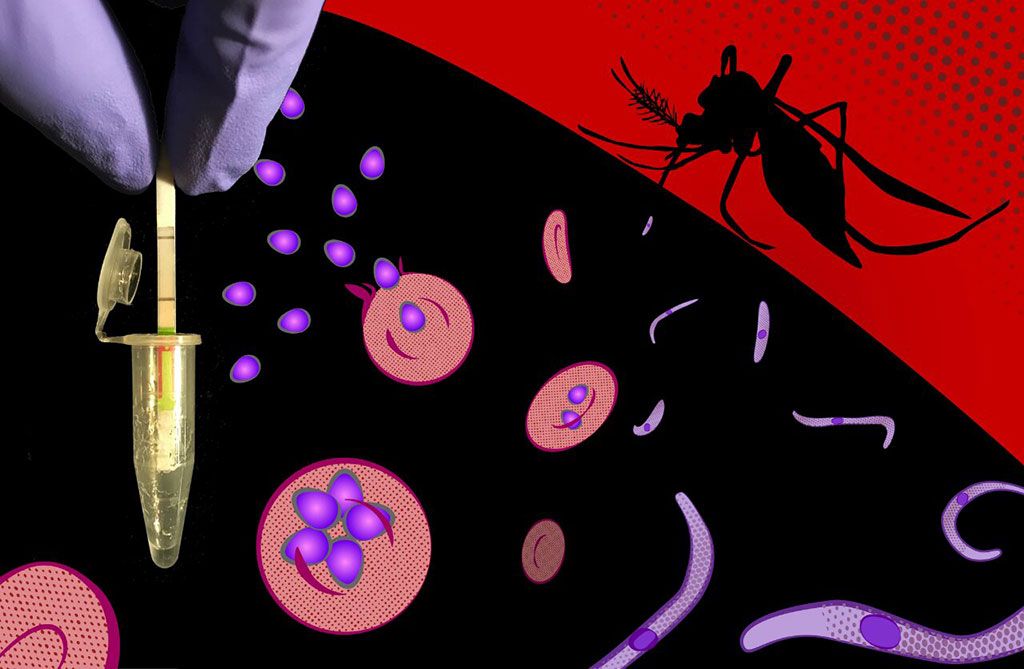
Imagen: Un ensayo de diagnóstico ultrasensible aplicable en el campo, detecta específicamente secuencias de ADN y ARN de todas las especies de Plasmodium en malaria sintomática y asintomática, y entrega sus resultados rápidamente en dispositivos reporteros simples (Fotografía cortesía de Peter Nguyen, Universidad de Harvard)
Investigadores de la Universidad de Harvard (Cambridge, MA, EUA) y sus colaboradores en el Instituto Tecnológico de Massachusetts (Cambridge, MA, EUA) y el Instituto Wyss de Ingeniería de Inspiración Biológica (Cambridge, MA, EUA), informaron sobre el desarrollo de una herramienta de diagnóstico basada en CRISPR para la detección ultrasensible y la diferenciación de los cuatro parásitos Plasmodium, utilizando la plataforma de detección de ácido nucleico SHERLOCK (desbloqueo de reportero enzimático específico de alta sensibilidad).
Los investigadores modificaron el protocolo SHERLOCK para incorporar la enzima CRISPR-Cas12a, que programaron para que fuera activada por un ARN guía que se uniera a una secuencia diana de ácido nucleico diana específica, en este caso una secuencia de una de las cuatro especies de Plasmodium. El Cas12a activado luego escindió de forma no específica cualquier hebra de ADN monocatenario en su vecindad con una tasa de rotación extremadamente alta de aproximadamente 1250 reacciones de escisión colaterales por segundo.
La plataforma de análisis completa se amplió para incluir un protocolo SHERLOCK de extracción rápida de parásitos de 10 minutos, seguido del protocolo de diagnóstico SHERLOCK durante 60 minutos, lo que permitió la detección específica de especies de Plasmodium mediante lecturas de tira de flujo lateral o fluorescente. El ensayo fue compatible con diferentes tipos de muestras, como sangre total, plasma, suero y sangre seca y todos los componentes necesarios para la amplificación, la activación de Cas12a y la generación de señales se liofilizaron en un solo tubo de ensayo que funcionó como una “reacción de un solo recipiente” después de la reconstitución de los reactivos cuando se mezclaron con una muestra del paciente.
El desempeño del diagnóstico SHERLOCK simplificado y listo para el campo se evaluó utilizando muestras simuladas de sangre total, suero y sangre seca (DBS), así como muestras clínicas de pacientes con infecciones por P. falciparum y P. vivax. Los resultados revelaron que el ensayo era capaz de detectar menos de dos parásitos por microlitro de sangre, un límite de detección sugerido por la Organización Mundial de la Salud (OMS). Los ensayos de P. falciparum y P. vivax mostraron una sensibilidad y especificidad del 100% en muestras clínicas (cinco muestras de P. falciparum y 10 de P. vivax).
“Este ensayo de diagnóstico de paludismo SHERLOCK listo para el campo supera los requisitos de sensibilidad y especificidad establecidos por la OMS para una prueba deseada que se puede usar para detectar una baja densidad de parásitos en portadores asintomáticos de todas las principales especies de Plasmodium”, dijo el autor principal, el Dr. James Collins, profesor de ingeniería médica y ciencia en el Instituto Tecnológico de Massachusetts. “Su diseño altamente optimizado podría proporcionar una solución viable al actual cuello de botella de diagnósticos en el camino para eliminar la malaria y, en general, permitir la vigilancia de la malaria en entornos de bajos recursos”.
El ensayo rápido SHERLOCK para los parásitos de la malaria se describió en la edición en línea del 21 de septiembre de 2020 de la revista Proceedings of the National Academy of Sciences of the United States of America.
Enlace relacionado:
Universidad de Harvard
Instituto Tecnológico de Massachusetts
Instituto Wyss de Ingeniería de Inspiración Biológica