Los microbios intestinales son diferentes entre dos enfermedades comunes
Por el equipo editorial de LabMedica en español
Actualizado el 08 Jan 2019
La enfermedad intestinal inflamatoria (EII) y el síndrome del intestino irritable (SII) son dos de las enfermedades más comunes del tracto gastrointestinal. A diferencia de la EII, el SII no causa inflamación, úlceras u otros daños en el intestino.Actualizado el 08 Jan 2019
Por el contrario, el SII es un problema mucho menos serio llamado un trastorno funcional. Esto significa que el sistema digestivo parece normal pero no funciona como debería. Los síntomas del SII pueden incluir calambres, hinchazón, gases, diarrea, estreñimiento y mucosidad en las heces. El SII también ha sido llamado colon espástico o intestino espástico.
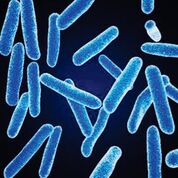
Imagen: Una micrografía electrónica de barrido a color (SEM) de Faecalibacterium prausnitzii, una de las bacterias anaeróbicas más abundantes en la microbiota intestinal humana; su abundancia relativa es un biomarcador de la salud intestinal en los adultos (Fotografía cortesía de BioFoundations).
Un equipo internacional de científicos dirigido por la Universidad de Groningen (Groningen, Países Bajos) realizó una secuenciación metagenómica en muestras de heces de 355 individuos con EII (enfermedad de Crohn o colitis ulcerosa), 412 individuos con SII y 1.025 personas no afectadas, controles sanos, en busca de especies microbianas y cepas asociadas con una o ambas afecciones inflamatorias del intestino.
El equipo realizó una secuenciación metagenómica de tipo escopeta utilizando instrumentos Illumina (Illumina, San Diego, CA, EUA) en el ADN microbiano en muestras de heces recolectadas en el hogar de 1.792 casos bien fenotipificados y controles de tres cohortes de los Países Bajos. Los datos de la secuencia del equipo llevaron a 219 taxones relacionados con la enfermedad de Crohn, 102 taxones asociados con la colitis ulcerosa y 66 taxones con vínculos aparentes con el SII. Hubo cierta superposición entre las condiciones: dentro de la EII, por ejemplo, al menos 87 de los microbios implicados en la colitis ulcerosa también aparecieron en individuos con enfermedad de Crohn.
El científico observó que la diversidad de cepas dentro de especies bacterianas beneficiosas, como Faecalibacterium prausnitzii, tendía a disminuir en los intestinos de los individuos con EII o SII en relación con los controles no afectados. También observaron cambios en la diversidad de cepas para 21 especies bacterianas en individuos con enfermedad de Crohn, en comparación con los cambios en la diversidad de cepas en 15 especies en aquellos pacientes con colitis ulcerosa y en los pacientes en el grupo SII. El equipo también calculó las tasas de crecimiento para un subconjunto de las especies microbianas intestinales, identificando pequeños grupos de especies que parecían haber alterado la abundancia en cada una de las condiciones. Además, investigaron las diferencias en la composición bacteriana, el contenido de genes y las funciones de los genes en los casos de EII y SII.
Los autores concluyeron que a pesar de la superposición sustancial entre el microbioma intestinal de los pacientes con EII y SII en comparación con los individuos de control, fueron capaces de utilizar las diferencias en la composición de la microbiota intestinal para poder diferenciar a los pacientes con EII de aquellos con SII. Al combinar los perfiles a nivel de especie y los perfiles de nivel de cepas con las tasas de crecimiento bacteriano, las funciones metabólicas, la resistencia a los antibióticos y el análisis del factor de virulencia, identificaron especies bacterianas clave que pueden estar involucradas en dos enfermedades gastrointestinales comunes. El estudio fue publicado el 19 de diciembre de 2018 en la revista Science Translational Medicine.
Enlace relacionado:
Universidad de Groningen
Illumina