Método de PCR identifica la inestabilidad de microsatélites en muestras tumorales
Por el equipo editorial de LabMedica en español
Actualizado el 14 Apr 2021
La detección sensible de la inestabilidad de microsatélites (MSI) en biopsias de tejido o líquidas usando secuenciación de siguiente generación (SSG) tiene cada vez más aplicaciones de pronóstico y predicción en el cáncer. Sin embargo, las complejidades de la SSG la hacen engorrosa en comparación con la detección de MSI mediante la PCR multiplex establecida. Actualizado el 14 Apr 2021
Los tumores con MSI acumulan grandes cantidades de inserciones o deleciones (indeles) de microsatélites somáticos (MS) debido a una pérdida de la capacidad normal de reparación de errores de apareamiento (MMR). Los niveles altos de MSI son predictivos para el resultado de la terapia del cáncer colorectal (CCR) en quimioterapia e inmunoterapia y han sido asociados con distintas características y resultados favorables incluyendo mejor pronóstico, una supervivencia más alta a los 5 años y menos metástasis.
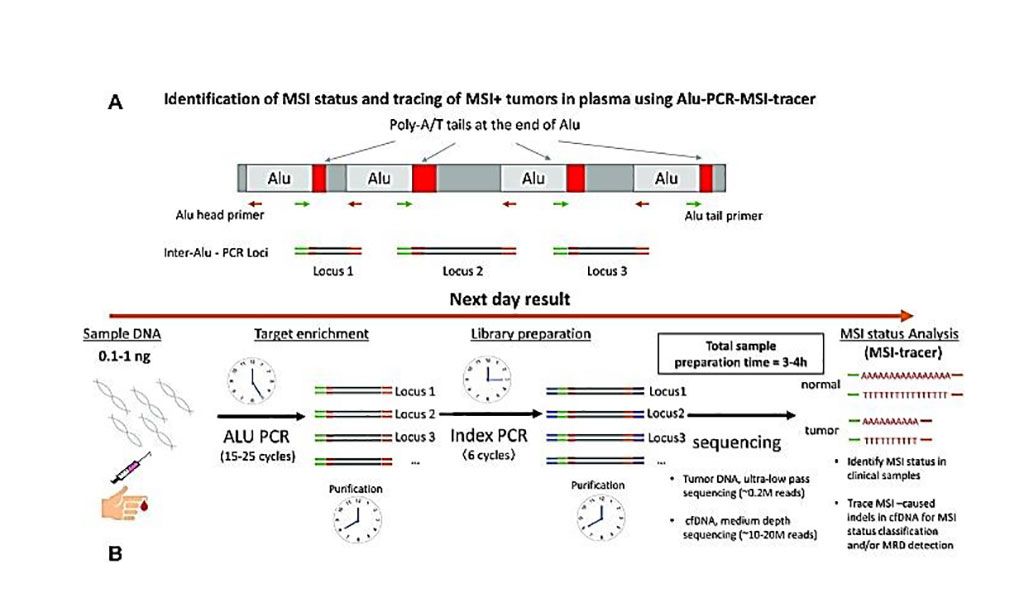
Imagen: Diagrama esquemático para la identificación de estado de MSI y rastreo de tumores MSI+ en plasma con el trazador Alu-PCR-MSI (Fotografía cortesía del Instituto de Cáncer Dana-Farber)
Los radiooncólogos del Instituto de Cáncer Dana-Farber (Boston, MA, EUA) y sus colegas, obtuvieron tejido fresco congelado de adenocarcinoma de colon estadío II/III y las emparejaron con biopsias de tejido normal de pacientes sin tratamiento previo obtenidas del Banco de Tumores del Hospital General de Massachusetts y el ADNg fue extraído usando el estuche Blood and Tissue (Qiagen, Hilden, Alemania). Extrajeron muestras de plasma de voluntarios sanos y de pacientes con adenocarcinoma de colon estadío I/II de pacientes sin tratamiento previo. El ADNlc fue aislado mediante el estuche QIAamp Circulating Nucleic de Qiagen. La concentración de ADN aislado fue cuantificada en un fluorómetro Qubit 3.0 a través de estuche de ensayo dsDNA HS (Thermo Fisher Scientific, Waltham, MA, EUA).
Para detectar los MSI el equipo desarrolló un método llamado inter-Alu-PCR seguido de SSG focalizado que combina las ventajas prácticas de la PCR multiplexada con la amplitud de la información proporcionada por la SSG. Inter-Alu-PCR emplea repeticiones de poliadenina de longitud variable presentes en cada elemento Alu y proporciona un enfoque rápido, masivamente paralelo, para capturar fracciones genómicas ricas en poli A dentro de amplicones cortos de 80 a 150 bp generados de las secuencias-Alu adyacentes. Una herramienta de análisis de software personalizada, trazador de MSI, permite la detección de MSI asociados a Alu a partir de las biopsias de tejido o rastrear las MSI a niveles bajos en el ADN circulante.
Para establecer el límite de detección del método en las muestras de tejido, los científicos probaron múltiples escenarios usando diluciones seriadas de ADN tumoral MSI-H de cáncer de colon en el ADN normal apareado. El equipo usó PCR digital en gotitas para validar el enfoque de dilución con mutaciones somáticas específicas del tumor como KRAS para un subgrupo de mutaciones. Cuando no estaba presente una muestra normal pareada, el equipo encontró que el método tenía un límite de detección de 0,15% a 0,5% para los indeles somáticos usando una muestra clínica de baja pureza tumoral. Cuando estaba disponible el tejido normal apareado, inter-Alu-PCR tenía un límite somático de detección entre 0,05% a 0,5%.
El equipo también mostró cómo inter-Alu-PCR podía ser usada potencialmente para detectar deleciones poli-adenina relacionadas con MSI en ADN libre de células (ADNlc) de la muestra de sangre de un paciente. Cuando se hizo el análisis del ADNlc de los pacientes con cáncer de colon y muestras sanas, vieron que los pacientes con MSI-H produjeron una puntuación más alta del trazador MSI en comparación con MSS o las muestras normales. En general, los autores del estudio encontraron que el inter-Alu-PCR podía clasificar las MSI usando tan solo 0,1 ng de entrada de ADN de la muestra de sangre de un paciente.
Los autores concluyeron que las ventajas prácticas e informativas de inter-Alu-PCR la hacen una herramienta poderosa y práctica para identificar el estado de MSI del tejido o rastrear los indeles asociados con la MSI en biopsias líquidas utilizando cantidades diminutas de material de partida. El estudio fue publicado el 26 de febrero de 2021 en la revista “Nucleic Acids Research”.
Enlace relacionado:
Instituto de Cáncer Dana-Farber
Thermo Fisher Scientific