Identifican subtipos definidos del síndrome mielodisplásico mediante análisis genómicos, transcriptómicos
Por el equipo editorial de LabMedica en español
Actualizado el 01 Jan 2020
El síndrome mielodisplásico es una enfermedad premaligna que afecta las células mieloides. Es un precursor de la leucemia mieloide aguda, un cáncer sanguíneo agresivo causado por la acumulación de células sanguíneas inmaduras.Actualizado el 01 Jan 2020
El mayor uso de la secuenciación en la última década ha mejorado la comprensión del campo de las mutaciones genéticas que causan el síndrome mielodisplásico (SMD) y la leucemia mieloide aguda (LMA), pero en su mayor parte, esos datos no se han integrado con los datos de expresión.
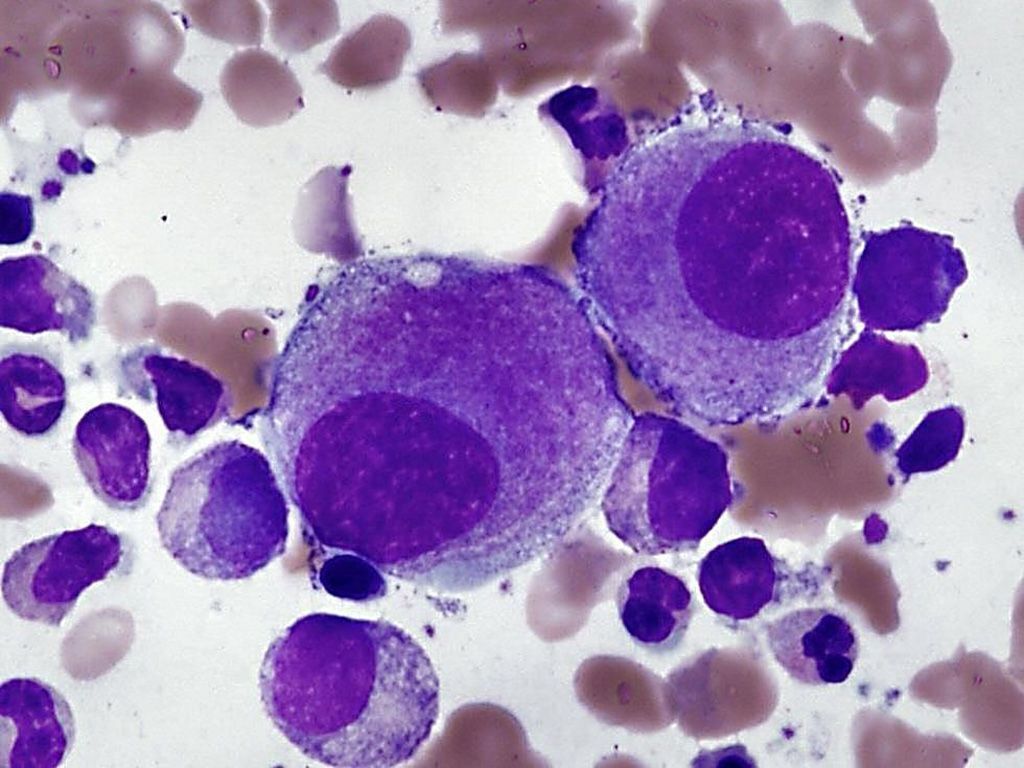
Imagen: Película delgada de la médula ósea de un paciente con síndrome mielodisplásico mostrando pequeños megacariocitos hipolobulados que son típicos del síndrome con una del (5q) aislada (Fotografía cortesía de John P. Hunt, MD)
Los científicos del Hospital de Investigación Infantil de San Judas (Memphis, TN, EUA) y sus colegas llevaron a cabo la secuenciación del genoma completo y el análisis transcriptómico a través de ARN-seq de muestras de cáncer de más de 1.300 pacientes adultos, casi 600 con LMA y alrededor de 700 con SMD y observaron cómo las variantes genéticas detectadas rastreaban los patrones de expresión génica, las características clínicas de la enfermedad de los pacientes y los resultados.
El equipo pudo confirmar el diagnóstico del 11% de los pacientes donde la LMA se debió a anormalidades genéticas recurrentes de acuerdo con las clasificaciones de las Organizaciones Mundiales de Salud. Los investigadores también identificaron más de 7.000 variantes (incluidas mutaciones somáticas y de la línea germinal, fusiones quiméricas y variantes estructurales) en 839 genes, alrededor de un tercio de los cuales eran genes promotores potenciales. Los pacientes albergaron entre una y 18 mutaciones, y promediaron cinco mutaciones. Algunas mutaciones genéticas se superponen entre las dos enfermedades, pero fueron más frecuentes en un entorno que en el otro. Por ejemplo, las mutaciones de NPM1 ocurrieron en el 27% de los casos de LMA y alrededor del 1% de los casos de SMD.
Los investigadores mostraron que, si bien los casos de LMA tenían perfiles de expresión génica que se agrupaban con patrones mutacionales específicos, los perfiles de expresión de pacientes con SMD no eran tan variables a pesar de que también tenían un panorama complejo de mutaciones. Alrededor del 27% de los casos de SMD tenían mutaciones en SF3B1, que no aparecieron en el 14% de los pacientes con mutaciones SFRS2 y el 6% de los casos con mutaciones U2AF1. Además, alrededor del 14% de los casos de SMD tenían mutaciones TP53 y el 11% tenían mutaciones RUNX1, que ocurrieron con mutaciones en los reguladores epigenéticos y se asociaron con los resultados del paciente.
Ilaria Iacobucci, PhD, autora principal del estudio, dijo: “Este estudio proporciona, por primera vez, una descripción muy detallada de cómo las diferentes mutaciones cooperan juntas, y muestra cómo se pueden utilizar para estratificar a los pacientes mediante la catalogación de diferentes mutaciones y correlacionándolos con el resultado”. El estudio se presentó en el congreso anual de la Sociedad Estadounidense de Hematología, celebrado del 7 al 10 de diciembre de 2019 en Orlando, Florida, EUA.
Enlace relacionado:
Hospital de Investigación Infantil de San Judas