Las alteraciones genómicas y los análisis de expresión diagnostican la LEA
Por el equipo editorial de LabMedica en español
Actualizado el 15 Apr 2019
Un artículo reciente identificó las alteraciones genómicas que definen los subgrupos que comprenden la leucemia eritroide aguda.Actualizado el 15 Apr 2019
La leucemia eritroide aguda (LEA) es una leucemia de alto riesgo con una base genética poco conocida y mucha controversia sobre su diagnóstico dentro del espectro de la enfermedades abarcadas por la mielodisplasia y la leucemia mieloide. Los síndromes mielodisplásicos (SMD) son un grupo de cánceres en los que las células sanguíneas inmaduras en la médula ósea no maduran y, por lo tanto, no se convierten en células sanguíneas sanas. En contraste, la leucemia es un cáncer de la línea mieloide de las células sanguíneas, que se caracteriza por el rápido crecimiento de células anormales que se acumulan en la médula ósea y en la sangre y que interfieren con las células sanguíneas normales.
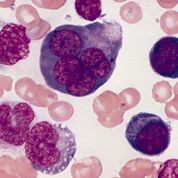
Imagen: Frotis de médula ósea en un caso de leucemia eritroide aguda que muestra un eritroblasto multinucleado con cromatina nuclear megaloblastoide (Fotografía cortesía de Wikimedia Commons).
Para desentrañar la controversia sobre el diagnóstico de la LEA, los investigadores del Hospital de Investigación para Niños St. Jude (Memphis, TN, EUA) compararon las características genómicas de 159 casos de LEA en niños y adultos con trastornos mieloides no LEA. Sus resultados definieron cinco subgrupos relacionados con la edad con distintos perfiles transcripcionales: adulto, proteína tumoral p53 (TP53) mutada; Nucleofosmina (NPM1) mutada; Histona-lisina N-metiltransferasa 2A (KMT2A) mutada/reorganizada; adulto, DEAD-box helicasa 41 (DDX41) mutada; y pediátrica, Nucleoporina 98 (NUP98) reorganizada.
Los investigadores encontraron que las características genómicas influyeron en el resultado de la enfermedad, con la sobreexpresión de mutaciones de NPM1 y HOXB9 (proteína homeobox Hox-B9) asociadas con un pronóstico favorable y las alteraciones en TP53, FLT3 (tirosina quinasa 3 relacionada con FMS) o RB1 (RB1) asociadas con una mala supervivencia.
“Las alteraciones genómicas y los perfiles de expresión génica fueron los predictores más fuertes de resultados en pacientes con LEA, lo que sugiere que se deberían incorporar en los criterios de diagnóstico y pronóstico”, dijo el autor principal, el Dr. Charles Mullighan, profesor de patología en el Hospital de Investigación Infantil St. Jude. “Estos resultados marcan una nueva era en la comprensión y el tratamiento de la LEA, una leucemia agresiva que ha estado plagada de controversias diagnósticas y resultados deficientes”.
El artículo se publicó el 29 de marzo de 2019 en la edición digital de la revista Nature Genetics.
Enlace relacionado:
Hospital de Investigación para Niños St. Jude