Evalúan ensayos moleculares para virus respiratorios
Por el equipo editorial de LabMedica en español
Actualizado el 18 May 2017
Las infecciones respiratorias agudas (IRA) son una de las principales causas de mortalidad en todo el mundo, y aproximadamente la mitad son causadas por virus respiratorios (VR). Existen varios tipos de pruebas para la detección de estos virus.Actualizado el 18 May 2017
La prueba de amplificación de ácidos nucleicos (NAAT) ha sido aceptada ampliamente en los últimos años y tiene ventajas en comparación con los métodos clásicos de cultivo viral y las pruebas directas de anticuerpos mediante fluorescencia. Las NAAT tienen una sensibilidad superior, que identifica casos de VR no detectados por métodos clásicos y los resultados de las pruebas para los VR están disponibles más rápidamente que los de los cultivos virales.
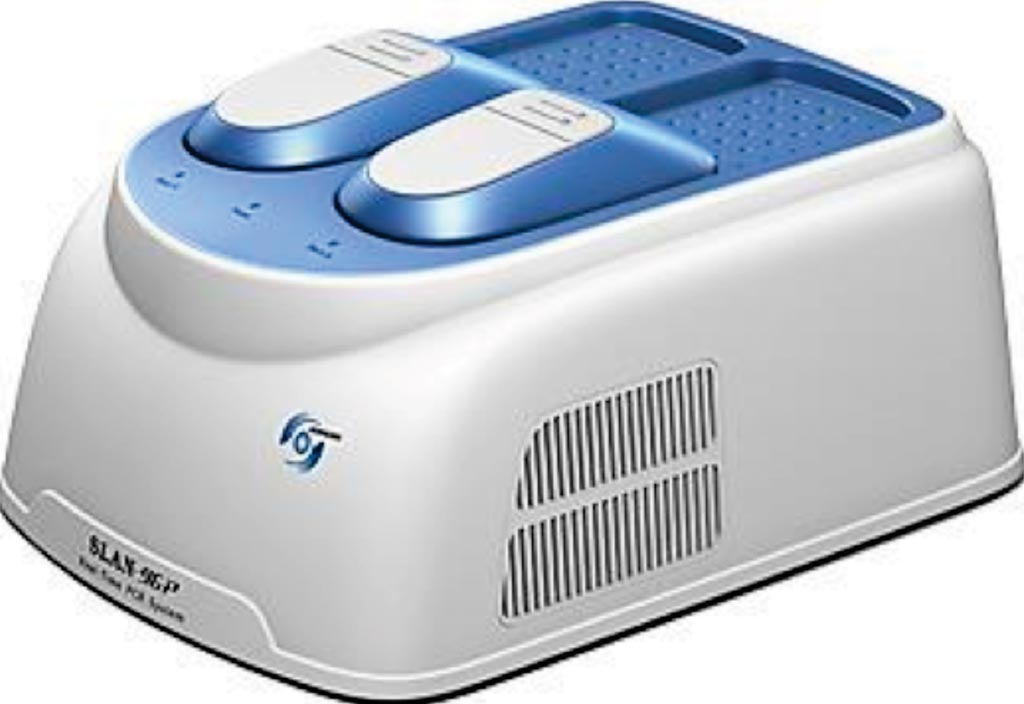
Imagen: El sistema de detección mediante reacción en cadena de la polimerasa (PCR) en tiempo real, SLAN (Fotografía cortesía de Shanghai Hongshi Medical Technology).
Los científicos del laboratorio de la Facultad de Medicina de la Universidad Nacional de Kangwon (Chuncheon, Corea del Sur), recolectaron, entre diciembre de 2015 y marzo de 2016, 201 muestras respiratorias (161 muestras de hisopado nasofaríngeo y 40 muestras de esputo) de soldados varones jóvenes (intervalo de edad, 18-27 años, mediana 21 años) con enfermedad respiratoria aguda. Las muestras de hisopo nasofaríngeo se obtuvieron utilizando hisopos de algodón y se recibieron muestras de esputo en recipientes estériles de plástico.
Se utilizó un sistema de extracción de ácido nucleico para cada ensayo para los VR. El equipo analizó las muestras con tres ensayos comerciales para VR: Seegene Anyplex II RV16 (AP, Seegene, Seúl, República de Corea, www.seegene.com), LG AdvanSure RV (AD, LG Chem, Seúl, Corea del Sur) y Biosewoom Real-Q RV (RQ, BioSewoom, Seúl, Corea del Sur). Las pruebas adicionales para los resultados discrepantes se llevaron a cabo mediante repetición del ensayo para VR o PCR monoplex, acoplada a secuenciación directa. El ensayo de AD realiza, tanto la reacción de transcripción inversa (RT), con el ARN extraído de la muestra como la reacción de PCR multiplex simultáneamente y se realiza en un sistema de detección de PCR en tiempo real SLAN (Shanghai Hongshi Medical Technology Co., Shanghai, China, www.hongshitech.com).
Los científicos encontraron que, de las 201 muestras, AP, AD y RQ detectaron 105 (52,2%), 99 (49,3%) y 95 (47,3%) casos positivos, respectivamente. Se identificaron muestras de co-infección viral en el ensayo de AP para 24 (11,9%) pacientes, en el ensayo de AD para 17 (8,5%) pacientes y en el ensayo RQ para 11 (5,5%) pacientes. El desempeño de los tres ensayos fue muy similar, con un 94% -100% de concordancia para todas las comparaciones de cada tipo de virus. Las pruebas adicionales de las muestras mostraron resultados discrepantes que demostraban que el ensayo de AD tenía la mayor tasa de concordancia con los resultados originales.
Los autores concluyeron que la concordancia de los tres ensayos fue muy buena, con un 94% -100% de correlación para todas las comparaciones. Sugieren que todos los ensayos de multiplexación serían adecuados para la detección de virus respiratorios en el contexto clínico. El estudio fue publicado el 11 de abril de 2017, en la revista Journal of Clinical Laboratory Analysis.