Panel de bacterias intestinales es útil para diagnosticar cáncer colorrectal
Por el equipo editorial de LabMedica en español
Actualizado el 11 May 2017
Actualizado el 11 May 2017
El análisis y la estandarización de datos de varios estudios publicados han permitido identificar un panel de microflora intestinal que es más frecuente en las heces de pacientes con cáncer colorrectal que en las heces de individuos normales.
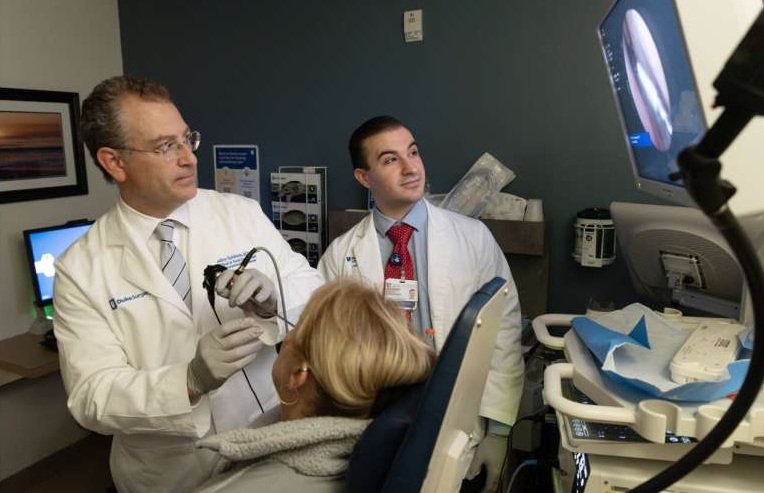
Imagen: Los investigadores analizaron nuevamente los datos crudos de las secuencias de ADN bacteriano de varios estudios y confirmaron los tipos de bacterias, previamente reportados, asociadas con el cáncer colorrectal e identificaron otras bacterias no asociadas previamente con la enfermedad (Fotografía cortesía de la Facultad de Medicina Baylor).
El cáncer colorrectal (CCR) es la segunda causa de mortalidad asociada al cáncer en los Estados Unidos, y los investigadores de la Facultad de Medicina Baylor (Houston, TX, EUA) y sus colegas de la empresa de biotecnología, Second Genome Inc. (Sur de San Francisco, CA, EUA), plantearon la teoría de que el microbioma fecal podría proporcionar biomarcadores no invasivos para el CCR.
Para confirmar esta teoría, los investigadores analizaron y nuevamente los datos crudos de las secuencias de ADN bacteriano de varios estudios publicados que abarcaron un total de 509 muestras (79 adenomas colorrectales, 195 CCR y 235 controles). Se repitieron los análisis de abundancia diferencial, regresión de los efectos aleatorios de metanálisis y de aprendizaje automático, para determinar la consistencia y las capacidades de diagnóstico de biomarcadores microbianos potenciales.
Los resultados revelaron que los taxones definitivos, incluyendo Parvimonas micra ATCC 33270, Streptococcus anginosus y miembros aún no cultivados de Proteobacteria, se incrementaban de manera frecuente y significativa en las heces de los pacientes con CCR, en comparación con los controles en todos los estudios y tenían alta capacidad discriminatoria en la clasificación diagnóstica .
“Este fue un primer paso prometedor para desarrollar una prueba no invasiva que podría utilizarse para la detección de cáncer colorrectal, complementando la colonoscopia o las pruebas de sangre oculta en heces”, dijo la autora principal, la Dra. Emily Hollister, profesora asistente de patología en la Facultad de Medicina Baylor.
“Este fue un estudio multinacional increíblemente grande y complejo”, dijo el autor contribuyente, Todd DeSantis, cofundador y vicepresidente de informática de Second Genome Inc. “Vimos muchas diferencias entre los centros médicos en la manera en que recolectaron y almacenaron cada muestra de heces y en los métodos utilizados para procesar el ADN bacteriano en las heces. Estas diferencias pueden ser problemáticas para la identificación de las cepas bacterianas que proliferan en pacientes con cáncer, pero nuestro equipo KnowlegeBase, en Second Genoma, dirigido por el autor contribuyente, Thomas Weinmaier, encontró formas de mejorar nuestra plataforma de software para resolver estas diferencias mientras avanzábamos en el estudio. Los resultados que surgieron de este desafiante conjunto de datos, ayudaron a validar nuestra plataforma, y en el proceso hemos sido capaces de ofrecer una visión de alta calidad para mejorar nuestra colaboración con el Dr. Hollister”.
El estudio fue publicado en la edición digital del 24 de marzo de 2017 de la revista Gut.